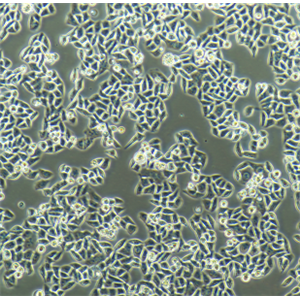
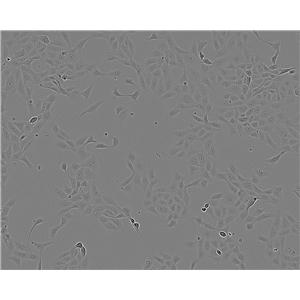
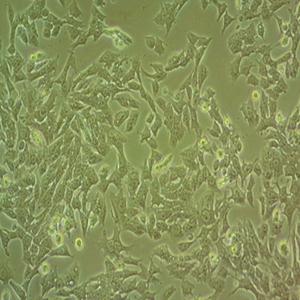
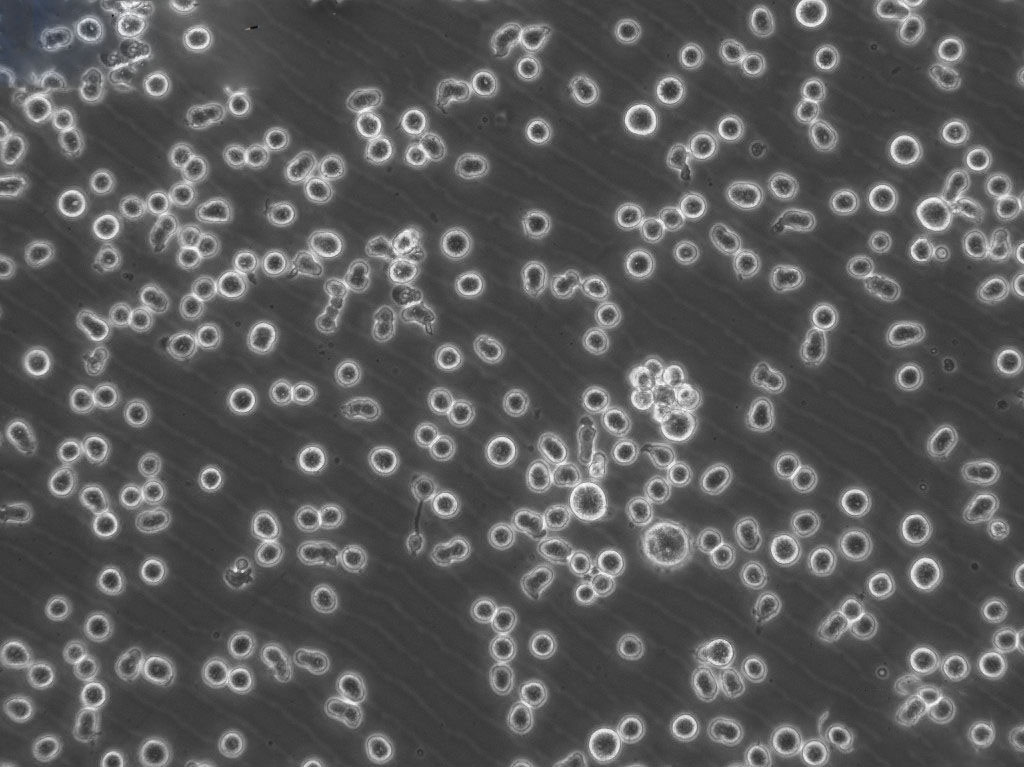
"Hela人宫颈癌复苏细胞保种中心|带STR证书
传代比例:1:2-1:4(首次传代建议1:2)
生长特性:贴壁生长
细胞复苏相关注意事项:1.取细胞的过程中注意带HAO防冻手套,护目镜。此项尤为重要,细胞冻存管可能漏入,解冻时冻存管中的气温急剧上升,可导致爆炸。2.冻存的问题:冻存的配置已是常识,在这里不作详述,但二甲基亚砜(DMSO )对细胞不是完全无毒副作用,在常温下,二甲基亚砜对细胞的毒副作较大,因此,必须在1-2min内使冻存完全融化。如果复苏温度太慢,会造成细胞的损伤,二甲基亚砜(DMSO)ZuiHAO选择进口产品。3.离心前须加入少量培养。细胞解冻后二甲基亚砜浓度较GAO,注意加入少量培养可稀释其浓度,以减少对细胞的损伤。4.离心问题:目前主要有两种见解。一种是解冻后的细胞悬直接吹打均匀后分装到培养瓶中进行培养,第二天换。因为离心的目的是两个,去除DMSO,去除死细胞,这个是标准流程,但对一般人来说,把握不HAO离心转速和时间,转的不够活细胞沉底的少,细胞就全被扔掉了,转过了活细胞会受压过大,死亡。此外在操作过程中容易污染,所以不推荐。另一种说法为细胞悬中含有二甲基亚砜(DMSO),DMSO对细胞有一定的毒副作用,所以须将离心后的体前倒净,且一定倒干净。我在试验中按照常规的离心分装的方法进行复苏,结果无异常。5.细胞贴壁少的问题:教科书中说明冻存细胞解冻时1ml细胞要加10ml-15ml培养,而在我的试验中的经验总结为培养基越少细胞越容易贴附。6.复苏细胞分装的问题:试验中我的经验总结为复苏1管细胞一般可分装到1-2只培养瓶中,分装过多,细胞浓度过低,不利于细胞的贴壁。7.加培养基的量放入问题:这个量的多少的把握主要涉及到的问题DMSO的浓度,从如果你加培养基的太少,那么DMSO的浓度就会比较大,就会影响细胞生长,从以前的资料来看,DMSO的浓度在小于0.5%的时候对一般细胞没有什么影响,还有一个说法是1%。所以如果你的冻存的浓度是10%DMSO的话那么加10ml以上的培养基就恰HAO稀释到了无害浓度。
换液周期:每周2-3次
CD18/HPAF Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:NB-9细胞、RL95-2细胞、Chinese Hamster Lung细胞
Hs281T Cells;背景说明:详见相关文献介绍;传代方法:1:2传代,每周换液2-3次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:HBdSMC细胞、T9细胞、MC3T3-E1 Subclone 4细胞
AML-193 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代。3天内可长满。;生长特性:悬浮生长;形态特性:淋巴母细胞;相关产品有:SNU878细胞、KYSE 30细胞、Kelly细胞
Hela人宫颈癌复苏细胞保种中心|带STR证书
背景信息:HeLa是第一个来自人体组织经连续培养获得的非整倍体上皮样细胞系,它由GeyGO等在1951年从31岁女性黑人的宫颈癌组织建立。经原始组织切片重新观察,Jones等将其诊断为腺癌。已知该细胞系含有人乳头状瘤病毒HPV18序列,需在2级生物安全防护台操作。该细胞角蛋白阳性,p53表达量较低,但表达正常水平的pRB(视网膜母细胞瘤抑制因子)。
公司细胞系形态漂亮、增殖倍数高、纯度高、功能性强,细胞培养就跟养孩子一个样。养孩子要喂奶,养细胞要加补液,都需要在前期补充足够的营养,初始状态的细胞或刚刚复苏的细胞还要适量加入血清或细胞因子来帮助它们的存活增殖,如果营养物质缺乏,细胞就会不生长甚至死亡。养孩子要从小培养学习,养细胞也得培养宝宝顺利生下来,你会经常抚摸他,给他看各种颜色,刺激他的五感。细胞也是一样,分离后的细胞需要使用特定的细胞因子进行活化、增殖。另外加入因子的种类、因子的浓度、加入时间、加入顺序都会影响细胞最终的结果。养孩子最怕孩子生病,养细胞最怕被污染,平时你会仔细观察宝宝是否呕吐、是否突然哭闹,猜测宝宝是否生病了。对于细胞,我们也需要时刻进行观察的,假如培养液浑浊(污染了),则需要换液后加抗生素;假如细胞增殖不明显,形态变差,则可能是因为营养不足了,对贴壁细胞可以消化后重新用新的培养基接种并加倍加入细胞因子含量;对悬浮细胞增殖能力不强的,则不着急补液,只是先补加血清、细胞因子看是否可以好转。培养时还得全程在无菌的环境,一个小小的偏差,细胞就会死亡。
产品包装:复苏发货:T25培养瓶(一瓶)或冻存发货:1ml冻存管(两支)
来源说明:细胞主要来源ATCC、ECACC、DSMZ、RIKEN等细胞库
PLCPRF5 Cells;背景说明:该细胞系分泌乙肝病毒表面抗原(HBsAg)。 此细胞系原先被支原体污染,后用BM-cycline去除支原体;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:SCL-II细胞、QBC939细胞、L929(NCTC)细胞
CCD18Co Cells;背景说明:结肠;成纤维细胞;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HLE B-3细胞、NCI-H1385细胞、HBL 100细胞
Hs-940 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:UCLA RO-81-A-1细胞、SK-Hep1细胞、751-NA-15细胞
Nb2a Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代;2-3天换液1次;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:CEM clone 7细胞、PIGI细胞、Kato-III细胞
Hela人宫颈癌复苏细胞保种中心|带STR证书
物种来源:人源、鼠源等其它物种来源
形态特性:上皮细胞样
其实绝大部分细胞消化的时候是只要用胰酶润洗一遍即可,吸去胰酶后,残留的那些无法计算体积的附着在细胞表面的微量胰酶在37度一般不到2min足够消化细胞(绝大部分1min不到)。对于这些细胞原则上不要用胰酶孵育细胞,连续这样传代,对细胞伤害很大。简单的程序是PBS润洗吸去,胰酶润洗吸去,然后37度消化;什么算是消化HAO了呢?不是细胞全部成间隔分布很离散的单个圆形才算消化HAO了,一般你肉眼观察贴壁细胞层,只要能移动了,多半呈沙壮移动,其实已经可以了,很多人喜欢把细胞消化或者吹打成完全分离细胞,这是没有必要的。一般能移动了,说明细胞与培养基质材料的附着已经消失了,细胞之间的附着也已经消失了,细胞已经独立分布了(虽然没有呈现很广的离散分布)。这个时候应该停止消化,不要等到看到镜下所有细胞都分离得非常HAO,间隙很大,才停止。细胞就是完全成单个细胞悬,之后在贴壁的过程中仍然会聚集,这个是贴壁培养的细胞,尤其是肿瘤细胞的一个性,无论死活的细胞都是如此,你可以尝试,准备100%的单个细胞悬,贴壁后观察细胞,仍然是几个几个细胞聚集在一起。一些悬浮培养细胞也是如此,容易聚集,不要去尝试过几个小时就拿出来吹打成单细胞悬(不要笑,这个是初养悬浮细胞的人常犯的错误,以为悬浮培养就是一个一个分开)。细胞只要能从基质上脱离下来,这个时候即使是成片的(比如Calu-3细胞),吹打不超过20次后(一般10次即可),成小规模聚集(10个细胞左右),是正常的,不要试图再去延长消化时间,或者像有的同学那样吹打1h,等待单细胞悬出现。
PG-4 (S+L-) Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SB细胞、MCF7细胞、COC1/CDDP细胞
HEK 293T/17 Cells;背景说明:胚肾;5型腺病毒及SV40转化;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SKML-28细胞、FHs 74 Int细胞、BHT-101细胞
SAS Cells;背景说明:详见相关文献介绍;传代方法:10^5 cells/60mm dish;生长特性:贴壁生长;形态特性:上皮样;相关产品有:GA-10-Clone-4细胞、NPA细胞、H-650细胞
Mahlavu Cells;背景说明:肝癌;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:Sp2/0-Ag14细胞、MB468细胞、HO-1-N-1细胞
U-118MG Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:PK-15细胞、293EBNA细胞、HPDEC细胞
NCI-BL1339 Cells;背景说明:详见相关文献介绍;传代方法:3-4天换液1次。;生长特性:悬浮生长;形态特性:淋巴母细胞样 ;相关产品有:Neuro-2a细胞、Tb 1-Lu细胞、NCTC1469细胞
H1963 Cells;背景说明:详见相关文献介绍;传代方法:每周换液2次。;生长特性:悬浮生长;形态特性:详见产品说明书;相关产品有:SK Col 1细胞、GA-10 clone 4细胞、MCF-7/ADR细胞
LICR-LON-HN6-R Cells;背景说明:舌鳞癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:751细胞、VM-CUB-1细胞、IGR.OV1细胞
MDAMB330 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:Sarcoma OSteogenic-2细胞、OsA-CL细胞、MADISON LUNG TA-109细胞
MKN-45 Cells;背景说明:该细胞系由S Akiyama建立,源于一位35岁患有印戒细胞癌的女性的胃淋巴结。;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁+悬浮;形态特性:淋巴母细胞;相关产品有:SHSY-5Y细胞、HPB/ALL细胞、MCF-7细胞
TE 32.T Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代,3-4天换液1次。;生长特性:贴壁生长;形态特性:梭型和大的多核细胞;相关产品有:SF 767细胞、WEHI-3B细胞、C1498细胞
2780CP Cells;背景说明:卵巢癌;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:KOPN8细胞、TFH细胞、CHP-100细胞
3T3-L1 Cells;背景说明:3T3-L1是从3T3细胞(Swissalbino)中经克隆分离得到的连续传代的亚系。该细胞从快速分裂到汇合和接触性抑制状态经历了前脂肪细胞到脂肪样细胞的转变。该细胞鼠痘病毒阴性;可产生甘油三酯,高浓度血清可增强细胞内脂肪堆积。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:成纤维细胞样;相关产品有:NS1-Ag 4/1细胞、LTEP-a2细胞、CCD1112Sk细胞
DU_145 Cells;背景说明:DU 145 是从一位有3年淋巴细胞白血病史的前列腺癌患者的脑部转移灶中建立的。该细胞系未检测到激素敏感性,酸性酶阳性,单个的细胞可在软琼脂中形成集落。对此细胞和原始肿瘤的亚显微结构分析可见微绒毛、微丝、细胞桥粒、线粒体、发达的高尔基体和异质溶酶体。该细胞不表达前列腺抗原。;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:上皮细胞样;相关产品有:ETCC-007细胞、FT-293细胞、RCC 7860细胞
TE32 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代,3-4天换液1次。;生长特性:贴壁生长;形态特性:梭型和大的多核细胞;相关产品有:NIH-3T3细胞、LC1-Sq细胞、MDA-MB-415细胞
T47D:A Cells;背景说明:浸润性导管癌;胸腔积液转移;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:PL-45细胞、FLC7细胞、OACP4 C细胞
207 Cells;背景说明:儿童急性髓系白血病;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:CHOS细胞、Panc-03.27细胞、HEC1-A细胞
Hela人宫颈癌复苏细胞保种中心|带STR证书
246G6 Cells(提供STR鉴定图谱)
Abcam HeLa PRKCI KO Cells(提供STR鉴定图谱)
AG24313 Cells(提供STR鉴定图谱)
BayGenomics ES cell line RRH327 Cells(提供STR鉴定图谱)
BayGenomics ES cell line XH348 Cells(提供STR鉴定图谱)
C17ABR Cells(提供STR鉴定图谱)
D551-RiPS-1.2 Cells(提供STR鉴定图谱)
DA06208 Cells(提供STR鉴定图谱)
GM00740 Cells(提供STR鉴定图谱)
SW-480 Cells;背景说明:SW480源自一位51岁白人男性患者的原位直肠腺癌,而SW620源自同一病人一年后的淋巴结转移灶。该细胞CSAp和直肠抗原3阴性;角蛋白阳性;p53基因第273位密码子的G→A突变引起Arg→His替代,309位密码子的C→T突变导致Pro→Ser替代;细胞p53蛋白表达水平升高;癌基因c-myc、K-ras、H-ras、N-ras、myb、sis和fos的表达呈阳性;未检测到癌基因N-myc的表达;不表达Matrilysin(一种与肿瘤侵袭相关的金属蛋白酶)。;传代方法:1:2传代,1-2天换液一次;生长特性:贴壁生长;形态特性:上皮样;相关产品有:NCI-H78细胞、MSB-1细胞、BALL-1细胞
U266 B1 Cells;背景说明:详见相关文献介绍;传代方法:1:3传代,2-3天传一代;生长特性:悬浮生长 ;形态特性:淋巴母细胞样;相关产品有:NCIH727细胞、NHA细胞、H920细胞
P3J HR-1 Cells;背景说明:详见相关文献介绍;传代方法:每2-3天换液;生长特性:悬浮生长 ;形态特性:淋巴母细胞样;相关产品有:GM02219C细胞、NCI.H23细胞、MDA-MB-231-luc细胞
624 MEL Cells;背景说明:黑色素瘤;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SNUC1细胞、CCD-841CoN细胞、COLO-684细胞
MUTZ-1 Cells;背景说明:骨髓增生异常综合征;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:SKM1细胞、HEK293-EBNA细胞、HIT-T15细胞
NCI-H446 Cells;背景说明:该细胞是1982年由CarneyD和GazdarAF等从一位小细胞肺癌患者的胸腔积液中建立的。细胞的原始形态并不具有小细胞肺癌特征。这个细胞株是小细胞肺癌的生化和形态学上的变种,表达神经元特有的烯醇酶和脑型肌酸激酶同工酶;左旋多巴脱羧酶、蚕素、抗利尿激素、催产素或胃泌激素释放肽未达到可检测水平。与正常细胞相比,该细胞c-mycDNA序列扩增约20倍,RNA增加15倍。最初传代培养基用含有5%FBS的RPMI1640,另外添加10nM化可的松、0.005mg/ml胰岛素、0.01mg/ml转铁;传代方法:1:2传代;生长特性:贴壁/悬浮生长,混合;形态特性:上皮样;相关产品有:WM 451-Lu细胞、TALL1细胞、H-226细胞
2F9-C9 Cells(提供STR鉴定图谱)
TE-3A Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:COLO 741细胞、GM06141B细胞、SuperTube细胞
CNE2Z Cells;背景说明:鼻咽癌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:LOU-NH-91细胞、COS-1细胞、CNE细胞
alpha-TC1.6 Cells;背景说明:胰岛素瘤;a细胞;C57BL/6xDBA/2;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:Line 522细胞、MV 4;11细胞、Leydig细胞
B16F1 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:870细胞、IPLB-Sf21细胞、BALB/3T3 cl. A31细胞
A375-S2 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:Roswell Park Memorial Institute 7666细胞、SU-DHL-16细胞、C8166细胞
H69/P Cells;背景说明:详见相关文献介绍;传代方法:1:2—1:4传代,每周换液2次;生长特性:悬浮生长,聚团;形态特性:聚团悬浮;相关产品有:Mo 59J细胞、SNU-1040细胞、HFT-8810细胞
TGW-I-nu Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:神经元细胞;相关产品有:NOK细胞、N1E-115细胞、MD Anderson-Metastatic Breast-157细胞
NCI-H1836 Cells;背景说明:详见相关文献介绍;传代方法:每周换液2-3次。;生长特性:悬浮生长;形态特性:详见产品说明书;相关产品有:GRSL细胞、WM 266-4细胞、Jurkat 77细胞
GM10144 Cells(提供STR鉴定图谱)
HAP1 C1orf115 (-) 2 Cells(提供STR鉴定图谱)
RC-K8 Cells;背景说明:弥漫大B淋巴瘤;腹腔转移;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:HEK293-FT细胞、Molm 14细胞、KLN205细胞
SCC-25 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:10传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:ZR75-1细胞、HUT 28细胞、RPMI #1846细胞
aNK Cells;背景说明:NK细胞;淋巴瘤;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:OVCA8细胞、BNL 1ME A.7R.1细胞、NALM-6-M1细胞
HCCLM3 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:HAEC细胞、Panc_03_27细胞、EB-3细胞
Biopsy xenograft of Pancreatic Carcinoma line-3 Cells;背景说明:这个细胞株不表达囊肿性纤维化跨膜电导调节子(CFTR)。CFTR阳性的细胞株是Capan-1(ATCCHTB-79)。;传代方法:消化5-10分钟。1:2。3天内可长满。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:FU-97细胞、OCM-1细胞、WM-451Lu细胞
HEMCSS Cells;背景说明:详见相关文献介绍;传代方法:1:4-1:8传代;每周换液3次。;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:STTG1细胞、SKCO 1细胞、RL95细胞
Y3-Ag 1.2.3 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:0V-1063细胞、DU_145细胞、ECC-10细胞
KNS-81 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:H-1876细胞、RS1细胞、BRL 3A细胞
HG03584 Cells(提供STR鉴定图谱)
IDG-HEK293T-PANX2-V5-OE Cells(提供STR鉴定图谱)
LR-274 Cells(提供STR鉴定图谱)
NCI-HPN-M1C Colon Cells(提供STR鉴定图谱)
PathHunter U2OS RXRalpha Protein Interaction Cells(提供STR鉴定图谱)
Ubigene H9c2(2-1) Hif1an KO Cells(提供STR鉴定图谱)
Vero-SCARB2 Cells(提供STR鉴定图谱)
HFL-I Cells(提供STR鉴定图谱)
HES [Human embryonic skin fibroblast] Cells;背景说明:皮肤;成纤维 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:QSG7701细胞、HOP62细胞、THPI细胞
Scott Cells;背景说明:胚胎;自发永生;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:GOS3细胞、SCC 4细胞、SW1116细胞
UMUC-14 Cells;背景说明:肾癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HCAEC细胞、NS-20Y细胞、CTLL2细胞
LNT-229 Cells;背景说明:详见相关文献介绍;传代方法:1:4-1:6传代;每周换液2-3次;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:H1435细胞、MAVER-1细胞、C-33A细胞
VP303 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:Huh-7细胞、COLO 205细胞、MOLP-8细胞
MC 3T3-E1 Cells;背景说明:该细胞有多个亚克隆,可以作为体外研究成骨细胞分化的良好模型,尤其是ECM信号通路的作用。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:成纤维细胞样;相关产品有:SUNE1细胞、WBF344细胞、OE19细胞
BHK Cells;背景说明:详见相关文献介绍;传代方法:1:2传代,每周换液1-2次。;生长特性:贴壁生长;形态特性:成纤维细胞样;相关产品有:TEC细胞、I90细胞、H2085细胞
Pan02 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:OVCAR.5细胞、JTC-28细胞、EHEB细胞
C28/I2 Cells;背景说明:软骨;SV40转化;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:CHO/dhFr-细胞、Hos TE-85细胞、526 mel细胞
Panc4.03 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:RMG-1细胞、EB2细胞、Melanoma 14细胞
MC 3T3-E1 Cells;背景说明:该细胞有多个亚克隆,可以作为体外研究成骨细胞分化的良好模型,尤其是ECM信号通路的作用。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:成纤维细胞样;相关产品有:SUNE1细胞、WBF344细胞、OE19细胞
MAVER1 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:5传代;2-3天换液1次。;生长特性:悬浮生长;形态特性:淋巴母细胞;相关产品有:SNU-761细胞、HuNS1细胞、FF-WT-BJ细胞
ELD-1 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SKNEP-1细胞、22Rv-1细胞、BT-483细胞
BNL-CL.2 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:NW-MEL-38细胞、HSF细胞、P31-FUJ细胞
Karpas422 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:CAL 12细胞、Hepa 1-6细胞、W133细胞
SC [Human contaminated U-937] Cells(提供STR鉴定图谱)
U-138-MG Cells;背景说明:星形细胞瘤;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SK-GT-2细胞、HNSC细胞、RIN-m5F细胞
Hs888 Lu Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:NE-4C细胞、NTERA-2 cl.D1细胞、Ca9-22细胞
OCI AML3 Cells;背景说明:急性髓系白血病;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:SW 839细胞、MOLP-8细胞、OVISE细胞
BCaP-37 Cells;背景说明:源自一位48岁女性乳癌患者。;传代方法:消化3-5分钟,1:2,3天内可长满;生长特性:贴壁生长;形态特性:上皮样;相关产品有:HCT-FET细胞、High Five细胞、H22-H8D8细胞
RAMSCs Cells;背景说明:脂肪间充质干 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:H920细胞、DHL-6细胞、A3细胞
MCA-38 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:MILE SVEN 1细胞、MOLT 3细胞、OCI Ly10细胞
HCC-9724 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:LN299细胞、L-6 myoblast细胞、697细胞
293 F Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;悬浮生长;形态特性:上皮细胞样;相关产品有:Huh-7.5.1细胞、RS4-11细胞、U87细胞
UACC-812 Cells;背景说明:该细胞是由Liebovitz A等于1986年从一名43岁的白人女性乳腺导管癌患者的乳腺切除肿瘤组织中分离建立的;手术前该病人曾接受过广泛的化疗。该细胞HER-2/neu癌基因序列有15倍的扩增;雌激素受体ER、孕激素受体PR和糖蛋白P阴性。;传代方法:1:3传代;5-7天1次。 ;生长特性:贴壁生长;形态特性:上皮样;相关产品有:HT144-mel细胞、CL 1-5细胞、H69C细胞
A-2780 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:H9c2细胞、TNC-1B12B4细胞、FU-OV-1细胞
PCI-SG231 Cells;背景说明:肝内胆管癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HT1376细胞、HLMVEC细胞、Fao细胞
SKNFI Cells;背景说明:详见相关文献介绍;传代方法:1:4传代,每周换液2次;生长特性:贴壁生长;形态特性:上皮样;相关产品有:Acanthosis Nigricans 3rd attempt-CArcinoma细胞、CAL-12T细胞、NCI H295R细胞
A 375 Cells;背景说明:A375源自一位54岁女性,是Giard DJ等人建立的一系列细胞株中的一株。该细胞可在免疫抑制小鼠上成瘤,在琼脂上形成克隆。;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:上皮细胞样;相关产品有:LAPC4细胞、SCC25细胞、H-1651细胞
GT1-1 Cells;背景说明:GT1-1为GT1细胞系的亚克隆,GT1来源于稳定表达SV40大T抗原的转基因小鼠产生的可以分泌促性腺激素释放激素LHRH的肿瘤。GT1-1细胞可以表达pro-LHRHmRNA,并向培养基中分泌LHRH样的免疫反应性的物质。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:CPAE细胞、UPCI-SCC090细胞、Roswell Park Memorial Institute 7666细胞
Hela人宫颈癌复苏细胞保种中心|带STR证书
BayGenomics ES cell line RRJ519 Cells(提供STR鉴定图谱)
BayGenomics ES cell line XK518 Cells(提供STR鉴定图谱)
FW14-14 Cells(提供STR鉴定图谱)
NQ6.24.2 Cells(提供STR鉴定图谱)
XF11.4C4 Cells(提供STR鉴定图谱)
MCF7-parkin clone 11 Cells(提供STR鉴定图谱)
" "PubMed=13261081
Moore A.E., Sabachewsky L., Toolan H.W.
Culture characteristics of four permanent lines of human cancer cells.
Cancer Res. 15:598-602(1955)
PubMed=16589695; DOI=10.1073/pnas.41.7.432; PMCID=PMC528114
Puck T.T., Marcus P.I.
A rapid method for viable cell titration and clone production with HeLa cells in tissue culture: the use of X-irradiated cells to supply conditioning factors.
Proc. Natl. Acad. Sci. U.S.A. 41:432-437(1955)
PubMed=14031339
Katzberg A.A.
The effect of space flights on living human cells aboard Discoverer XVIII.
Tech. Doc. Rep. SAMTDR USAF Sch. Aerosp. Med. 62:43.1-43.4(1962)
PubMed=14185313; DOI=10.1126/science.146.3641.241
Cell Culture Collection Committee
Animal cell strains. The Cell Culture Collection Committee has assembled and certified 23 strains of animal cells.
Science 146:241-243(1964)
PubMed=5668122; DOI=10.3181/00379727-128-33119
Peterson W.D. Jr., Stulberg C.S., Swanborg N.K., Robinson A.R.
Glucose-6-phosphate dehydrogenase isoenzymes in human cell cultures determined by sucrose-agar gel and cellulose acetate zymograms.
Proc. Soc. Exp. Biol. Med. 128:772-776(1968)
DOI=10.1007/BF02618370
Stulberg C.S., Coriell L.L., Kniazeff A.J., Shannon J.E.
The animal cell culture collection.
In Vitro 5:1-16(1970)
PubMed=4942173; DOI=10.1097/00006250-197112000-00028
Jones H.W. Jr., McKusick V.A., Harper P.S., Wuu K.-D.
George Otto Gey (1899-1970). The HeLa cell and a reappraisal of its origin.
Obstet. Gynecol. 38:945-949(1971)
DOI=10.1007/978-1-4757-1647-4_13
Biedler J.L.
Chromosome abnormalities in human tumor cells in culture.
(In book chapter) Human tumor cells in vitro; Fogh J. (eds.); pp.359-394; Springer; New York; USA (1975)
PubMed=1246620; DOI=10.1126/science.1246620
Hsu S.H., Schacter B.Z., Delaney N.L., Miller T.B., McKusick V.A., Kennett R.H., Bodmer J.G., Young D., Bodmer W.F.
Genetic characteristics of the HeLa cell.
Science 191:392-394(1976)
PubMed=77569; DOI=10.1111/j.1399-0039.1978.tb01259.x
Espmark J.A., Ahlqvist-Roth L., Sarne L., Persson A.
Tissue typing of cells in culture. III. HLA antigens of established human cell lines. Attempts at typing by the mixed hemadsorption technique.
Tissue Antigens 11:279-286(1978)
PubMed=6256643; DOI=10.1038/288724a0
Day R.S. 3rd, Ziolkowski C.H.J., Scudiero D.A., Meyer S.A., Lubiniecki A.S., Girardi A.J., Galloway S.M., Bynum G.D.
Defective repair of alkylated DNA by human tumour and SV40-transformed human cell strains.
Nature 288:724-727(1980)
PubMed=6935474; DOI=10.1093/jnci/66.2.239
Wright W.C., Daniels W.P., Fogh J.
Distinction of seventy-one cultured human tumor cell lines by polymorphic enzyme analysis.
J. Natl. Cancer Inst. 66:239-247(1981)
PubMed=6358339; DOI=10.1093/jhmas/38.4.415
Brown R.W., Henderson J.H.M.
The mass production and distribution of HeLa cells at Tuskegee Institute, 1953-55.
J. Hist. Med. Allied Sci. 38:415-431(1983)
PubMed=6401685; DOI=10.1007/BF02617989
Halton D.M., Peterson W.D. Jr., Hukku B.
Cell culture quality control by rapid isoenzymatic characterization.
In Vitro 19:16-24(1983)
PubMed=6825208; DOI=10.1093/carcin/4.2.199
Yarosh D.B., Foote R.S., Mitra S., Day R.S. 3rd
Repair of O6-methylguanine in DNA by demethylation is lacking in Mer- human tumor cell strains.
Carcinogenesis 4:199-205(1983)
PubMed=2983228; DOI=10.1038/314111a0
Schwarz E., Freese U.-K., Gissmann L., Mayer W., Roggenbuck B., Stremlau A., zur Hausen H.
Structure and transcription of human papillomavirus sequences in cervical carcinoma cells.
Nature 314:111-114(1985)
PubMed=2990217; PMCID=PMC1888002
Yee C., Krishnan-Hewlett I., Baker C.C., Schlegel R., Howley P.M.
Presence and expression of human papillomavirus sequences in human cervical carcinoma cell lines.
Am. J. Pathol. 119:361-366(1985)
CLPUB00262
Gold M.
A conspiracy of cells. One woman's immortal legacy and the medical scandal it caused.
(In book) ISBN 9780887060991; pp.1-171; State University of New York Press; Albany; USA (1986)
PubMed=3518877; DOI=10.3109/07357908609038260
Fogh J.
Human tumor lines for cancer research.
Cancer Invest. 4:157-184(1986)
PubMed=3028716; DOI=10.1159/000132342
Popescu N.C., DiPaolo J.A., Amsbaugh S.C.
Integration sites of human papillomavirus 18 DNA sequences on HeLa cell chromosomes.
Cytogenet. Cell Genet. 44:58-62(1987)
PubMed=3180844; DOI=10.1159/000132579
Chen T.-R.
Re-evaluation of HeLa, HeLa S3, and HEp-2 karyotypes.
Cytogenet. Cell Genet. 48:19-24(1988)
PubMed=3371749; DOI=10.1016/0090-8258(88)90029-7
Grenman S.E., Shapira A., Carey T.E.
In vitro response of cervical cancer cell lines CaSki, HeLa, and ME-180 to the antiestrogen tamoxifen.
Gynecol. Oncol. 30:228-238(1988)
PubMed=1522048; DOI=10.1007/BF02634140
Kataoka E., Honma M., Ohnishi K., Sofuni T., Mizusawa H.
Application of highly polymorphic DNA markers to the identification of HeLa cell sublines.
In Vitro Cell. Dev. Biol. Anim. 28:553-556(1992)
PubMed=8380785; DOI=10.1006/gyno.1993.1016
Iwasaka T., Oh-uchida M., Matsuo N., Yokoyama M., Fukuda K., Hara K., Fukuyama K., Hori K., Sugimori H.
Correlation between HPV positivity and state of the p53 gene in cervical carcinoma cell lines.
Gynecol. Oncol. 48:104-109(1993)
PubMed=9892199
Macville M.V.E., Schrock E., Padilla-Nash H.M., Keck C., Ghadimi B.M., Zimonjic D.B., Popescu N.C., Ried T.
Comprehensive and definitive molecular cytogenetic characterization of HeLa cells by spectral karyotyping.
Cancer Res. 59:141-150(1999)
PubMed=10423141; DOI=10.1099/0022-1317-80-7-1725
Meissner J.D.
Nucleotide sequences and further characterization of human papillomavirus DNA present in the CaSki, SiHa and HeLa cervical carcinoma cell lines.
J. Gen. Virol. 80:1725-1733(1999)
PubMed=11416159; DOI=10.1073/pnas.121616198; PMCID=PMC35459
Masters J.R.W., Thomson J.A., Daly-Burns B., Reid Y.A., Dirks W.G., Packer P., Toji L.H., Ohno T., Tanabe H., Arlett C.F., Kelland L.R., Harrison M., Virmani A.K., Ward T.H., Ayres K.L., Debenham P.G.
Short tandem repeat profiling provides an international reference standard for human cell lines.
Proc. Natl. Acad. Sci. U.S.A. 98:8012-8017(2001)
PubMed=11668190; DOI=10.1177/002215540104901105
Quentmeier H., Osborn M., Reinhardt J., Zaborski M., Drexler H.G.
Immunocytochemical analysis of cell lines derived from solid tumors.
J. Histochem. Cytochem. 49:1369-1378(2001)
PubMed=12001993; DOI=10.1038/nrc775
Masters J.R.W.
HeLa cells 50 years on: the good, the bad and the ugly.
Nat. Rev. Cancer 2:315-319(2002)
PubMed=12793746; DOI=10.1269/jrr.43.s133
Ohnishi T., Ohnishi K., Takahashi A., Taniguchi Y., Sato M., Nakano T., Nagaoka S.
Detection of DNA damage induced by space radiation in Mir and space shuttle.
J. Radiat. Res. 43 Suppl. 1:S133-S136(2002)
PubMed=12661003; DOI=10.1002/gcc.10196
Seitz S., Wassmuth P., Plaschke J., Schackert H.K., Karsten U., Santibanez-Koref M.F., Schlag P.M., Scherneck S.
Identification of microsatellite instability and mismatch repair gene mutations in breast cancer cell lines.
Genes Chromosomes Cancer 37:29-35(2003)
PubMed=15302935; DOI=10.1073/pnas.0404720101; PMCID=PMC514446
Beausoleil S.A., Jedrychowski M.P., Schwartz D., Elias J.E., Villen J., Li J.-X., Cohn M.A., Cantley L.C., Gygi S.P.
Large-scale characterization of HeLa cell nuclear phosphoproteins.
Proc. Natl. Acad. Sci. U.S.A. 101:12130-12135(2004)
PubMed=15531914; DOI=10.1038/sj.onc.1208235
Baldus S.E., Schwarz E., Lohrey C., Zapatka M., Landsberg S., Hahn S.A., Schmidt D., Dienes H.-P., Schmiegel W.H., Schwarte-Waldhoff I.
Smad4 deficiency in cervical carcinoma cells.
Oncogene 24:810-819(2005)
PubMed=15901131; DOI=10.1016/j.prp.2005.01.002
Murai Y., Hayashi S., Takahashi H., Tsuneyama K., Takano Y.
Correlation between DNA alterations and p53 and p16 protein expression in cancer cell lines.
Pathol. Res. Pract. 201:109-115(2005)
PubMed=17311676; DOI=10.1186/1471-2164-8-53; PMCID=PMC1805756
Kloth J.N., Oosting J., van Wezel T., Szuhai K., Knijnenburg J., Gorter A., Kenter G.G., Fleuren G.J., Jordanova E.S.
Combined array-comparative genomic hybridization and single-nucleotide polymorphism-loss of heterozygosity analysis reveals complex genetic alterations in cervical cancer.
BMC Genomics 8:53.1-53.13(2007)
PubMed=19450234; DOI=10.2144/000113089; PMCID=PMC2696096
Rahbari R., Sheahan T., Modes V., Collier P., Macfarlane C.M., Badge R.M.
A novel L1 retrotransposon marker for HeLa cell line identification.
BioTechniques 46:277-284(2009)
PubMed=19722756; DOI=10.5858/133.9.1463
Lucey B.P., Nelson-Rees W.A., Hutchins G.M.
Henrietta Lacks, HeLa cells, and cell culture contamination.
Arch. Pathol. Lab. Med. 133:1463-1467(2009)
CLPUB00377
Skloot R.L.
The immortal life of Henrietta Lacks.
(In book) ISBN 9781400052172; pp.1-400; Random House; New York; USA (2010)
CLPUB00468
Javitt G.H.
Why not take all of me? Reflections on the immortal life of Henrietta Lacks and the status of participants in research using human specimens.
Minn. J. Law Sci. Technol. 11:713-755(2010)
PubMed=19941903; DOI=10.1016/j.jviromet.2009.11.022
Karger A., Bettin B., Lenk M., Mettenleiter T.C.
Rapid characterisation of cell cultures by matrix-assisted laser desorption/ionisation mass spectrometric typing.
J. Virol. Methods 164:116-121(2010)
PubMed=21269460; DOI=10.1186/1752-0509-5-17; PMCID=PMC3039570
Burkard T.R., Planyavsky M., Kaupe I., Breitwieser F.P., Burckstummer T., Bennett K.L., Superti-Furga G., Colinge J.
Initial characterization of the human central proteome.
BMC Syst. Biol. 5:17.1-17.13(2011)
PubMed=22068331; DOI=10.1038/msb.2011.81; PMCID=PMC3261714
Nagaraj N., Wisniewski J.R., Geiger T., Cox J., Kircher M., Kelso J., Paabo S., Mann M.
Deep proteome and transcriptome mapping of a human cancer cell line.
Mol. Syst. Biol. 7:548-548(2011)
PubMed=21937730; DOI=10.1074/mcp.M111.011429; PMCID=PMC3316722
Boisvert F.-M., Ahmad Y., Gierlinski M., Charriere F., Lamont D., Scott M., Barton G., Lamond A.I.
A quantitative spatial proteomics analysis of proteome turnover in human cells.
Mol. Cell. Proteomics 11:M111.011429-M111.011429(2012)
PubMed=22278370; DOI=10.1074/mcp.M111.014050; PMCID=PMC3316730
Geiger T., Wehner A., Schaab C., Cox J., Mann M.
Comparative proteomic analysis of eleven common cell lines reveals ubiquitous but varying expression of most proteins.
Mol. Cell. Proteomics 11:M111.014050-M111.014050(2012)
PubMed=22412903; DOI=10.1371/journal.pone.0032667; PMCID=PMC3296745
Vazquez-Mena O., Medina-Martinez I., Juarez-Torres E., Barron V., Espinosa A., Villegas-Sepulveda N., Gomez-Laguna L., Nieto-Martinez K., Orozco L., Roman-Bassaure E., Munoz Cortez S., Borges Ibanez M., Venegas-Vega C.A., Guardado-Estrada M., Rangel-Lopez A., Kofman S., Berumen J.
Amplified genes may be overexpressed, unchanged, or downregulated in cervical cancer cell lines.
PLoS ONE 7:E32667-E32667(2012)
CLPUB00507
Pultarova T.
HeLa cells: immortal space travellers.
Space Saf. Mag. 7:10-12(2013)
PubMed=23205564; DOI=10.1021/pr300859k
Malerod H., Graham R.L.J., Sweredoski M.J., Hess S.
Comprehensive profiling of N-linked glycosylation sites in HeLa cells using hydrazide enrichment.
J. Proteome Res. 12:248-259(2013)
PubMed=23336012; DOI=10.1371/journal.pone.0054672; PMCID=PMC3545996
Horvat T., Dezeljin M., Redzic I., Barisic D., Herak Bosnar M., Lauc G., Zoldos V.
Reversibility of membrane N-glycome of HeLa cells upon treatment with epigenetic inhibitors.
PLoS ONE 8:E54672-E54672(2013)
PubMed=23925224; DOI=10.1038/500141a; PMCID=PMC5101952
Hudson K.L., Collins F.S.
Biospecimen policy: family matters.
Nature 500:141-142(2013)
PubMed=23925245; DOI=10.1038/nature12064; PMCID=PMC3740412
Adey A.C., Burton J.N., Kitzman J.O., Hiatt J.B., Lewis A.P., Martin B.K., Qiu R.-L., Lee C., Shendure J.
The haplotype-resolved genome and epigenome of the aneuploid HeLa cancer cell line.
Nature 500:207-211(2013)
PubMed=24134916; DOI=10.1186/1755-8166-6-44; PMCID=PMC3879223
McCormack A., Fan J.-L., Duesberg M., Bloomfield M., Fiala C., Duesberg P.H.
Individual karyotypes at the origins of cervical carcinomas.
Mol. Cytogenet. 6:44.1-44.23(2013)
PubMed=24618588; DOI=10.1371/journal.pone.0091433; PMCID=PMC3950186
Chernobrovkin A.L., Zubarev R.A.
Detection of viral proteins in human cells lines by xeno-proteomics: elimination of the last valid excuse for not testing every cellular proteome dataset for viral proteins.
PLoS ONE 9:E91433-E91433(2014)
PubMed=24696503; DOI=10.1074/mcp.M113.035170; PMCID=PMC4047476
Guo X.-F., Trudgian D.C., Lemoff A., Yadavalli S., Mirzaei H.
Confetti: a multiprotease map of the HeLa proteome for comprehensive proteomics.
Mol. Cell. Proteomics 13:1573-1584(2014)
PubMed=24908793
Gilgenkrantz S.
Sixty years of HeLa cell cultures.
Hist. Sci. Med. 48:139-144(2014)
PubMed=25960936; DOI=10.4161/21624011.2014.954893; PMCID=PMC4355981
Boegel S., Lower M., Bukur T., Sahin U., Castle J.C.
A catalog of HLA type, HLA expression, and neo-epitope candidates in human cancer cell lines.
OncoImmunology 3:e954893.1-e954893.12(2014)
CLPUB00376
Verspaget C.J.
Unruly bodies: monstrous readings of biotechnology.
Thesis PhD (2015); Curtin University; Perth; Australia
PubMed=25485619; DOI=10.1038/nbt.3080
Klijn C., Durinck S., Stawiski E.W., Haverty P.M., Jiang Z.-S., Liu H.-B., Degenhardt J., Mayba O., Gnad F., Liu J.-F., Pau G., Reeder J., Cao Y., Mukhyala K., Selvaraj S.K., Yu M.-M., Zynda G.J., Brauer M.J., Wu T.D., Gentleman R.C., Manning G., Yauch R.L., Bourgon R., Stokoe D., Modrusan Z., Neve R.M., de Sauvage F.J., Settleman J., Seshagiri S., Zhang Z.-M.
A comprehensive transcriptional portrait of human cancer cell lines.
Nat. Biotechnol. 33:306-312(2015)
PubMed=25807930; DOI=10.1002/anie.201500342; PMCID=PMC4471546
Broncel M., Serwa R.A., Ciepla P., Krause E., Dallman M.J., Magee A.I., Tate E.W.
Multifunctional reagents for quantitative proteome-wide analysis of protein modification in human cells and dynamic profiling of protein lipidation during vertebrate development.
Angew. Chem. Int. Ed. Engl. 54:5948-5951(2015)
PubMed=25877200; DOI=10.1038/nature14397
Yu M., Selvaraj S.K., Liang-Chu M.M.Y., Aghajani S., Busse M., Yuan J., Lee G., Peale F.V., Klijn C., Bourgon R., Kaminker J.S., Neve R.M.
A resource for cell line authentication, annotation and quality control.
Nature 520:307-311(2015)
PubMed=25894527; DOI=10.1371/journal.pone.0121314; PMCID=PMC4404347
Bausch-Fluck D., Hofmann A., Bock T., Frei A.P., Cerciello F., Jacobs A., Moest H., Omasits U., Gundry R.L., Yoon C., Schiess R., Schmidt A., Mirkowska P., Hartlova A.S., Van Eyk J.E., Bourquin J.-P., Aebersold R., Boheler K.R., Zandstra P.W., Wollscheid B.
A mass spectrometric-derived cell surface protein atlas.
PLoS ONE 10:E0121314-E0121314(2015)
PubMed=26554430; DOI=10.1021/acs.analchem.5b03639
Dimayacyac-Esleta B.R.T., Tsai C.-F., Kitata R.B., Lin P.-Y., Choong W.-K., Lin T.-D., Wang Y.-T., Weng S.-H., Yang P.-C., Arco S.D., Sung T.-Y., Chen Y.-J.
Rapid high-pH reverse phase stagetip for sensitive small-scale membrane proteomic profiling.
Anal. Chem. 87:12016-12023(2015)
PubMed=26589293; DOI=10.1186/s13073-015-0240-5; PMCID=PMC4653878
Scholtalbers J., Boegel S., Bukur T., Byl M., Goerges S., Sorn P., Loewer M., Sahin U., Castle J.C.
TCLP: an online cancer cell line catalogue integrating HLA type, predicted neo-epitopes, virus and gene expression.
Genome Med. 7:118.1-118.7(2015)
PubMed=27397505; DOI=10.1016/j.cell.2016.06.017; PMCID=PMC4967469
Iorio F., Knijnenburg T.A., Vis D.J., Bignell G.R., Menden M.P., Schubert M., Aben N., Goncalves E., Barthorpe S., Lightfoot H., Cokelaer T., Greninger P., van Dyk E., Chang H., de Silva H., Heyn H., Deng X.-M., Egan R.K., Liu Q.-S., Miroo T., Mitropoulos X., Richardson L., Wang J.-H., Zhang T.-H., Moran S., Sayols S., Soleimani M., Tamborero D., Lopez-Bigas N., Ross-Macdonald P., Esteller M., Gray N.S., Haber D.A., Stratton M.R., Benes C.H., Wessels L.F.A., Saez-Rodriguez J., McDermott U., Garnett M.J.
A landscape of pharmacogenomic interactions in cancer.
Cell 166:740-754(2016)
PubMed=28078501; DOI=10.1007/s11626-016-0128-8
Ambrose C.T.
The Tissue Culture Laboratory of Dr. George Otto Gey 60 yrs ago as recalled by a former student.
In Vitro Cell. Dev. Biol. Anim. 53:467-473(2017)
PubMed=28196595; DOI=10.1016/j.ccell.2017.01.005; PMCID=PMC5501076
Li J., Zhao W., Akbani R., Liu W.-B., Ju Z.-L., Ling S.-Y., Vellano C.P., Roebuck P., Yu Q.-H., Eterovic A.K., Byers L.A., Davies M.A., Deng W.-L., Gopal Y.N.V., Chen G., von Euw E.M., Slamon D.J., Conklin D., Heymach J.V., Gazdar A.F., Minna J.D., Myers J.N., Lu Y.-L., Mills G.B., Liang H.
Characterization of human cancer cell lines by reverse-phase protein arrays.
Cancer Cell 31:225-239(2017)
PubMed=28261610; DOI=10.1155/2017/4180703; PMCID=PMC5316418
Kontostathi G., Zoidakis J., Makridakis M., Lygirou V., Mermelekas G., Papadopoulos T., Vougas K., Vlamis-Gardikas A., Drakakis P., Loutradis D., Vlahou A., Anagnou N.P., Pappa K.I.
Cervical cancer cell line secretome highlights the roles of transforming growth factor-beta-induced protein ig-h3, peroxiredoxin-2, and NRF2 on cervical carcinogenesis.
BioMed Res. Int. 2017:4180703.1-4180703.15(2017)
PubMed=28601559; DOI=10.1016/j.cels.2017.05.009; PMCID=PMC5493283
Bekker-Jensen D.B., Kelstrup C.D., Batth T.S., Larsen S.C., Haldrup C., Bramsen J.B., Sorensen K.D., Hoyer S., Orntoft T.F., Lindbjerg Andersen C., Nielsen M.L., Olsen J.V.
An optimized shotgun strategy for the rapid generation of comprehensive human proteomes.
Cell Syst. 4:587-599.e4(2017)
PubMed=29156801; DOI=10.18632/oncotarget.21174; PMCID=PMC5689691
Kalu N.N., Mazumdar T., Peng S.-H., Shen L., Sambandam V., Rao X.-Y., Xi Y.-X., Li L.-R., Qi Y., Gleber-Netto F.O., Patel A., Wang J., Frederick M.J., Myers J.N., Pickering C.R., Johnson F.M.
Genomic characterization of human papillomavirus-positive and -negative human squamous cell cancer cell lines.
Oncotarget 8:86369-86383(2017)
PubMed=30175587; DOI=10.1021/acs.jproteome.8b00392
Robin T., Bairoch A., Muller M., Lisacek F., Lane L.
Large-scale reanalysis of publicly available HeLa cell proteomics data in the context of the Human Proteome Project.
J. Proteome Res. 17:4160-4170(2018)
PubMed=30778230; DOI=10.1038/s41587-019-0037-y
Liu Y.-S., Mi Y., Mueller T., Kreibich S., Williams E.G., Van Drogen A., Borel C., Frank M., Germain P.-L., Bludau I., Mehnert M., Seifert M., Emmenlauer M., Sorg I., Bezrukov F., Sloan-Bena F., Zhou H., Dehio C., Testa G., Saez-Rodriguez J., Antonarakis S.E., Hardt W.-D., Aebersold R.
Multi-omic measurements of heterogeneity in HeLa cells across laboratories.
Nat. Biotechnol. 37:314-322(2019)
PubMed=30787054; DOI=10.1158/1055-9965.EPI-18-1132; PMCID=PMC6548687
Hooker S.E. Jr., Woods-Burnham L., Bathina M., Lloyd S., Gorjala P., Mitra R., Nonn L., Kimbro K.S., Kittles R.A.
Genetic ancestry analysis reveals misclassification of commonly used cancer cell lines.
Cancer Epidemiol. Biomarkers Prev. 28:1003-1009(2019)
PubMed=30894373; DOI=10.1158/0008-5472.CAN-18-2747; PMCID=PMC6445675
Dutil J., Chen Z.-H., Monteiro A.N.A., Teer J.K., Eschrich S.A.
An interactive resource to probe genetic diversity and estimated ancestry in cancer cell lines.
Cancer Res. 79:1263-1273(2019)
PubMed=31068700; DOI=10.1038/s41586-019-1186-3; PMCID=PMC6697103
Ghandi M., Huang F.W., Jane-Valbuena J., Kryukov G.V., Lo C.C., McDonald E.R. 3rd, Barretina J.G., Gelfand E.T., Bielski C.M., Li H.-X., Hu K., Andreev-Drakhlin A.Y., Kim J., Hess J.M., Haas B.J., Aguet F., Weir B.A., Rothberg M.V., Paolella B.R., Lawrence M.S., Akbani R., Lu Y.-L., Tiv H.L., Gokhale P.C., de Weck A., Mansour A.A., Oh C., Shih J., Hadi K., Rosen Y., Bistline J., Venkatesan K., Reddy A., Sonkin D., Liu M., Lehar J., Korn J.M., Porter D.A., Jones M.D., Golji J., Caponigro G., Taylor J.E., Dunning C.M., Creech A.L., Warren A.C., McFarland J.M., Zamanighomi M., Kauffmann A., Stransky N., Imielinski M., Maruvka Y.E., Cherniack A.D., Tsherniak A., Vazquez F., Jaffe J.D., Lane A.A., Weinstock D.M., Johannessen C.M., Morrissey M.P., Stegmeier F., Schlegel R., Hahn W.C., Getz G., Mills G.B., Boehm J.S., Golub T.R., Garraway L.A., Sellers W.R.
Next-generation characterization of the Cancer Cell Line Encyclopedia.
Nature 569:503-508(2019)
PubMed=31433507; DOI=10.15252/embj.2018100847; PMCID=PMC6826212
Hardman G., Perkins S., Brownridge P.J., Clarke C.J., Byrne D.P., Campbell A.E., Kalyuzhnyy A., Myall A., Eyers P.A., Jones A.R., Eyers C.E.
Strong anion exchange-mediated phosphoproteomics reveals extensive human non-canonical phosphorylation.
EMBO J. 38:e100847.1-e100847.22(2019)
PubMed=31790455; DOI=10.1371/journal.pone.0225466; PMCID=PMC6886862
Hu W.-E., Zhang X., Guo Q.-F., Yang J.-W., Yang Y., Wei S.-C., Su X.-D.
HeLa-CCL2 cell heterogeneity studied by single-cell DNA and RNA sequencing.
PLoS ONE 14:E0225466-E0225466(2019)
PubMed=33389257; DOI=10.1007/s10096-020-04106-0; PMCID=PMC7778494
Wurtz N., Penant G., Jardot P., Duclos N., La Scola B.
Culture of SARS-CoV-2 in a panel of laboratory cell lines, permissivity, and differences in growth profile.
Eur. J. Clin. Microbiol. Infect. Dis. 40:477-484(2021)"