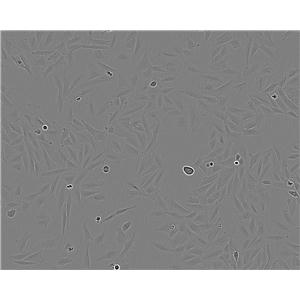
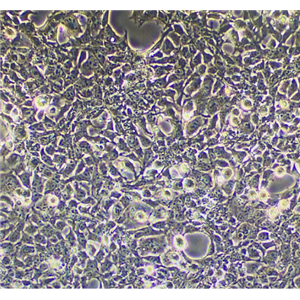
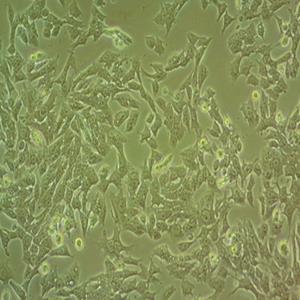
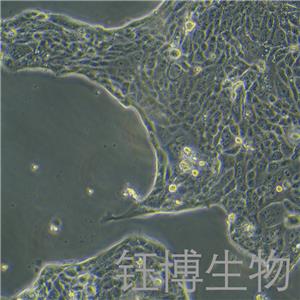
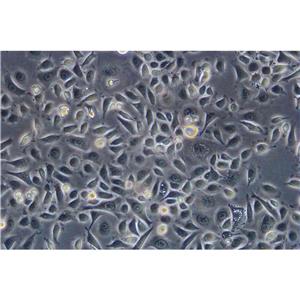
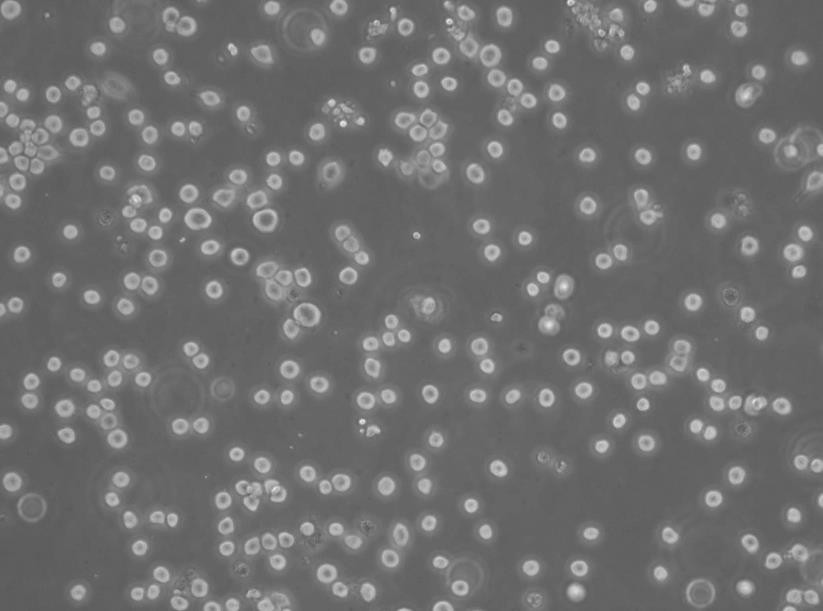
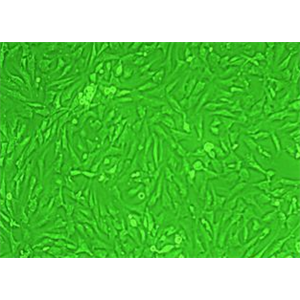
"Calu-3人肺腺癌复苏细胞保种中心|带STR证书<胸水>
传代比例:1:2-1:4(首次传代建议1:2)
生长特性:贴壁生长
细胞冻存复苏材料与方法步骤:常用的细胞冷冻贮存器为贮存器,规格有35L和50L两种。使用时要注意以下几点:(1)一般两周需充一次,至少一个月充一次。温度达-196℃,使用时注意勿让溅到皮肤上,以免引起冻伤。(2)容器为双层结构,中间为真空层,瓶口有双层焊接处,应防止焊接部裂开。(3)在装入时,要注意缓慢小心,并用厚纸卷筒或制漏斗作引导,使直达瓶底,如有专用灌注装置则更HAO。若为初次使用,加时更要缓慢,以免温度骤降而使容器损坏。细胞冻存时常备的材料有:0.25%胰蛋白酶,含10%~20%的血清培养,DMSO(分析纯)或无色新鲜甘油(121°C蒸气GAO压消毒),2mL安瓿(或专用细胞冻存管)、吸管、离心管、喷灯、纱布袋(或冻存管架)等。主要操作步骤为:(1)选择处于对数生长期的细胞,在冻存前一天ZuiHAO换。将多个培养瓶中的细胞培养 去掉,用0.25%胰蛋白酶消化。适时去掉胰蛋白酶,加入少量新培养。用吸管吸取培养反复吹打瓶壁上的细胞,使其成为均匀分散的细胞悬。悬浮生产细胞则不要消化处理。然后将细胞收集于离心管中离心(1000r/min,10分钟)。(2)去上清,加入含20%小牛血清的完全培养基,于4℃预冷15分钟后,逐滴加入已无菌的DMSO或甘油,用吸管轻轻吹打使细胞均匀,细胞浓度为3×106~1×107/mL之间。(3)将上述细胞分装于安瓿或专用冷冻塑料管中,安瓿装1~1.5mL在火焰喷灯上封口,封口处要完全封闭,圆滑无勾。冷冻管要将盖子盖紧,并标记HAO细胞名称和冻存日期,同时作HAO登记(日期、细胞种类及代次、冻存支数)。(4)将装HAO细胞的安瓿或冻存管装入沙布袋内;置于容器颈口处存放过夜,次日转入中。采用控制降温速度的方法也可采用下列步骤:先将安瓿置入4℃冰箱中2~3小时,再移至冰箱冷冻室内3~4小时,再吊入容器颈气态部分存放2小时,Zui后沉入中。细胞冻存在中可以长期保存,但为妥善起见,冻存半年后,ZuiHAO取出一只安瓿细胞复苏培养,观察生长情况,然后再继续冻存。
换液周期:每周2-3次
Meat Animal Research Center-145 Cells;背景说明:胚肾;自发永生;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:Hu-P-T3细胞、CWR22R细胞、CCD-841-CoN细胞
Stanford University-Diffuse Histiocytic Lymphoma-4 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:淋巴母细胞;相关产品有:MDA-MB361细胞、SW-837细胞、Cloudman M3细胞
SUDHL-1 Cells;背景说明:间变性大细胞淋巴瘤;胸腔积液转移;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:NCI-SNU-119细胞、JIMT-1细胞、COS1细胞
Calu-3人肺腺癌复苏细胞保种中心|带STR证书<胸水>
背景信息:该细胞是从一名25岁的白人男性肺腺癌患者的胸水中分离建立的;该患者曾使用过环磷酰胺、博来霉素、阿霉素进行治疗。该细胞接种至裸鼠可成瘤;可作转染宿主。
细胞系的选择需要考虑到细胞系的功能特点、生长速率、铺板效率、生长条件和生长特征、克隆效率、培养方式等因素,如果您想高产量表达重组蛋白,您可以选择可以悬浮生长的快速生长细胞系。细胞培养的操作步骤主要包括传代、换液、冻存和复苏。这些步骤确保了细胞能够在实验室环境中长期存活并继续增殖。传代是将细胞从一个容器转移到另一个容器的过程,以扩大细胞数量;换液是为了清除代谢废物并补充新鲜培养基;冻存则是为了长期保存细胞,而复苏则是重新激活冷冻保存的细胞使其恢复正常生长。
产品包装:复苏发货:T25培养瓶(一瓶)或冻存发货:1ml冻存管(两支)
来源说明:细胞主要来源ATCC、ECACC、DSMZ、RIKEN等细胞库
JIII Cells;背景说明:单核细胞白血病;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:MDA-MB-468细胞、LS1034细胞、3D4/21细胞
RK13 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:CCLP1细胞、AMJ2C8细胞、H-2444细胞
NCI-H647 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:6传代;每周换液2次。;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:HCCLM6细胞、SPC-A-1细胞、Intestinal Epithelioid Cell line No. 6细胞
UCW 100 Cells;背景说明:肺;自发永生;雄性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:RPTEC/TERT 1细胞、SW839细胞、TCam 2细胞
Calu-3人肺腺癌复苏细胞保种中心|带STR证书<胸水>
物种来源:人源、鼠源等其它物种来源
形态特性:上皮细胞样
很多朋友讨论细胞培养问题,见到很多很HAO的经验总结,这里说一些我个人的经验,因为一些比较殊的原因,我自己培养接触过近300种细胞,常用于做实验的,累积有百余种,可以说遇到过许多各式各样古怪的细胞。这里挑细胞消化开始做我的第一篇专题,并不是因为细胞消化Zui重要,而是近期看到大家频繁讨论这个话题,我就抛砖引玉,下面几点拙见,可能与其它朋友总结的一些经验有点出入,仅供大家参考。许多同学对细胞消化做了许多研究,得出了很多有价值的经验,也见到很多人的困惑。其实细胞培养,尤其是细胞系的培养,就消化而言,不是太难,做得多了,善于总结经验,就能把细胞越养越HAO。一般的程序步骤,细节操作,我这里就不讲了,只讲一些基本操作背后的知识,如果不对之处,欢迎指正,总结下来,细胞培养中消化很重要,但其实消化并不是细胞培养的关键所在(虽然很重要),关键所在是细胞来源,血清质量和水源(自己配制溶的话)。我看到版上许多人养细胞遇到各种各样的问题,很多时候boleneck没有找到,虽然通过其它方法有所改善,但仍然是事倍功半。因为人们往往注意自己的操作,总觉得自己没有经验,而忽视试剂,溶尤其是细胞的质量,后者其实才是许多细胞培养实验室常见的问题。
A-72 Cells;背景说明:癌细胞;金毛猎犬;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:MDA-157细胞、aTC1 Clone 6细胞、NU-GC-4细胞
KM12SM Cells;背景说明:结肠癌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:OV90细胞、16-HBEo细胞、SW 948细胞
NCI-H1793 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:6传代 ;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:Sol8细胞、Colo-678细胞、H-2135细胞
ABC-1 Cells;背景说明:详见相关文献介绍;传代方法:每周换液2次。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:NCIH1869细胞、L 363细胞、NCIH1930细胞
hSCC-25 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:10传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:SF 295细胞、K1735细胞、HDF-a细胞
Buffalo Rat Liver-3A Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:VMRCLCD细胞、Hs940.T细胞、Verda reno细胞
VAESBJ Cells;背景说明:详见相关文献介绍;传代方法:1:3传代,每周2次;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:ELD-1细胞、NCI-H322T细胞、MyLa2059细胞
HS-5 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:上皮细胞样;相关产品有:HEK293-F细胞、HEK293细胞、TN5B14细胞
Hs675T Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代,每周2-3次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:A2780/CP70细胞、Tu-177细胞、624 MEL细胞
M1 Cells;背景说明:髓系白血病;SL;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:VM-CUB-1细胞、COLO-320细胞、MDA-MB-435S细胞
Renal Proximal Tubule Epithelial Cells/TERT-immortalized 1 Cells;背景说明:肾;近端小管上皮;HGNC-TERT转化;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:NCI-H-69细胞、WI38细胞、H-292细胞
GM06141 Cells;背景说明:这株淋巴母细胞样细胞株,源自一位30岁白人男性一,患有恶性红细胞白血病,能够自然产生并能诱导球蛋白合成。细胞的EB病毒核抗原阴性,没有表面免疫球蛋白与细胞质免疫球蛋白。HEL细胞表达HLA抗原(HLA-A3,AW32,BW35),β-2小球蛋白,一定比例的细胞还表达Ia抗原。这个细胞株提供了一种用于研究红细胞分化和球蛋白基因表达的模型。它类似于小鼠中的血友病。;传代方法:1:2传代。3天内可长满。;生长特性:悬浮生长;形态特性:淋巴母细胞样;相关产品有:RBL-I细胞、THP 1细胞、NCI N87细胞
SCL II Cells;背景说明:皮肤鳞癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:IBRS-2细胞、HO-8910细胞、J774.A1细胞
HCC0015 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:COV434细胞、IBMF-7细胞、IMCD-3细胞
CTLL-2 Cells;背景说明:该细胞是源自C57BL/6的细胞毒性的T淋巴细胞。其生长以来IL-2。;传代方法:1:2传代;生长特性:悬浮生长;形态特性:详见产品说明书;相关产品有:M14细胞、CemT4细胞、KLM-1细胞
SBC-5 Cells;背景说明:详见相关文献介绍;传代方法:每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SACC-LM细胞、Soleus clone 8细胞、253J-Bladder-V细胞
MT-2J Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;生长特性:悬浮生长;形态特性:淋巴母细胞;相关产品有:SKNAS细胞、FUOV1细胞、293/EBNA细胞
Calu-3人肺腺癌复苏细胞保种中心|带STR证书<胸水>
3G10G5 Cells(提供STR鉴定图谱)
Abcam Jurkat ARSA KO Cells(提供STR鉴定图谱)
AKR-MCA Cells(提供STR鉴定图谱)
BayGenomics ES cell line RRJ465 Cells(提供STR鉴定图谱)
BayGenomics ES cell line XK440 Cells(提供STR鉴定图谱)
Ca759 Cells(提供STR鉴定图谱)
DA00375 Cells(提供STR鉴定图谱)
DA04988 Cells(提供STR鉴定图谱)
G1 [Drosophila] Cells(提供STR鉴定图谱)
CHO Cells;背景说明:1957年,PuckTT从成年中国仓鼠卵巢的活检组织建立了CHO细胞;广泛用于生物制品的表达。;传代方法:1:3传代,3-4天换液一次;生长特性:贴壁生长;形态特性:上皮样;相关产品有:MT-2细胞、EVSAT细胞、HECCL-1细胞
RC-2 Cells;背景说明:来源于日本人的肾脏肿瘤细胞。 可以移植到裸鼠。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:HR-1细胞、HPDE细胞、OKT3细胞
10T1/2 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:BGC-823细胞、MT2细胞、NTERA2细胞
Line 207 Cells;背景说明:儿童急性髓系白血病;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:HCC1806细胞、BC-022细胞、U251-MG细胞
130T Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代,3-4天换液1次。;生长特性:贴壁生长;形态特性:梭型和大的多核细胞;相关产品有:L 132细胞、HuPT4细胞、F81细胞
C32 mel Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代,2天换液1次。;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:MESSA-DX5细胞、C1R细胞、NGEC细胞
14E5 Cells(提供STR鉴定图谱)
SNU-761 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:HM1900细胞、MES 13细胞、769P细胞
A2780 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:RMG1细胞、Sf21细胞、CCD 841 CoTr细胞
HNE3 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:GM04678细胞、KYSE-410细胞、LM-TK-细胞
GM05372E Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SNU423细胞、NBL-7细胞、L5178YR细胞
H510 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:8传代;每周换液2次。;生长特性:混合生长;形态特性:上皮细胞样;相关产品有:OCI-LY-1细胞、BEL7404细胞、IMR-90细胞
U87 MG Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:F56 [Human neoplasm]细胞、Chinese Hamster Lung细胞、NCI-H929细胞
H2030 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:4传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:Molm14细胞、CALU1细胞、L 1210细胞
BNCL-2 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:CAKI 2细胞、QGY-7701细胞、A72细胞
GM09937 Cells(提供STR鉴定图谱)
HAP1 BRD4 (-) 3 Cells(提供STR鉴定图谱)
PIG3 Cells;背景说明:皮肤;黑色素 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HT 29细胞、786-O RCC细胞、JURKAT E-61细胞
TGBC11T Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:Co 205细胞、CLONE M3细胞、CMT167细胞
BIC-1 Cells;背景说明:食管腺癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:BALB/c 3T3 clone A31细胞、SW-756细胞、ONS76细胞
SUDHL-6 Cells;背景说明:详见相关文献介绍;传代方法:1:3—1:6传代,3—4天换液1次;生长特性:悬浮生长 ;形态特性:淋巴母细胞样;相关产品有:MCF-10 Attached细胞、University of Michigan-Renal Carcinoma-2细胞、RGC-5细胞
T1-73 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:PM6细胞、C12细胞、CL MC/9细胞
HEK 293-H Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:Hs870T细胞、KYSE510细胞、PLA801-95C细胞
HCMEC Cells;背景说明:心脏微血管;内皮 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:C4-2B细胞、LAD-2细胞、Hs706T细胞
OVISE Cells;背景说明:详见相关文献介绍;传代方法:5 x 10^4 cells/ml;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:HCC1954BL细胞、H2087细胞、HM细胞
HG03398 Cells(提供STR鉴定图谱)
ID00017 Cells(提供STR鉴定图谱)
LNCaP95 clone 2-D3 Cells(提供STR鉴定图谱)
NCI-H460-Luc Cells(提供STR鉴定图谱)
PathHunter U2OS CDC25A Degradation Cells(提供STR鉴定图谱)
Ubigene Hep G2 SGMS1 KO Cells(提供STR鉴定图谱)
XYFMGG04D Cells(提供STR鉴定图谱)
HEV0188 Cells(提供STR鉴定图谱)
SCC-25 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:10传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:ZR75-1细胞、HUT 28细胞、RPMI #1846细胞
NCIH520 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:6传代;2-3天换液1次;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SUDHL-16细胞、A 172细胞、DC2.4细胞
Panc02-H0 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:PANC-08-13细胞、Y-1细胞、VA-ES-BJ细胞
UMR 106 Cells;背景说明:注射放射性同位素磷(32P)诱导产生的可移植性大鼠骨肉瘤克隆建立了UMR-106细胞株。 细胞对PTH,前列腺素及破骨甾体有响应。 对PTH的响应度,UMR-106比相关细胞株UMR-108(ATCC CRL-1663)要高。 蛋白激酶C的活化抑制ATP诱导的胞内水平的升高。 起始骨肉瘤和克隆株都是University of Sheffield的T.J. Martin建立的。;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:上皮细胞样;相关产品有:SW 1990细胞、BSC1细胞、PC-3M-IE8细胞
AdHek Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:BHT101细胞、WPE-int细胞、Hs 766细胞
AdHek Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:BHT101细胞、WPE-int细胞、Hs 766细胞
TE-11 Cells;背景说明:详见相关文献介绍;传代方法:消化3-5分钟。1:2。3天内可长满。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:HuPT4细胞、COV434细胞、RPMI6666细胞
MOLT 4 Cells;背景说明:MOLT-4与MOLT-3来源于一名19岁的男性急性淋巴细胞性白血病的复发患者,该患者前期接受过多种药物联合化疗。MOLT-4细胞系为T淋巴细胞起源,p53基因的第248位密码子有一个G→A突变,不表达p53,不表达免疫球蛋白或EB病毒;可产生高水平的末端脱氧核糖转移酶;表达CD1(49%),CD2(35%),CD3A(26%)B(33%)C(34%),CD4(55%),CD5(72%),CD6(22%),CD7(77%)。;传代方法:1:2传代;生长特性:悬浮生长;形态特性:淋巴母细胞样;圆形;相关产品有:NCI-H676B细胞、NBLAN5T细胞、TMK-1细胞
NCI-H2085 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:6传代 ;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:L-6细胞、H-7721细胞、HT55细胞
TE 671 Cells;背景说明:胚胎性横纹肌肉瘤;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SCC15细胞、RT4细胞、SACCLM细胞
A72 Cells;背景说明:癌细胞;金毛猎犬;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:JROECL19细胞、P3/NS1/1-Ag4.1细胞、PF382细胞
AC29 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:HEC-1-B细胞、H8细胞、GM3190细胞
HEK 293 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:WM266细胞、PaTu8988s细胞、LN382细胞
LMTK- Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:ECV细胞、MUM2B细胞、MOLM-13细胞
CemT4 Cells;背景说明:急性T淋巴细胞白血病;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:HCC-1937细胞、X63-Ag8细胞、GM2219C细胞
SAS-H1 Cells(提供STR鉴定图谱)
8402 Cells;背景说明:急性T淋巴细胞白血病;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:VMCUB1细胞、BMDC细胞、WM 2664细胞
MPC 11 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:悬浮生长;形态特性:详见产品说明书;相关产品有:KLE细胞、H1105细胞、SEG-1细胞
SUM 159PT Cells;背景说明:乳腺癌;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:GM02132细胞、TE-5细胞、P3-X63Ag8.653细胞
L929 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:NCI-H1792细胞、HuCC-T1细胞、293 EBNA细胞
10T1/2 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:BGC-823细胞、MT2细胞、NTERA2细胞
ROS 17/2.8 Cells;背景说明:骨肉瘤;ACI 9935;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HLFa细胞、293 Ad5细胞、UMNSAH-DF 1细胞
MRAEC Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:LNCaP C4-2B细胞、LS-123细胞、RAMSCs细胞
MC/CAR Cells;背景说明:B淋巴;EBV转化;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:A-2058细胞、A 72细胞、WEHI 3B细胞
SKNEP Cells;背景说明:超微结构有少许微绒毛,连接复合物,形态完整的高尔基体,内质网多为光滑型,脂滴,没有病毒棵粒。;传代方法:1:2传代。3天内可长满。;生长特性:半贴壁生长;形态特性:上皮细胞;相关产品有:U-138MG细胞、U14细胞、BIC1细胞
VM Cub 1 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:INS1E细胞、DHL6细胞、hFOB细胞
LC-1-sq Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:RH35细胞、CL MC/9细胞、Calu6细胞
NCIH747 Cells;背景说明:详见相关文献介绍;传代方法:1:2—1:4传代,每周换液2次;生长特性:贴壁生长;形态特性:上皮样;相关产品有:SK Mel 1细胞、E.G7-OVA细胞、HUC-1细胞
GCT0404 Cells;背景说明:骨巨细胞瘤;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:CMT64细胞、EM3细胞、H2126细胞
A101D Cells;背景说明:详见相关文献介绍;传代方法:1:4-1:6传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:CL 1-5细胞、A375.S2细胞、TE-3A细胞
Calu-3人肺腺癌复苏细胞保种中心|带STR证书<胸水>
BayGenomics ES cell line RRJ155 Cells(提供STR鉴定图谱)
BayGenomics ES cell line XK138 Cells(提供STR鉴定图谱)
FL653 Cells(提供STR鉴定图谱)
NIH3T3/fPD1 Cells(提供STR鉴定图谱)
WAZ-1 Cells(提供STR鉴定图谱)
MCF10A-AKTm-1 Cells(提供STR鉴定图谱)
" "PubMed=3518877; DOI=10.3109/07357908609038260
Fogh J.
Human tumor lines for cancer research.
Cancer Invest. 4:157-184(1986)
PubMed=3940644
Brower M., Carney D.N., Oie H.K., Gazdar A.F., Minna J.D.
Growth of cell lines and clinical specimens of human non-small cell lung cancer in a serum-free defined medium.
Cancer Res. 46:798-806(1986)
PubMed=3129183
Hubbard W.C., Alley M.C., McLemore T.L., Boyd M.R.
Evidence for thromboxane biosynthesis in established cell lines derived from human lung adenocarcinomas.
Cancer Res. 48:2674-2677(1988)
PubMed=3335022
Alley M.C., Scudiero D.A., Monks A., Hursey M.L., Czerwinski M.J., Fine D.L., Abbott B.J., Mayo J.G., Shoemaker R.H., Boyd M.R.
Feasibility of drug screening with panels of human tumor cell lines using a microculture tetrazolium assay.
Cancer Res. 48:589-601(1988)
PubMed=7515578; DOI=10.1152/ajplung.1994.266.5.L493
Shen B.-Q., Finkbeiner W.E., Wine J.J., Mrsny R.J., Widdicombe J.H.
Calu-3: a human airway epithelial cell line that shows cAMP-dependent Cl-secretion.
Am. J. Physiol. 266:L493-L501(1994)
PubMed=9636188; DOI=10.1073/pnas.95.13.7556; PMCID=PMC22681
Kaplan D.H., Shankaran V., Dighe A.S., Stockert E., Aguet M., Old L.J., Schreiber R.D.
Demonstration of an interferon gamma-dependent tumor surveillance system in immunocompetent mice.
Proc. Natl. Acad. Sci. U.S.A. 95:7556-7561(1998)
PubMed=10523844; DOI=10.1038/sj.onc.1202957
Agochiya M., Brunton V.G., Owens D.W., Parkinson E.K., Paraskeva C., Keith W.N., Frame M.C.
Increased dosage and amplification of the focal adhesion kinase gene in human cancer cells.
Oncogene 18:5646-5653(1999)
PubMed=11064206; DOI=10.1016/S0378-5173(00)00452-X
Foster K.A., Avery M.L., Yazdanian M., Audus K.L.
Characterization of the Calu-3 cell line as a tool to screen pulmonary drug delivery.
Int. J. Pharm. 208:1-11(2000)
PubMed=15463957; DOI=10.1016/j.jcf.2004.05.040
Gruenert D.C., Willems M., Cassiman J.-J., Frizzell R.A.
Established cell lines used in cystic fibrosis research.
J. Cyst. Fibros. 3:191-196(2004)
PubMed=17483357; DOI=10.1158/0008-5472.CAN-06-4495
Tooker P., Yen W.-C., Ng S.-C., Negro-Vilar A., Hermann T.W.
Bexarotene (LGD1069, Targretin), a selective retinoid X receptor agonist, prevents and reverses gemcitabine resistance in NSCLC cells by modulating gene amplification.
Cancer Res. 67:4425-4433(2007)
PubMed=18083107; DOI=10.1016/j.cell.2007.11.025
Rikova K., Guo A.-L., Zeng Q.-F., Possemato A., Yu J., Haack H., Nardone J., Lee K., Reeves C., Li Y., Hu Y.-R., Tan Z.-P., Stokes M.P., Sullivan L., Mitchell J., Wetzel R., MacNeill J., Ren J.-M., Yuan J., Bakalarski C.E., Villen J., Kornhauser J.M., Smith B., Li D.-Q., Zhou X.-M., Gygi S.P., Gu T.-L., Polakiewicz R.D., Rush J., Comb M.J.
Global survey of phosphotyrosine signaling identifies oncogenic kinases in lung cancer.
Cell 131:1190-1203(2007)
PubMed=19153074; DOI=10.1093/hmg/ddp034
Medina P.P., Castillo S.D., Blanco S., Sanz-Garcia M., Largo C., Alvarez S., Yokota J., Gonzalez-Neira A., Benitez J., Clevers H.C., Cigudosa J.C., Lazo P.A., Sanchez-Cespedes M.
The SRY-HMG box gene, SOX4, is a target of gene amplification at chromosome 6p in lung cancer.
Hum. Mol. Genet. 18:1343-1352(2009)
PubMed=19472407; DOI=10.1002/humu.21028; PMCID=PMC2900846
Blanco R., Iwakawa R., Tang M.-Y., Kohno T., Angulo B., Pio R., Montuenga L.M., Minna J.D., Yokota J., Sanchez-Cespedes M.
A gene-alteration profile of human lung cancer cell lines.
Hum. Mutat. 30:1199-1206(2009)
PubMed=20090954; DOI=10.1371/journal.pone.0008729; PMCID=PMC2806919
Yoshikawa T., Hill T.E., Yoshikawa N., Popov V.L., Galindo C.L., Garner H.R., Peters C.J., Tseng C.-T.
Dynamic innate immune responses of human bronchial epithelial cells to severe acute respiratory syndrome-associated coronavirus infection.
PLoS ONE 5:E8729-E8729(2010)
PubMed=20164919; DOI=10.1038/nature08768; PMCID=PMC3145113
Bignell G.R., Greenman C.D., Davies H.R., Butler A.P., Edkins S., Andrews J.M., Buck G., Chen L., Beare D., Latimer C., Widaa S., Hinton J., Fahey C., Fu B.-Y., Swamy S., Dalgliesh G.L., Teh B.T., Deloukas P., Yang F.-T., Campbell P.J., Futreal P.A., Stratton M.R.
Signatures of mutation and selection in the cancer genome.
Nature 463:893-898(2010)
PubMed=20215515; DOI=10.1158/0008-5472.CAN-09-3458; PMCID=PMC2881662
Rothenberg S.M., Mohapatra G., Rivera M.N., Winokur D., Greninger P., Nitta M., Sadow P.M., Sooriyakumar G., Brannigan B.W., Ulman M.J., Perera R.M., Wang R., Tam A., Ma X.-J., Erlander M., Sgroi D.C., Rocco J.W., Lingen M.W., Cohen E.E.W., Louis D.N., Settleman J., Haber D.A.
A genome-wide screen for microdeletions reveals disruption of polarity complex genes in diverse human cancers.
Cancer Res. 70:2158-2164(2010)
PubMed=20557307; DOI=10.1111/j.1349-7006.2010.01622.x; PMCID=PMC11158680
Iwakawa R., Kohno T., Enari M., Kiyono T., Yokota J.
Prevalence of human papillomavirus 16/18/33 infection and p53 mutation in lung adenocarcinoma.
Cancer Sci. 101:1891-1896(2010)
PubMed=22460905; DOI=10.1038/nature11003; PMCID=PMC3320027
Barretina J.G., Caponigro G., Stransky N., Venkatesan K., Margolin A.A., Kim S., Wilson C.J., Lehar J., Kryukov G.V., Sonkin D., Reddy A., Liu M., Murray L., Berger M.F., Monahan J.E., Morais P., Meltzer J., Korejwa A., Jane-Valbuena J., Mapa F.A., Thibault J., Bric-Furlong E., Raman P., Shipway A., Engels I.H., Cheng J., Yu G.-Y.K., Yu J.-J., Aspesi P. Jr., de Silva M., Jagtap K., Jones M.D., Wang L., Hatton C., Palescandolo E., Gupta S., Mahan S., Sougnez C., Onofrio R.C., Liefeld T., MacConaill L.E., Winckler W., Reich M., Li N.-X., Mesirov J.P., Gabriel S.B., Getz G., Ardlie K., Chan V., Myer V.E., Weber B.L., Porter J., Warmuth M., Finan P., Harris J.L., Meyerson M.L., Golub T.R., Morrissey M.P., Sellers W.R., Schlegel R., Garraway L.A.
The Cancer Cell Line Encyclopedia enables predictive modelling of anticancer drug sensitivity.
Nature 483:603-607(2012)
PubMed=22961666; DOI=10.1158/2159-8290.CD-12-0112; PMCID=PMC3567922
Byers L.A., Wang J., Nilsson M.B., Fujimoto J., Saintigny P., Yordy J.S., Giri U., Peyton M., Fan Y.-H., Diao L.-X., Masrorpour F., Shen L., Liu W.-B., Duchemann B., Tumula P., Bhardwaj V., Welsh J., Weber S., Glisson B.S., Kalhor N., Wistuba I.I., Girard L., Lippman S.M., Mills G.B., Coombes K.R., Weinstein J.N., Minna J.D., Heymach J.V.
Proteomic profiling identifies dysregulated pathways in small cell lung cancer and novel therapeutic targets including PARP1.
Cancer Discov. 2:798-811(2012)
PubMed=24207061; DOI=10.1186/1559-0275-10-16; PMCID=PMC3827840
Cerciello F., Choi M., Nicastri A., Bausch-Fluck D., Ziegler A., Vitek O., Felley-Bosco E., Stahel R.A., Aebersold R., Wollscheid B.
Identification of a seven glycopeptide signature for malignant pleural mesothelioma in human serum by selected reaction monitoring.
Clin. Proteomics 10:16.1-16.12(2013)
PubMed=25485619; DOI=10.1038/nbt.3080
Klijn C., Durinck S., Stawiski E.W., Haverty P.M., Jiang Z.-S., Liu H.-B., Degenhardt J., Mayba O., Gnad F., Liu J.-F., Pau G., Reeder J., Cao Y., Mukhyala K., Selvaraj S.K., Yu M.-M., Zynda G.J., Brauer M.J., Wu T.D., Gentleman R.C., Manning G., Yauch R.L., Bourgon R., Stokoe D., Modrusan Z., Neve R.M., de Sauvage F.J., Settleman J., Seshagiri S., Zhang Z.-M.
A comprehensive transcriptional portrait of human cancer cell lines.
Nat. Biotechnol. 33:306-312(2015)
PubMed=25555374; DOI=10.1016/j.ejps.2014.12.017
Kreft M.E., Dragin Jerman U., Lasic E., Hevir-Kene N., Lanisnik Rizner T., Peternel L., Kristan K.
The characterization of the human cell line Calu-3 under different culture conditions and its use as an optimized in vitro model to investigate bronchial epithelial function.
Eur. J. Pharm. Sci. 69:1-9(2015)
PubMed=25877200; DOI=10.1038/nature14397
Yu M., Selvaraj S.K., Liang-Chu M.M.Y., Aghajani S., Busse M., Yuan J., Lee G., Peale F.V., Klijn C., Bourgon R., Kaminker J.S., Neve R.M.
A resource for cell line authentication, annotation and quality control.
Nature 520:307-311(2015)
PubMed=25894527; DOI=10.1371/journal.pone.0121314; PMCID=PMC4404347
Bausch-Fluck D., Hofmann A., Bock T., Frei A.P., Cerciello F., Jacobs A., Moest H., Omasits U., Gundry R.L., Yoon C., Schiess R., Schmidt A., Mirkowska P., Hartlova A.S., Van Eyk J.E., Bourquin J.-P., Aebersold R., Boheler K.R., Zandstra P.W., Wollscheid B.
A mass spectrometric-derived cell surface protein atlas.
PLoS ONE 10:E0121314-E0121314(2015)
PubMed=26589293; DOI=10.1186/s13073-015-0240-5; PMCID=PMC4653878
Scholtalbers J., Boegel S., Bukur T., Byl M., Goerges S., Sorn P., Loewer M., Sahin U., Castle J.C.
TCLP: an online cancer cell line catalogue integrating HLA type, predicted neo-epitopes, virus and gene expression.
Genome Med. 7:118.1-118.7(2015)
PubMed=27397505; DOI=10.1016/j.cell.2016.06.017; PMCID=PMC4967469
Iorio F., Knijnenburg T.A., Vis D.J., Bignell G.R., Menden M.P., Schubert M., Aben N., Goncalves E., Barthorpe S., Lightfoot H., Cokelaer T., Greninger P., van Dyk E., Chang H., de Silva H., Heyn H., Deng X.-M., Egan R.K., Liu Q.-S., Miroo T., Mitropoulos X., Richardson L., Wang J.-H., Zhang T.-H., Moran S., Sayols S., Soleimani M., Tamborero D., Lopez-Bigas N., Ross-Macdonald P., Esteller M., Gray N.S., Haber D.A., Stratton M.R., Benes C.H., Wessels L.F.A., Saez-Rodriguez J., McDermott U., Garnett M.J.
A landscape of pharmacogenomic interactions in cancer.
Cell 166:740-754(2016)
PubMed=28196595; DOI=10.1016/j.ccell.2017.01.005; PMCID=PMC5501076
Li J., Zhao W., Akbani R., Liu W.-B., Ju Z.-L., Ling S.-Y., Vellano C.P., Roebuck P., Yu Q.-H., Eterovic A.K., Byers L.A., Davies M.A., Deng W.-L., Gopal Y.N.V., Chen G., von Euw E.M., Slamon D.J., Conklin D., Heymach J.V., Gazdar A.F., Minna J.D., Myers J.N., Lu Y.-L., Mills G.B., Liang H.
Characterization of human cancer cell lines by reverse-phase protein arrays.
Cancer Cell 31:225-239(2017)
PubMed=29681454; DOI=10.1016/j.cell.2018.03.028; PMCID=PMC5935540
McMillan E.A., Ryu M.-J., Diep C.H., Mendiratta S., Clemenceau J.R., Vaden R.M., Kim J.-H., Motoyaji T., Covington K.R., Peyton M., Huffman K., Wu X.-F., Girard L., Sung Y., Chen P.-H., Mallipeddi P.L., Lee J.Y., Hanson J., Voruganti S., Yu Y., Park S., Sudderth J., DeSevo C., Muzny D.M., Doddapaneni H., Gazdar A.F., Gibbs R.A., Hwang T.H., Heymach J.V., Wistuba I.I., Coombes K.R., Williams N.S., Wheeler D.A., MacMillan J.B., DeBerardinis R.J., Roth M.G., Posner B.A., Minna J.D., Kim H.S., White M.A.
Chemistry-first approach for nomination of personalized treatment in lung cancer.
Cell 173:864-878.e29(2018)
PubMed=30894373; DOI=10.1158/0008-5472.CAN-18-2747; PMCID=PMC6445675
Dutil J., Chen Z.-H., Monteiro A.N.A., Teer J.K., Eschrich S.A.
An interactive resource to probe genetic diversity and estimated ancestry in cancer cell lines.
Cancer Res. 79:1263-1273(2019)
PubMed=31068700; DOI=10.1038/s41586-019-1186-3; PMCID=PMC6697103
Ghandi M., Huang F.W., Jane-Valbuena J., Kryukov G.V., Lo C.C., McDonald E.R. 3rd, Barretina J.G., Gelfand E.T., Bielski C.M., Li H.-X., Hu K., Andreev-Drakhlin A.Y., Kim J., Hess J.M., Haas B.J., Aguet F., Weir B.A., Rothberg M.V., Paolella B.R., Lawrence M.S., Akbani R., Lu Y.-L., Tiv H.L., Gokhale P.C., de Weck A., Mansour A.A., Oh C., Shih J., Hadi K., Rosen Y., Bistline J., Venkatesan K., Reddy A., Sonkin D., Liu M., Lehar J., Korn J.M., Porter D.A., Jones M.D., Golji J., Caponigro G., Taylor J.E., Dunning C.M., Creech A.L., Warren A.C., McFarland J.M., Zamanighomi M., Kauffmann A., Stransky N., Imielinski M., Maruvka Y.E., Cherniack A.D., Tsherniak A., Vazquez F., Jaffe J.D., Lane A.A., Weinstock D.M., Johannessen C.M., Morrissey M.P., Stegmeier F., Schlegel R., Hahn W.C., Getz G., Mills G.B., Boehm J.S., Golub T.R., Garraway L.A., Sellers W.R.
Next-generation characterization of the Cancer Cell Line Encyclopedia.
Nature 569:503-508(2019)"