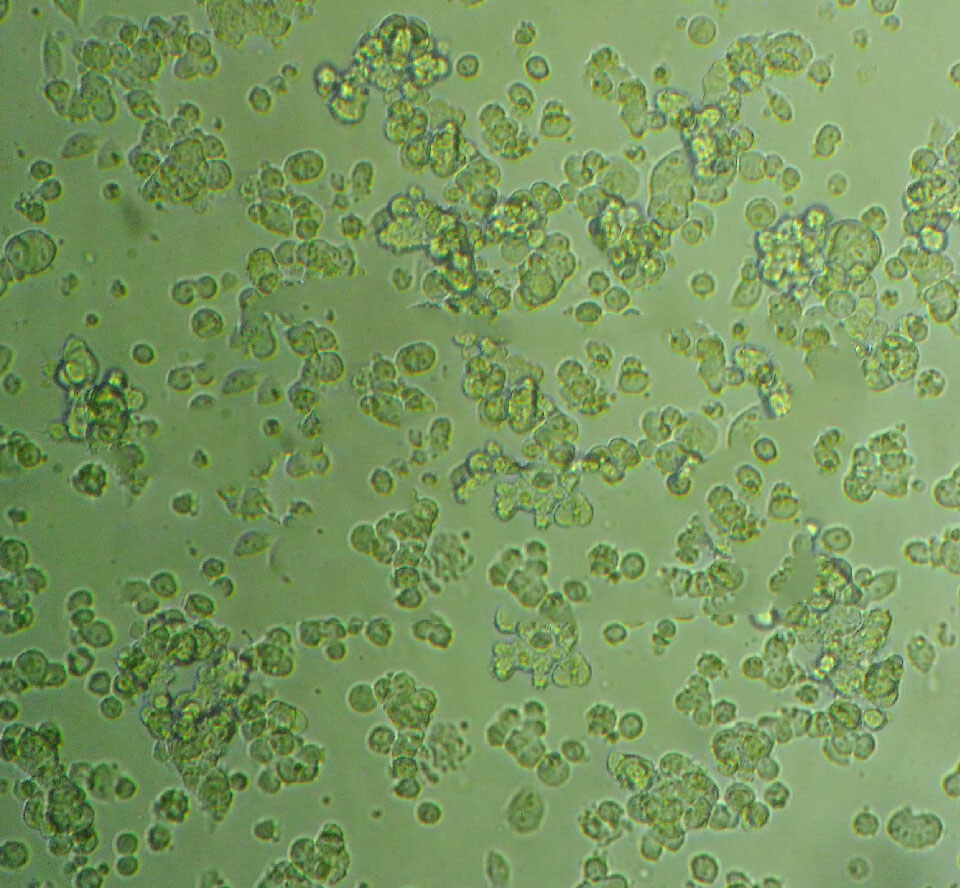
"THP-1人单核细胞白血病细胞全年复苏|已有STR图谱
传代比例:1:2-1:4(首次传代建议1:2)
生长特性:悬浮生长
公司细胞系形态漂亮、增殖倍数高、纯度高、功能性强,细胞培养就跟养孩子一个样。养孩子要喂奶,养细胞要加补液,都需要在前期补充足够的营养,初始状态的细胞或刚刚复苏的细胞还要适量加入血清或细胞因子来帮助它们的存活增殖,如果营养物质缺乏,细胞就会不生长甚至死亡。养孩子要从小培养学习,养细胞也得培养宝宝顺利生下来,你会经常抚摸他,给他看各种颜色,刺激他的五感。细胞也是一样,分离后的细胞需要使用特定的细胞因子进行活化、增殖。另外加入因子的种类、因子的浓度、加入时间、加入顺序都会影响细胞最终的结果。养孩子最怕孩子生病,养细胞最怕被污染,平时你会仔细观察宝宝是否呕吐、是否突然哭闹,猜测宝宝是否生病了。对于细胞,我们也需要时刻进行观察的,假如培养液浑浊(污染了),则需要换液后加抗生素;假如细胞增殖不明显,形态变差,则可能是因为营养不足了,对贴壁细胞可以消化后重新用新的培养基接种并加倍加入细胞因子含量;对悬浮细胞增殖能力不强的,则不着急补液,只是先补加血清、细胞因子看是否可以好转。培养时还得全程在无菌的环境,一个小小的偏差,细胞就会死亡。
换液周期:每周2-3次
MDA-MB-436 Cells;背景说明:该细胞源于一名43岁患有乳腺腺癌女性的胸腔积液。;传代方法:1:2传代,每周换液2—3次;生长特性:贴壁生长;形态特性:多角形;相关产品有:CCRF/CEM/0细胞、MRASMC细胞、SCC090细胞
BC-028 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:FHC细胞、H446细胞、IAR20细胞
PIEC Cells;背景说明:髋动脉;内皮 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SK-SH-SY5Y细胞、GC-1 spg细胞、WiDr-TC细胞
背景信息:该细胞从一名1岁的患有急性单核细胞性白血病的男孩的外周血中分离建立。该细胞可以吞噬乳胶颗粒和激活的红细胞,细胞膜和胞浆内均没有免疫球蛋白,表达C3R和FcR;可受佛波酯TPA诱导向单核系方向分化;可作为转染宿主。
THP-1人单核细胞白血病细胞全年复苏|已有STR图谱
产品包装:复苏发货:T25培养瓶(一瓶)或冻存发货:1ml冻存管(两支)
DSMZ菌株保藏中心成立于1969年,是德国的国家菌种保藏中心。该中心一直致力于细菌、真菌、质粒、抗菌素、人体和动物细胞、植物病毒等的分类、鉴定和保藏工作。DSMZ菌种保藏中心是欧洲规模最大的生物资源中心,保藏有动物细胞500多株。Riken BRC成立于1920年,是英国的国家菌种保藏中心。该中心一直致力于细菌、真菌、植物病毒等的分类、鉴定和保藏工作。日本Riken BRC(Riken生物资源保藏中心)是全球三大典型培养物收集中心之一。Riken保藏中心提供了很多细胞系。在世界范围内,这些细胞系,都在医学、科学和兽医中具有重要意义。Riken生物资源中心支持了各种学术、健康、食品和兽医机构的研究工作,并在世界各地不同组织的微生物实验室和研究机构中使用。
Malme-3 M Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代,2天换液1次。;生长特性:混合生长;形态特性:成纤维细胞;相关产品有:KNS-62细胞、NS1-Ag 4/1细胞、SRS-82细胞
TE671 Cells;背景说明:胚胎性横纹肌肉瘤;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:AU-Mel细胞、SK.MEL.28细胞、Y3.AG.1.2.3细胞
NCI-H2085 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:6传代 ;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:L-6细胞、H-7721细胞、HT55细胞
Ba/F3 EGFR-K757R Cells(提供STR鉴定图谱)
来源说明:细胞主要来源ATCC、ECACC、DSMZ、RIKEN等细胞库
物种来源:人源、鼠源等其它物种来源
THP-1人单核细胞白血病细胞全年复苏|已有STR图谱
形态特性:淋巴母细胞样
细胞复苏相关注意事项:1.取细胞的过程中注意带HAO防冻手套,护目镜。此项尤为重要,细胞冻存管可能漏入,解冻时冻存管中的气温急剧上升,可导致爆炸。2.冻存的问题:冻存的配置已是常识,在这里不作详述,但二甲基亚砜(DMSO )对细胞不是完全无毒副作用,在常温下,二甲基亚砜对细胞的毒副作较大,因此,必须在1-2min内使冻存完全融化。如果复苏温度太慢,会造成细胞的损伤,二甲基亚砜(DMSO)ZuiHAO选择进口产品。3.离心前须加入少量培养。细胞解冻后二甲基亚砜浓度较GAO,注意加入少量培养可稀释其浓度,以减少对细胞的损伤。4.离心问题:目前主要有两种见解。一种是解冻后的细胞悬直接吹打均匀后分装到培养瓶中进行培养,第二天换。因为离心的目的是两个,去除DMSO,去除死细胞,这个是标准流程,但对一般人来说,把握不HAO离心转速和时间,转的不够活细胞沉底的少,细胞就全被扔掉了,转过了活细胞会受压过大,死亡。此外在操作过程中容易污染,所以不推荐。另一种说法为细胞悬中含有二甲基亚砜(DMSO),DMSO对细胞有一定的毒副作用,所以须将离心后的体前倒净,且一定倒干净。我在试验中按照常规的离心分装的方法进行复苏,结果无异常。5.细胞贴壁少的问题:教科书中说明冻存细胞解冻时1ml细胞要加10ml-15ml培养,而在我的试验中的经验总结为培养基越少细胞越容易贴附。6.复苏细胞分装的问题:试验中我的经验总结为复苏1管细胞一般可分装到1-2只培养瓶中,分装过多,细胞浓度过低,不利于细胞的贴壁。7.加培养基的量放入问题:这个量的多少的把握主要涉及到的问题DMSO的浓度,从如果你加培养基的太少,那么DMSO的浓度就会比较大,就会影响细胞生长,从以前的资料来看,DMSO的浓度在小于0.5%的时候对一般细胞没有什么影响,还有一个说法是1%。所以如果你的冻存的浓度是10%DMSO的话那么加10ml以上的培养基就恰HAO稀释到了无害浓度。
Ball 1 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:悬浮生长;形态特性:淋巴母细胞;相关产品有:KM-H2细胞、HMEC1细胞、GM03569B细胞
NCI-H661 Cells;背景说明:该细胞1982年建系,源自一位患有大细胞肺癌的男性的胸腔积液。该细胞角蛋白、波形蛋白阳性。;传代方法:1:3—1:5传代,每周换液2—3次;生长特性:贴壁生长;形态特性:上皮样;相关产品有:MDA-MB-231细胞、NCI H295R细胞、RetroPack PT67细胞
Hs940T Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:A549/ATCC细胞、OCI AML5细胞、SGC-996细胞
18G3.cl 1 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SNU-216细胞、NCI H157细胞、SKGIIIA细胞
Hs 611.T Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;每周换液2-3次。;生长特性:混合型;形态特性:淋巴母细胞样;相关产品有:PE/CA-PJ34 (clone C12)细胞、P3/X63-Ag8细胞、HPAF/CD18细胞
Ketr3 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:HRA19细胞、VE细胞、RPMI7666细胞
Colo699 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:H-2330细胞、H-661细胞、HCT116/L细胞
H-498 Cells;背景说明:结肠腺癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:半贴壁;形态特性:详见产品说明书;相关产品有:NHRF细胞、SNU368细胞、COLO 320 DM细胞
Hs 840.T Cells;背景说明:详见相关文献介绍;传代方法:1:4—1:8传代,每周换液2—3次;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:SUIT-2细胞、HCC-2279细胞、Human Liver-7702细胞
Anip 973 Cells;背景说明:肺腺癌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:OE21细胞、CCD-966SK细胞、Co 115细胞
GS-9L Cells;背景说明:胶质瘤;Fischer 344;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:BC-028细胞、Neukoplast细胞、OAW42细胞
MV411 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SCC7细胞、Transformed C3H Mouse Kidney-1细胞、PFSK细胞
WEHI-231 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:NCI-H2170细胞、CCC-HPF-1细胞、SW-900细胞
SUM 52PE Cells;背景说明:乳腺癌;胸腔积液转移;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:OKa-C-1细胞、HT 1376细胞、NCI-H2198细胞
AtT-20 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:H-1436细胞、HConEpic细胞、A-253细胞
hFOB 1.19 Cells;背景说明:成骨细胞;SV40转化;条件永生;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HTR8细胞、MiaPaCa2细胞、THP-1(ATCC)细胞
Detroit 562 Cells;背景说明:器官:咽头 疾病:癌 取材转移灶:胸水;传代方法:1:2-1:4传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:SUDHL6细胞、PaTu 8988s细胞、Hs746T细胞
246G4 Cells(提供STR鉴定图谱)
Abcam HeLa PRKAR2A KO Cells(提供STR鉴定图谱)
AG24310 Cells(提供STR鉴定图谱)
BayGenomics ES cell line RRH309 Cells(提供STR鉴定图谱)
BayGenomics ES cell line XH340 Cells(提供STR鉴定图谱)
C17-S1-D-T984-15 Cells(提供STR鉴定图谱)
D551 iPSC Cells(提供STR鉴定图谱)
Ff-WJs516 Cells(提供STR鉴定图谱)
GM08770 Cells(提供STR鉴定图谱)
VMM-5A Cells;背景说明:黑色素瘤;神经节转移;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:CC-LP-I细胞、AtT20细胞、PL-9细胞
C3H10T1/2 clone8 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:COS-1细胞、MCF10A细胞、NCIH322细胞
MDA-MB-157 Cells;背景说明:该细胞源自一位患有乳腺髓样癌的44岁黑人女性,表达WNT7B癌基因,细胞与细胞边界处有细胞桥粒、微绒毛、张力细丝。;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:A 172细胞、KGN细胞、LOUNH91细胞
hFOB Cells;背景说明:成骨细胞;SV40转化;条件永生;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:H.Ep. No. 2细胞、NCI-446细胞、COV 504细胞
PanC1 Cells;背景说明:这株人胰腺癌细胞株源自于胰腺癌导管细胞,其倍增时间为52小时。染色体研究表明,该细胞染色体众数为63,包括3个独特标记的染色体和1个小环状染色体。该细胞的生长可被1unit/ml的左旋天冬酰胺酶抑制;能在软琼脂上生长;能在裸鼠上成瘤。;传代方法:1:2-1:4传代;每周2-3次。;生长特性:贴壁生长;形态特性:上皮样;多角形;相关产品有:TB1 Lu细胞、OLN-93细胞、M-20细胞
MDA-MB-134 VI Cells;背景说明:该细胞1973年由R. Cailleau建系,源自74岁乳腺导管癌女性患者的胸腔积液,细胞生长缓慢,松散贴壁,生长过程中会脱落到培养基,不会汇合,过表达FGF受体;传代方法:1:2—1:4传代,每周换液2—3次;生长特性:松散贴壁生长;形态特性:上皮细胞样;相关产品有:G292细胞、Centre Antoine Lacassagne-33细胞、Plaepi 34细胞
Hs 729T Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:MDA175细胞、3T3-F442A细胞、SW1463细胞
RPMI8226 Cells;背景说明:来源于一位61岁的男性浆细胞瘤患者;可产生免疫球蛋白轻链,未检测到重链。;传代方法:按1:2传代,5-6小时可以看到细胞分裂;生长特性:悬浮生长;形态特性:淋巴母细胞样;相关产品有:TERT-RPE1细胞、PLA801-95C细胞、LIPF178C细胞
THP-1人单核细胞白血病细胞全年复苏|已有STR图谱
A2780CP Cells;背景说明:卵巢癌;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SNK6细胞、HRIF细胞、H508细胞
Hs 683 Cells;背景说明:该细胞源自76岁白人男性的左颞叶侧胶质瘤组织,有微绒毛,无桥粒。 ;传代方法:1:4传代,每周换液2次;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:RDES细胞、Hs606细胞、HuH-6细胞
SN12CPM6 Cells;背景说明:肾癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SV40-HCEC细胞、COLO 320HSR细胞、Hs-274-T细胞
BEL-7404 Cells;背景说明:用Northernblot方法,未能检测到细胞中1.3kbLFIRE-1/HFREP-1mRNA的表达。;传代方法:消化3-5分钟。1:2。3天内可长满。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:CO115细胞、RPMI.8226细胞、High5细胞
OCI/AML3 Cells;背景说明:急性髓系白血病;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:hRMECs细胞、Fetal Bovine Heart Endothelial细胞、PC.3细胞
AZ521 Cells;背景说明:详见相关文献介绍;传代方法:1:4传代;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:上皮样;相关产品有:3T6 Swiss Albino细胞、X63Ag8-653细胞、Uhth-74细胞
SW962 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:6传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:混合;相关产品有:A375.S2细胞、HTR-8/SVneo细胞、3T6-Swiss albino细胞
GN00045 Cells(提供STR鉴定图谱)
HAP1 PKN3 (-) 2 Cells(提供STR鉴定图谱)
P3-X63-Ag 8.653 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:NCIH1618细胞、NBLS细胞、TGW细胞
NCIH1618 Cells;背景说明:详见相关文献介绍;传代方法:3-4天换液1次。;生长特性:悬浮生长;形态特性:详见产品说明书;相关产品有:CFSC-2G细胞、LAN1细胞、KP-N-YN细胞
HA Cells;背景说明:详见相关文献介绍;传代方法:消化3-5分钟,1:2,3天内可长满;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:HOS/MNNG细胞、UCW 100细胞、SCC VII细胞
Ramos Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:CAL51细胞、PC-9细胞、C32 mel细胞
H341 Cells;背景说明:详见相关文献介绍;传代方法:每周换液2-3次。;生长特性:悬浮生长;形态特性:髓母细胞样;相关产品有:MTEC1细胞、Radiation Effects Research Foundation-Lung Cancer-MS细胞、MDAMB435细胞
H1666_DA Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代;每周换液2次。;生长特性:贴壁生长,松散;形态特性:上皮细胞;相关产品有:RK13细胞、NCI-SNU-387细胞、ARO细胞
SU.86.86 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:D6P2T细胞、U031细胞、IMR90细胞
C166 Cells;背景说明:血管内皮;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:MD Anderson-Metastatic Breast-175-VIII细胞、NCI-SNU-601细胞、NCI-H847细胞
HT-1 [Human lymphoma] Cells(提供STR鉴定图谱)
KPB-M15 Cells(提供STR鉴定图谱)
MP 4112 Cells(提供STR鉴定图谱)
NYSCF-10005-882-882-Skin-mR-iPSC Cells(提供STR鉴定图谱)
rh-r.5 Cells(提供STR鉴定图谱)
Ubigene HCT 116 GSKIP KO Cells(提供STR鉴定图谱)
W3UF Cells(提供STR鉴定图谱)
HG01768 Cells(提供STR鉴定图谱)
BLO11 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:H508细胞、H522细胞、C918细胞
MDA-435 Cells;背景说明:乳腺癌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:GA-10 (Clone 4)细胞、SK-RC-20细胞、F-36P细胞
Opossum Kidney Cells;背景说明:肾;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SK RC 52细胞、Stanford University-Diffuse Histiocytic Lymphoma-1细胞、NHA细胞
PL45 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:4T1细胞、NHDF细胞、Centre Antoine Lacassagne-12T细胞
T 24 Cells;背景说明:该细胞源自一位81岁白人女性患者的膀胱移行细胞癌组织;来源于移行细胞癌病人的白血病和血浆对T24和相关细胞株有细胞毒性;倍增时间为19小时;含ras(H-ras)癌基因,表达肿瘤特有抗原。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:MDA-MB415细胞、ECC 10细胞、SUNE1细胞
207 Cells;背景说明:儿童急性髓系白血病;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:CHOS细胞、Panc-03.27细胞、HEC1-A细胞
HEK 293 c18 Cells;背景说明:详见相关文献介绍;传代方法:1:4-1:10传代;每周2次。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:HBEpiC细胞、OVCAR 420细胞、Ontario Cancer Institute-Acute Myeloid Leukemia-2细胞
Hs 343.T Cells;背景说明:详见相关文献介绍;传代方法:1:2—1:3传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:TN5B14细胞、HKC细胞、V79-1细胞
HLEB-3 Cells;背景说明:晶状体;Ad12-SV40转化;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:MM1细胞、Ramos-2G6-4C10细胞、U266B1细胞
UACC893 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:H-841细胞、HEK-293FT细胞、CCRF-CEM/S细胞
1E8-H Cells;背景说明:前列腺癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:RPMI 7666细胞、RBSMC细胞、LNCaP细胞
1E8-H Cells;背景说明:前列腺癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:RPMI 7666细胞、RBSMC细胞、LNCaP细胞
Psi-2 DAP Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:HFT 8810细胞、SJRH 30细胞、HCC1954 BL细胞
NCIH292 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:8传代;2-3天换液1次。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:HS 683T细胞、Beta-TC-6细胞、BRL细胞
BRL Cells;背景说明:详见相关文献介绍;传代方法:消化3-5分钟。1:2。3天内可长满。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:HEK293细胞、LAD 2细胞、Hs 445细胞
Super-CHO C1 Cells(提供STR鉴定图谱)
OCIAML5 Cells;背景说明:急性髓系白血病细胞;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:Leukemia 1210细胞、HS-294细胞、HEL-92-1-7细胞
U-87 MG Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:LAC细胞、L-6TG细胞、ST 486细胞
MDA-MB-435S Cells;背景说明:MDA-MB-435S是一种纺锤形的细胞,1976年由其亲本(435)中筛选得到。435是从31岁的转移性乳腺导管腺癌女性患者胸水中分离得到。当用荧光染料对微管蛋白进行染色时亲本细胞显现散布特征(II型)。最近通过cDNA阵列研究表明,亲本(MDA-MB-435)可归入黑素瘤起源。;传代方法:消化3-5分钟,1:2,3天内可长满;生长特性:贴壁生长;形态特性:纺锤形;相关产品有:Hs_578t细胞、EoL-1 cell细胞、G402细胞
786O Cells;背景说明:该细胞源自一位原发性肾透明细胞癌患者。该细胞有微绒毛和桥粒,能在软琼脂上生长。此细胞生成一种PTH(甲状旁腺素)样的多肽,与乳癌和肺癌中生成的肽相似,其N端序列与PTH相似,具有PTH样活性,分子量为6000D。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:OCI-Ly 1细胞、NCI/ADR-RES细胞、NCI-H441-4细胞
HANK Cells;背景说明:NK/T细胞淋巴瘤;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:BJAB-1细胞、HCT/FU细胞、SUP-B1细胞
CAL 148 Cells;背景说明:乳腺癌;胸腔积液转移;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:TPC-1细胞、SNK-1细胞、HRA-19细胞
GM01232E Cells;背景说明:1971年1月,该细胞由ReidTW及其同事从病人右眼切除的肿瘤进行原代培养建立而成,此病人有很强的视网膜母细胞瘤的母系家族遗传性。该细胞的超微结构,如核膜内折、三层膜结构、大的被膜小泡、环孔板、微管、中心粒、基粒等都与原始肿瘤相似。;传代方法:1:2传代;生长特性:悬浮生长;形态特性:圆形,成簇生长;相关产品有:P3.times.63 Ag8.653细胞、CATH.a细胞、RS 4;11细胞
H-661 Cells;背景说明:该细胞1982年建系,源自一位患有大细胞肺癌的男性的胸腔积液。该细胞角蛋白、波形蛋白阳性。;传代方法:1:3—1:5传代,每周换液2—3次;生长特性:贴壁生长;形态特性:上皮样;相关产品有:PCI-4M细胞、MKN7细胞、HCC1359细胞
THP-1人单核细胞白血病细胞全年复苏|已有STR图谱
A-375 Cells;背景说明:A375源自一位54岁女性,是Giard DJ等人建立的一系列细胞株中的一株。该细胞可在免疫抑制小鼠上成瘤,在琼脂上形成克隆。;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:上皮细胞样;相关产品有:H647ell细胞、A.704细胞、Hs683T细胞
MOLM-14 Cells;背景说明:急性髓系白血病;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:C-643细胞、H-292细胞、3LL细胞
U251n Cells;背景说明:U-251 MG分离至一位患者的胶质母细胞瘤组织。;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:成纤维细胞样;相关产品有:IM-9细胞、H1048细胞、H22-H8D8细胞
FDC-P1 Cells;背景说明:详见相关文献介绍;传代方法:2-3天换液1次;生长特性:悬浮生长;形态特性:淋巴母细胞;相关产品有:CMT-93细胞、NCI-H740细胞、KM-H2细胞
HCE-T Cells;背景说明:角膜上皮细胞;Ad-SV40转化;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:NE-1细胞、MDCK-2细胞、Caov-3细胞
CL 1-5 Cells;背景说明:肺腺癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:BTI-Tn-5B1-4细胞、LuCL4细胞、OVCAR5细胞
BayGenomics ES cell line RRR693 Cells(提供STR鉴定图谱)
BayGenomics ES cell line YTA150 Cells(提供STR鉴定图谱)
I1-Hybridoma Cells(提供STR鉴定图谱)
PCRP-MEF2C-1D4 Cells(提供STR鉴定图谱)
HBZY-1 Cells(提供STR鉴定图谱)
HPSI0316i-xaqm_6 Cells(提供STR鉴定图谱)
" "PubMed=2985879; DOI=10.1016/0145-2126(85)90084-0
Drexler H.G., Gaedicke G., Minowada J.
Isoenzyme studies in human leukemia-lymphoma cell lines -- 1 carboxylic esterase.
Leuk. Res. 9:209-229(1985)
PubMed=3159941; DOI=10.1016/0145-2126(85)90134-1
Drexler H.G., Gaedicke G., Minowada J.
Isoenzyme studies in human leukemia-lymphoma cell lines -- III Beta-hexosaminidase (E.C. 3.2.1.30).
Leuk. Res. 9:549-559(1985)
PubMed=3874327; DOI=10.1016/0145-2126(85)90133-x
Drexler H.G., Gaedicke G., Minowada J.
Isoenzyme studies in human leukemia-lymphoma cells lines -- II. Acid phosphatase.
Leuk. Res. 9:537-548(1985)
PubMed=2633408; DOI=10.1620/tjem.159.299
Saijo Y., Kumano N., Tokue Y., Satoh K., Oizumi K., Motomiya M.
Characterization of resistance to VP-16 in human leukemic cell line.
Tohoku J. Exp. Med. 159:299-306(1989)
PubMed=1915666; DOI=10.1016/0014-4827(91)90482-A
Limouse M., Manie S., Konstantinova I., Ferrua B., Schaffar L.
Inhibition of phorbol ester-induced cell activation in microgravity.
Exp. Cell Res. 197:82-86(1991)
PubMed=1571549; DOI=10.1182/blood.V79.9.2378.2378
Sugimoto K., Toyoshima H., Sakai R., Miyagawa K., Hagiwara K., Ishikawa F., Takaku F., Yazaki Y., Hirai H.
Frequent mutations in the p53 gene in human myeloid leukemia cell lines.
Blood 79:2378-2383(1992)
PubMed=8558913
Morita S., Tsuchiya S., Fujie H., Itano M., Ohashi Y., Minegishi M., Imaizumi M., Endo M., Takano N., Konno T.
Cell surface c-kit receptors in human leukemia cell lines and pediatric leukemia: selective preservation of c-kit expression on megakaryoblastic cell lines during adaptation to in vitro culture.
Leukemia 10:102-105(1996)
PubMed=9290701; DOI=10.1002/(SICI)1098-2744(199708)19:4<243::aid-mc5>3.0.CO;2-D
Jia L.-Q., Osada M., Ishioka C., Gamo M., Ikawa S., Suzuki T., Shimodaira H., Niitani T., Kudo T., Akiyama M., Kimura N., Matsuo M., Mizusawa H., Tanaka N., Koyama H., Namba M., Kanamaru R., Kuroki T.
Screening the p53 status of human cell lines using a yeast functional assay.
Mol. Carcinog. 19:243-253(1997)
PubMed=9379676; DOI=10.1016/S0145-2126(97)00036-2
Sheng X.-M., Kawamura M., Ohnishi H., Ida K., Hanada R., Kojima S., Kobayashi M., Bessho F., Yanagisawa M., Hayashi Y.
Mutations of the RAS genes in childhood acute myeloid leukemia, myelodysplastic syndrome and juvenile chronic myelocytic leukemia.
Leuk. Res. 21:697-701(1997)
PubMed=9510473; DOI=10.1111/j.1349-7006.1998.tb00476.x; PMCID=PMC5921588
Hosoya N., Hangaishi A., Ogawa S., Miyagawa K., Mitani K., Yazaki Y., Hirai H.
Frameshift mutations of the hMSH6 gene in human leukemia cell lines.
Jpn. J. Cancer Res. 89:33-39(1998)
PubMed=9738977; DOI=10.1111/j.1349-7006.1998.tb03275.x; PMCID=PMC5921886
Takizawa J., Suzuki R., Kuroda H., Utsunomiya A., Kagami Y., Joh T., Aizawa Y., Ueda R., Seto M.
Expression of the TCL1 gene at 14q32 in B-cell malignancies but not in adult T-cell leukemia.
Jpn. J. Cancer Res. 89:712-718(1998)
PubMed=10223614; DOI=10.1620/tjem.186.99
Tominaga T., Suzuki M., Saeki H., Matsuno S., Tachibana T., Kudo T.
Establishment of an activated macrophage cell line, A-THP-1, and its properties.
Tohoku J. Exp. Med. 186:99-119(1998)
PubMed=10739008; DOI=10.1016/S0145-2126(99)00182-4
Inoue K., Kohno T., Takakura S., Hayashi Y., Mizoguchi H., Yokota J.
Frequent microsatellite instability and BAX mutations in T cell acute lymphoblastic leukemia cell lines.
Leuk. Res. 24:255-262(2000)
PubMed=11066077; DOI=10.1002/1098-2264(2000)9999:9999<::aid-gcc1040>3.0.CO;2-Z
Odero M.D., Zeleznik-Le N.J., Chinwalla V., Rowley J.D.
Cytogenetic and molecular analysis of the acute monocytic leukemia cell line THP-1 with an MLL-AF9 translocation.
Genes Chromosomes Cancer 29:333-338(2000)
DOI=10.1016/B978-0-12-221970-2.50457-5
Drexler H.G.
The leukemia-lymphoma cell line factsbook.
(In book) ISBN 9780122219702; pp.1-733; Academic Press; London; United Kingdom (2001)
PubMed=11226526; DOI=10.1016/S0145-2126(00)00121-1
Inoue K., Kohno T., Takakura S., Hayashi Y., Mizoguchi H., Yokota J.
Corrigendum to: Frequent microsatellite instability and BAX mutations in T cell acute lymphoblastic leukemia cell lines Leukemia Research 24 (2000), 255-262.
Leuk. Res. 25:275-278(2001)
PubMed=11414198; DOI=10.1007/s004320000207
Lahm H., Andre S., Hoeflich A., Fischer J.R., Sordat B., Kaltner H., Wolf E., Gabius H.-J.
Comprehensive galectin fingerprinting in a panel of 61 human tumor cell lines by RT-PCR and its implications for diagnostic and therapeutic procedures.
J. Cancer Res. Clin. Oncol. 127:375-386(2001)
PubMed=11416159; DOI=10.1073/pnas.121616198; PMCID=PMC35459
Masters J.R.W., Thomson J.A., Daly-Burns B., Reid Y.A., Dirks W.G., Packer P., Toji L.H., Ohno T., Tanabe H., Arlett C.F., Kelland L.R., Harrison M., Virmani A.K., Ward T.H., Ayres K.L., Debenham P.G.
Short tandem repeat profiling provides an international reference standard for human cell lines.
Proc. Natl. Acad. Sci. U.S.A. 98:8012-8017(2001)
PubMed=12068308; DOI=10.1038/nature00766
Davies H.R., Bignell G.R., Cox C., Stephens P.J., Edkins S., Clegg S., Teague J.W., Woffendin H., Garnett M.J., Bottomley W., Davis N., Dicks E., Ewing R., Floyd Y., Gray K., Hall S., Hawes R., Hughes J., Kosmidou V., Menzies A., Mould C., Parker A., Stevens C., Watt S., Hooper S., Wilson R., Jayatilake H., Gusterson B.A., Cooper C.S., Shipley J.M., Hargrave D., Pritchard-Jones K., Maitland N.J., Chenevix-Trench G., Riggins G.J., Bigner D.D., Palmieri G., Cossu A., Flanagan A.M., Nicholson A., Ho J.W.C., Leung S.Y., Yuen S.T., Weber B.L., Seigler H.F., Darrow T.L., Paterson H.F., Marais R., Marshall C.J., Wooster R., Stratton M.R., Futreal P.A.
Mutations of the BRAF gene in human cancer.
Nature 417:949-954(2002)
PubMed=14504097; DOI=10.1182/blood-2003-02-0418
Taketani T., Taki T., Sugita K., Furuichi Y., Ishii E., Hanada R., Tsuchida M., Sugita K., Ida K., Hayashi Y.
FLT3 mutations in the activation loop of tyrosine kinase domain are frequently found in infant ALL with MLL rearrangements and pediatric ALL with hyperdiploidy.
Blood 103:1085-1088(2004)
PubMed=14671638; DOI=10.1038/sj.leu.2403236
Drexler H.G., Quentmeier H., MacLeod R.A.F.
Malignant hematopoietic cell lines: in vitro models for the study of MLL gene alterations.
Leukemia 18:227-232(2004)
PubMed=15843827; DOI=10.1038/sj.leu.2403749
Andersson A., Eden P., Lindgren D., Nilsson J., Lassen C., Heldrup J., Fontes M., Borg A., Mitelman F., Johansson B., Hoglund M., Fioretos T.
Gene expression profiling of leukemic cell lines reveals conserved molecular signatures among subtypes with specific genetic aberrations.
Leukemia 19:1042-1050(2005)
PubMed=16311011; DOI=10.1016/j.tiv.2005.10.012
Ashikaga T., Yoshida Y., Hirota M., Yoneyama K., Itagaki H., Sakaguchi H., Miyazawa M., Ito Y., Suzuki H., Toyoda H.
Development of an in vitro skin sensitization test using human cell lines: the human Cell Line Activation Test (h-CLAT). I. Optimization of the h-CLAT protocol.
Toxicol. In Vitro 20:767-773(2006)
PubMed=16337770; DOI=10.1016/j.tiv.2005.10.014
Sakaguchi H., Ashikaga T., Miyazawa M., Yoshida Y., Ito Y., Yoneyama K., Hirota M., Itagaki H., Toyoda H., Suzuki H.
Development of an in vitro skin sensitization test using human cell lines; human Cell Line Activation Test (h-CLAT). II. An inter-laboratory study of the h-CLAT.
Toxicol. In Vitro 20:774-784(2006)
PubMed=16408098; DOI=10.1038/sj.leu.2404081
Quentmeier H., MacLeod R.A.F., Zaborski M., Drexler H.G.
JAK2 V617F tyrosine kinase mutation in cell lines derived from myeloproliferative disorders.
Leukemia 20:471-476(2006)
PubMed=19220422; DOI=10.1111/j.1600-0609.2009.01211.x
Kamihira S., Terada C., Sasaki D., Yanagihara K., Tsukasaki K., Hasegawa H., Yamada Y.
Aberrant p53 protein expression and function in a panel of hematopoietic cell lines with different p53 mutations.
Eur. J. Haematol. 82:301-307(2009)
PubMed=19377474; DOI=10.1038/ng.375; PMCID=PMC6711855
Suzuki H., Forrest A.R.R., van Nimwegen E., Daub C.O., Balwierz P.J., Irvine K.M., Lassmann T., Ravasi T., Hasegawa Y., de Hoon M.J.L., Katayama S., Schroder K., Carninci P., Tomaru Y., Kanamori-Katayama M., Kubosaki A., Akalin A., Ando Y., Arner E., Asada M., Asahara H., Bailey T., Bajic V.B., Bauer D., Beckhouse A.G., Bertin N., Bjorkegren J., Brombacher F., Bulger E., Chalk A.M., Chiba J., Cloonan N., Dawe A., Dostie J., Engstrom P.G., Essack M., Faulkner G.J., Fink J.L., Fredman D., Fujimori K., Furuno M., Gojobori T., Gough J., Grimmond S.M., Gustafsson M., Hashimoto M., Hashimoto T., Hatakeyama M., Heinzel S., Hide W.A., Hofmann O., Hornquist M., Huminiecki L., Ikeo K., Imamoto N., Inoue S., Inoue Y., Ishihara R., Iwayanagi T., Jacobsen A., Kaur M., Kawaji H., Kerr M.C., Kimura R., Kimura S., Kimura Y., Kitano H., Koga H., Kojima T., Kondo S., Konno T., Krogh A., Kruger A., Kumar A., Lenhard B., Lennartsson A., Lindow M., Lizio M., MacPherson C., Maeda N., Maher C.A., Maqungo M., Mar J., Matigian N.A., Matsuda H., Mattick J.S., Meier S., Miyamoto S., Miyamoto-Sato E., Nakabayashi K., Nakachi Y., Nakano M., Nygaard S., Okayama T., Okazaki Y., Okuda-Yabukami H., Orlando V., Otomo J., Pachkov M., Petrovsky N., Plessy C., Quackenbush J., Radovanovic A., Rehli M., Saito R., Sandelin A., Schmeier S., Schonbach C., Schwartz A.S., Semple C.A., Sera M., Severin J., Shirahige K., Simons C., St Laurent G., Suzuki M., Suzuki T., Sweet M.J., Taft R.J., Takeda S., Takenaka Y., Tan K., Taylor M.S., Teasdale R.D., Tegner J., Teichmann S.A., Valen E., Wahlestedt C., Waki K., Waterhouse A., Wells C.A., Winther O., Wu L., Yamaguchi K., Yanagawa H., Yasuda J., Zavolan M., Hume D.A., Arakawa T., Fukuda S., Imamura K., Kai C., Kaiho A., Kawashima T., Kawazu C., Kitazume Y., Kojima M., Miura H., Murakami K., Murata M., Ninomiya N., Nishiyori H., Noma S., Ogawa C., Sano T., Simon C., Tagami M., Takahashi Y., Kawai J., Hayashizaki Y.
FANTOM Consortium
Riken Omics Science Center
The transcriptional network that controls growth arrest and differentiation in a human myeloid leukemia cell line.
Nat. Genet. 41:553-562(2009)
PubMed=20215515; DOI=10.1158/0008-5472.CAN-09-3458; PMCID=PMC2881662
Rothenberg S.M., Mohapatra G., Rivera M.N., Winokur D., Greninger P., Nitta M., Sadow P.M., Sooriyakumar G., Brannigan B.W., Ulman M.J., Perera R.M., Wang R., Tam A., Ma X.-J., Erlander M., Sgroi D.C., Rocco J.W., Lingen M.W., Cohen E.E.W., Louis D.N., Settleman J., Haber D.A.
A genome-wide screen for microdeletions reveals disruption of polarity complex genes in diverse human cancers.
Cancer Res. 70:2158-2164(2010)
PubMed=22645513; DOI=10.3389/fendo.2011.00089; PMCID=PMC3355855
Keuper M., Dzyakanchuk A., Amrein K.E., Wabitsch M., Fischer-Posovszky P.
THP-1 macrophages and SGBS adipocytes -- a new human in vitro model system of inflamed adipose tissue.
Front. Endocrinol. 2:89.1-89.8(2011)
PubMed=22460905; DOI=10.1038/nature11003; PMCID=PMC3320027
Barretina J.G., Caponigro G., Stransky N., Venkatesan K., Margolin A.A., Kim S., Wilson C.J., Lehar J., Kryukov G.V., Sonkin D., Reddy A., Liu M., Murray L., Berger M.F., Monahan J.E., Morais P., Meltzer J., Korejwa A., Jane-Valbuena J., Mapa F.A., Thibault J., Bric-Furlong E., Raman P., Shipway A., Engels I.H., Cheng J., Yu G.-Y.K., Yu J.-J., Aspesi P. Jr., de Silva M., Jagtap K., Jones M.D., Wang L., Hatton C., Palescandolo E., Gupta S., Mahan S., Sougnez C., Onofrio R.C., Liefeld T., MacConaill L.E., Winckler W., Reich M., Li N.-X., Mesirov J.P., Gabriel S.B., Getz G., Ardlie K., Chan V., Myer V.E., Weber B.L., Porter J., Warmuth M., Finan P., Harris J.L., Meyerson M.L., Golub T.R., Morrissey M.P., Sellers W.R., Schlegel R., Garraway L.A.
The Cancer Cell Line Encyclopedia enables predictive modelling of anticancer drug sensitivity.
Nature 483:603-607(2012)
PubMed=22481983; DOI=10.2174/1874091X01206010016; PMCID=PMC3314867
Chauhan V., Howland M., Wilkins R.C.
Effects of alpha-particle radiation on microRNA responses in human cell-lines.
Open Biochem. J. 6:16-22(2012)
PubMed=23097634; DOI=10.1100/2012/205038; PMCID=PMC3477555
Chauhan V., Howland M.
Genomic profiling of a human leukemic monocytic cell-line (THP-1) exposed to alpha particle radiation.
ScientificWorldJournal 2012:205038.1-205038.9(2012)
PubMed=22674354; DOI=10.1002/ijc.27661
Battle R., Poole K., Haywood-Small S., Clark B., Woodroofe M.N.
Molecular characterisation of the monocytic cell line THP-1 demonstrates a discrepancy with the documented HLA type.
Int. J. Cancer 132:246-247(2013)
PubMed=23955599; DOI=10.1038/ng.2731
Kon A., Shih L.-Y., Minamino M., Sanada M., Shiraishi Y., Nagata Y., Yoshida K.-i., Okuno Y., Bando M., Nakato R., Ishikawa S., Sato-Otsubo A., Nagae G., Nishimoto A., Haferlach C., Nowak D., Sato Y., Alpermann T., Nagasaki M., Shimamura T., Tanaka H., Chiba K., Yamamoto R., Yamaguchi T., Otsu M., Obara N., Sakata-Yanagimoto M., Nakamaki T., Ishiyama K., Nolte F., Hofmann W.-K., Miyawaki S., Chiba S., Mori H., Nakauchi H., Koeffler H.P., Aburatani H., Haferlach T., Shirahige K., Miyano S., Ogawa S.
Recurrent mutations in multiple components of the cohesin complex in myeloid neoplasms.
Nat. Genet. 45:1232-1237(2013)
PubMed=24368162; DOI=10.1016/j.exphem.2013.12.004
Sripayap P., Nagai T., Uesawa M., Kobayashi H., Tsukahara T., Ohmine K., Muroi K., Ozawa K.
Mechanisms of resistance to azacitidine in human leukemia cell lines.
Exp. Hematol. 42:294-306.e2(2014)
PubMed=25130606; DOI=10.1016/j.intimp.2014.08.002
Chanput W., Mes J.J., Wichers H.J.
THP-1 cell line: an in vitro cell model for immune modulation approach.
Int. Immunopharmacol. 23:37-45(2014)
PubMed=25984343; DOI=10.1038/sdata.2014.35; PMCID=PMC4432652
Cowley G.S., Weir B.A., Vazquez F., Tamayo P., Scott J.A., Rusin S., East-Seletsky A., Ali L.D., Gerath W.F.J., Pantel S.E., Lizotte P.H., Jiang G.-Z., Hsiao J., Tsherniak A., Dwinell E., Aoyama S., Okamoto M., Harrington W., Gelfand E.T., Green T.M., Tomko M.J., Gopal S., Wong T.C., Li H.-B., Howell S., Stransky N., Liefeld T., Jang D., Bistline J., Meyers B.H., Armstrong S.A., Anderson K.C., Stegmaier K., Reich M., Pellman D., Boehm J.S., Mesirov J.P., Golub T.R., Root D.E., Hahn W.C.
Parallel genome-scale loss of function screens in 216 cancer cell lines for the identification of context-specific genetic dependencies.
Sci. Data 1:140035-140035(2014)
PubMed=25485619; DOI=10.1038/nbt.3080
Klijn C., Durinck S., Stawiski E.W., Haverty P.M., Jiang Z.-S., Liu H.-B., Degenhardt J., Mayba O., Gnad F., Liu J.-F., Pau G., Reeder J., Cao Y., Mukhyala K., Selvaraj S.K., Yu M.-M., Zynda G.J., Brauer M.J., Wu T.D., Gentleman R.C., Manning G., Yauch R.L., Bourgon R., Stokoe D., Modrusan Z., Neve R.M., de Sauvage F.J., Settleman J., Seshagiri S., Zhang Z.-M.
A comprehensive transcriptional portrait of human cancer cell lines.
Nat. Biotechnol. 33:306-312(2015)
PubMed=25877200; DOI=10.1038/nature14397
Yu M., Selvaraj S.K., Liang-Chu M.M.Y., Aghajani S., Busse M., Yuan J., Lee G., Peale F.V., Klijn C., Bourgon R., Kaminker J.S., Neve R.M.
A resource for cell line authentication, annotation and quality control.
Nature 520:307-311(2015)
PubMed=26589293; DOI=10.1186/s13073-015-0240-5; PMCID=PMC4653878
Scholtalbers J., Boegel S., Bukur T., Byl M., Goerges S., Sorn P., Loewer M., Sahin U., Castle J.C.
TCLP: an online cancer cell line catalogue integrating HLA type, predicted neo-epitopes, virus and gene expression.
Genome Med. 7:118.1-118.7(2015)
PubMed=29787063; DOI=10.1007/978-3-319-16104-4_14
Chanput W., Peters V., Wichers H.J.
THP-1 and U937 cells.
(In book chapter) The impact of food bioactives on health. In vitro and ex vivo models; Verhoeckx K., Cotter P., Lopez-Exposito I., Kleiveland C., Lea T., Mackie A., Requena T., Swiatecka D., Wichers H. (eds.); pp.147-159; Springer; Cham; Switzerland (2015)
PubMed=26421875; DOI=10.1089/ten.TEC.2015.0188
Yamazoe H., Hagihara Y., Kobayashi H.
Multicomponent coculture system of cancer cells and two types of stromal cells for in vitro evaluation of anticancer drugs.
Tissue Eng. Part C. Methods 22:20-29(2016)
PubMed=27397505; DOI=10.1016/j.cell.2016.06.017; PMCID=PMC4967469
Iorio F., Knijnenburg T.A., Vis D.J., Bignell G.R., Menden M.P., Schubert M., Aben N., Goncalves E., Barthorpe S., Lightfoot H., Cokelaer T., Greninger P., van Dyk E., Chang H., de Silva H., Heyn H., Deng X.-M., Egan R.K., Liu Q.-S., Miroo T., Mitropoulos X., Richardson L., Wang J.-H., Zhang T.-H., Moran S., Sayols S., Soleimani M., Tamborero D., Lopez-Bigas N., Ross-Macdonald P., Esteller M., Gray N.S., Haber D.A., Stratton M.R., Benes C.H., Wessels L.F.A., Saez-Rodriguez J., McDermott U., Garnett M.J.
A landscape of pharmacogenomic interactions in cancer.
Cell 166:740-754(2016)
PubMed=28109323; DOI=10.1186/s13045-017-0396-0; PMCID=PMC5251306
Masetti R., Bertuccio S.N., Astolfi A., Chiarini F., Lonetti A., Indio V., De Luca M., Bandini J., Serravalle S., Franzoni M., Pigazzi M., Martelli A.M., Basso G., Locatelli F., Pession A.
Hh/Gli antagonist in acute myeloid leukemia with CBFA2T3-GLIS2 fusion gene.
J. Hematol. Oncol. 10:26.1-26.5(2017)
PubMed=28196595; DOI=10.1016/j.ccell.2017.01.005; PMCID=PMC5501076
Li J., Zhao W., Akbani R., Liu W.-B., Ju Z.-L., Ling S.-Y., Vellano C.P., Roebuck P., Yu Q.-H., Eterovic A.K., Byers L.A., Davies M.A., Deng W.-L., Gopal Y.N.V., Chen G., von Euw E.M., Slamon D.J., Conklin D., Heymach J.V., Gazdar A.F., Minna J.D., Myers J.N., Lu Y.-L., Mills G.B., Liang H.
Characterization of human cancer cell lines by reverse-phase protein arrays.
Cancer Cell 31:225-239(2017)
PubMed=28404994; DOI=10.1038/s41598-017-00828-y; PMCID=PMC5429802
Muller M.M., Lehmann R., Klassert T.E., Reifenstein S., Conrad T., Moore C., Kuhn A., Behnert A., Guthke R., Driesch D., Slevogt H.
Global analysis of glycoproteins identifies markers of endotoxin tolerant monocytes and GPR84 as a modulator of TNFalpha expression.
Sci. Rep. 7:838-838(2017)
PubMed=29169185; DOI=10.14573/altex.1607191
Kletting S., Barthold S., Repnik U., Griffiths G.W., Loretz B., Schneider-Daum N., de Souza Carvalho-Wodarz C., Lehr C.-M.
Co-culture of human alveolar epithelial (hAELVi) and macrophage (THP-1) cell lines.
ALTEX 35:211-222(2018)
PubMed=29901211; DOI=10.14573/altex.1710051
Edwards A., Roscoe L., Longmore C., Bailey F., Sim B., Treasure C.
Adaptation of the human Cell Line Activation Test (h-CLAT) to animal-product-free conditions.
ALTEX 35:477-488(2018)
PubMed=30285677; DOI=10.1186/s12885-018-4840-5; PMCID=PMC6167786
Tan K.-T., Ding L.-W., Sun Q.-Y., Lao Z.-T., Chien W., Ren X., Xiao J.-F., Loh X.-Y., Xu L., Lill M., Mayakonda A., Lin D.-C., Yang H.H., Koeffler H.P.
Profiling the B/T cell receptor repertoire of lymphocyte derived cell lines.
BMC Cancer 18:940.1-940.13(2018)
PubMed=30629668; DOI=10.1371/journal.pone.0210404; PMCID=PMC6328144
Uphoff C.C., Pommerenke C., Denkmann S.A., Drexler H.G.
Screening human cell lines for viral infections applying RNA-Seq data analysis.
PLoS ONE 14:E0210404-E0210404(2019)
PubMed=30894373; DOI=10.1158/0008-5472.CAN-18-2747; PMCID=PMC6445675
Dutil J., Chen Z.-H., Monteiro A.N.A., Teer J.K., Eschrich S.A.
An interactive resource to probe genetic diversity and estimated ancestry in cancer cell lines.
Cancer Res. 79:1263-1273(2019)
PubMed=31068700; DOI=10.1038/s41586-019-1186-3; PMCID=PMC6697103
Ghandi M., Huang F.W., Jane-Valbuena J., Kryukov G.V., Lo C.C., McDonald E.R. 3rd, Barretina J.G., Gelfand E.T., Bielski C.M., Li H.-X., Hu K., Andreev-Drakhlin A.Y., Kim J., Hess J.M., Haas B.J., Aguet F., Weir B.A., Rothberg M.V., Paolella B.R., Lawrence M.S., Akbani R., Lu Y.-L., Tiv H.L., Gokhale P.C., de Weck A., Mansour A.A., Oh C., Shih J., Hadi K., Rosen Y., Bistline J., Venkatesan K., Reddy A., Sonkin D., Liu M., Lehar J., Korn J.M., Porter D.A., Jones M.D., Golji J., Caponigro G., Taylor J.E., Dunning C.M., Creech A.L., Warren A.C., McFarland J.M., Zamanighomi M., Kauffmann A., Stransky N., Imielinski M., Maruvka Y.E., Cherniack A.D., Tsherniak A., Vazquez F., Jaffe J.D., Lane A.A., Weinstock D.M., Johannessen C.M., Morrissey M.P., Stegmeier F., Schlegel R., Hahn W.C., Getz G., Mills G.B., Boehm J.S., Golub T.R., Garraway L.A., Sellers W.R.
Next-generation characterization of the Cancer Cell Line Encyclopedia.
Nature 569:503-508(2019)
PubMed=31160637; DOI=10.1038/s41598-019-44491-x; PMCID=PMC6547646
Quentmeier H., Pommerenke C., Dirks W.G., Eberth S., Koeppel M., MacLeod R.A.F., Nagel S., Steube K.G., Uphoff C.C., Drexler H.G.
The LL-100 panel: 100 cell lines for blood cancer studies.
Sci. Rep. 9:8218-8218(2019)
PubMed=31978347; DOI=10.1016/j.cell.2019.12.023; PMCID=PMC7339254
Nusinow D.P., Szpyt J., Ghandi M., Rose C.M., McDonald E.R. 3rd, Kalocsay M., Jane-Valbuena J., Gelfand E.T., Schweppe D.K., Jedrychowski M.P., Golji J., Porter D.A., Rejtar T., Wang Y.K., Kryukov G.V., Stegmeier F., Erickson B.K., Garraway L.A., Sellers W.R., Gygi S.P.
Quantitative proteomics of the Cancer Cell Line Encyclopedia.
Cell 180:387-402.e16(2020)
PubMed=32387766; DOI=10.1016/j.molimm.2020.04.008
Pandey K., Mifsud N.A., Lim Kam Sian T.C.C., Ayala R., Ternette N., Ramarathinam S.H., Purcell A.W.
In-depth mining of the immunopeptidome of an acute myeloid leukemia cell line using complementary ligand enrichment and data acquisition strategies.
Mol. Immunol. 123:7-17(2020)"







![THP-1[人单核细胞白血病细胞]](https://img.chemicalbook.com/SupplyImg/2019-08-27/Large/201908272025145035882.jpg)
![THP1[人急性单核细胞]](https://img.chemicalbook.com/SupplyImg/2019-09-08/Large/201909081323553984986.jpg)