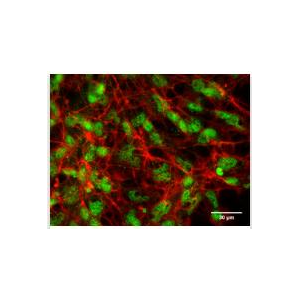
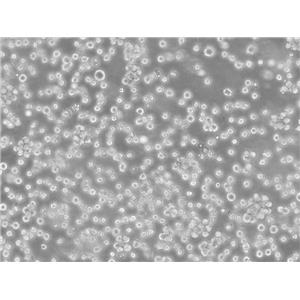
"AGS人胃腺癌细胞全年复苏|已有STR图谱
传代比例:1:2-1:4(首次传代建议1:2)
生长特性:贴壁生长
公司细胞系形态漂亮、增殖倍数高、纯度高、功能性强,细胞培养就跟养孩子一个样。养孩子要喂奶,养细胞要加补液,都需要在前期补充足够的营养,初始状态的细胞或刚刚复苏的细胞还要适量加入血清或细胞因子来帮助它们的存活增殖,如果营养物质缺乏,细胞就会不生长甚至死亡。养孩子要从小培养学习,养细胞也得培养宝宝顺利生下来,你会经常抚摸他,给他看各种颜色,刺激他的五感。细胞也是一样,分离后的细胞需要使用特定的细胞因子进行活化、增殖。另外加入因子的种类、因子的浓度、加入时间、加入顺序都会影响细胞最终的结果。养孩子最怕孩子生病,养细胞最怕被污染,平时你会仔细观察宝宝是否呕吐、是否突然哭闹,猜测宝宝是否生病了。对于细胞,我们也需要时刻进行观察的,假如培养液浑浊(污染了),则需要换液后加抗生素;假如细胞增殖不明显,形态变差,则可能是因为营养不足了,对贴壁细胞可以消化后重新用新的培养基接种并加倍加入细胞因子含量;对悬浮细胞增殖能力不强的,则不着急补液,只是先补加血清、细胞因子看是否可以好转。培养时还得全程在无菌的环境,一个小小的偏差,细胞就会死亡。
换液周期:每周2-3次
SCH Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SUP T1细胞、Metastatic Variant 522细胞、DoHH-2细胞
H-28 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:6传代,每周换液2-3次;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:NCIH2126细胞、NCI-H2228细胞、UACC-812细胞
RCF Cells;背景说明:心肌;成纤维 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HA细胞、Malme-3 M细胞、MRASMC细胞
背景信息:TheAGS细胞株源自一个未经治疗的切除肿瘤碎块。在下述培养基中植板率为34%。支原体感染后消除。
AGS人胃腺癌细胞全年复苏|已有STR图谱
产品包装:复苏发货:T25培养瓶(一瓶)或冻存发货:1ml冻存管(两支)
ATCC细胞库(American Type Culture Colection),该中心一直致力于细胞分类、鉴定和保藏工作。ATCC是全球最大的生物资源保藏中心,ATCC通过行业标准产品、服务和创新解决方案支持全球学术、政府、生物技术、制药、食品、农业和工业领域的科学进步。ATCC提供的服务和定制解决方案包括细胞和微生物培养、鉴定、生物衍生物的开发和生产、性能测试和生物资源保藏服务。美国国家标准协会(ANSI)认可了ATCC标准开发组织,并制定了标准协议,以确保生物材料的可靠性和可重复性。ATCC的使命是为了获取、鉴定、保存、开发、标准化和分发生物资源和生物信息,以提高和应用生物科学知识。
MLA144 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:HCA7细胞、LA-4 [Mouse lung adenoma]细胞、Scott and White No. 13细胞
4T1-LUC Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:HEL-92.1.7细胞、BT-325细胞、H650细胞
brain-derived Endothelial cells.3 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:NH-6细胞、RPMI 7951细胞、OCI-Ly 3细胞
2F2 [Mouse hybridoma against P.vivax csp] Cells(提供STR鉴定图谱)
来源说明:细胞主要来源ATCC、ECACC、DSMZ、RIKEN等细胞库
物种来源:人源、鼠源等其它物种来源
AGS人胃腺癌细胞全年复苏|已有STR图谱
形态特性:上皮细胞样
细胞株(系)的使用,为医学研究和测试工作带来了大的方便。但细胞的传代是有限制的,长期连续传代的细胞,不仅消耗大量的人力和物力,而且细胞的生长与形态等会有一定退变或转化,因而细胞失去原有的遗传性,有时还会由于细胞污染而造成传代中断,种子丢失。因此,在实际工作中常需冻存一定数量的细胞,以备替换使用。细胞冷冻与复苏是细胞培养 室的常规工作和通用技术。目前,细胞冻存Zui常用的技术是冷冻保存法,主要采用加适量保护剂的缓慢冷冻法冻存细胞。细胞在不加任何保护剂的情况下直接冷冻,细胞内外的水分会很快形成冰晶,从而引起一系列不良反应。如细胞脱水使局部电解质浓度增GAO,pH值改变,部分蛋白质由于上述原因而变性,引起细胞内部空间结构紊乱,溶酶体膜由此遭到损伤而释放出溶酶体酶,使细胞内结构成分造成破坏,线粒体肿胀,功能丢失,并造成能量代谢障碍。胞膜上的类脂蛋白复合体也易破坏引起细胞膜通透性的改变,使细胞内容物丢失。如果细胞内冰晶形成较多,随冷冻温度的降低,冰晶体积膨胀造成细胞核DNA空间构型发生不可逆的损伤,而致细胞死亡。因此,细胞冷冻技术的关键是尽可能地减少细胞内水分,减少细胞内冰晶的形成。采用甘油或二甲基亚砜作保护剂,这两种物质分子量小,溶解度大,易穿透细胞,可以使冰点下降,提GAO细胞膜对水的通透性,且对细胞无明显毒性。慢速冷冻方法又可使细胞内的水分渗出细胞外,减少胞内形成冰结晶的机会,从而减少冰晶对细胞的损伤。
RAMSCs Cells;背景说明:脂肪间充质干 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:H920细胞、DHL-6细胞、A3细胞
A10 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SK-MEL2细胞、alphaTC clone 6细胞、OV90细胞
H-9 Cells;背景说明:H9细胞是HUT78(ATCCTIB161)的克隆系(Callo,RC,etal)。细胞表面带有CD3、CD4标记。研究表明,该细胞系对人体免疫缺陷病毒(HIV-1)敏感,可用于检测、分离和增殖HIV-1,也可用于其它人类Tcell病毒的研究。;传代方法:1:3传代,2-3天传一代;生长特性:悬浮生长;形态特性:淋巴母细胞样;相关产品有:NCI-H1648细胞、NALM6细胞、H4IIE细胞
MF2059 Cells;背景说明:皮肤;T淋巴细胞瘤;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:WM266mel细胞、HBL 100细胞、SU.86细胞
Mel RM Cells;背景说明:黑色素瘤;神经节转移;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:MFC细胞、HEK-293-F细胞、H2135细胞
OCI-LY-7 Cells;背景说明:弥漫大B淋巴瘤;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:HEC-251细胞、SK-ES-1细胞、Hamster Islet Transformed-Tioguanine resistant clone 15细胞
ECV 304 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:SK-MEL24细胞、NCI-H596细胞、THLE-2细胞
USMC Cells;背景说明:血管平滑肌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:UT7细胞、Hs 840.T细胞、HEK-293-F细胞
TE-6 Cells;背景说明:详见相关文献介绍;传代方法:消化3-5分钟。1:2。3天内可长满。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:SK MEL 28细胞、MFC细胞、REC-1细胞
NHDF Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:CAL 33细胞、UCLA-SO-M21细胞、D341 Med细胞
RMC-1 Cells;背景说明:视网膜;Muller细胞;SD;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:VM-CUB-I细胞、LC-1-sq细胞、HuT102细胞
B16 Cells;背景说明:该细胞源于C57BL/6J小鼠黑色素瘤,可以产生黑色素,同基因小鼠体内移植可成瘤;传代方法:1:3传代,2-3天换液一次;生长特性:贴壁生长;形态特性:梭形;相关产品有:Panc-08.13细胞、CCD33Co细胞、Panc-8_13细胞
Panc02 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:P815细胞、KTA-7细胞、CHOS细胞
HaCaT Cells;背景说明:该细胞源自一位62岁患有黑色素瘤男性的病灶外围正常皮肤,角蛋白、角化细胞交联外膜蛋白、中间丝相关蛋白阳性。;传代方法:1:3—1:6传代,每周换液2—3次;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:HO-1-N-1细胞、Be Wo细胞、MGSMC细胞
NCI-H1792 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:8传代。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:MA 104细胞、COLO 678细胞、A-375SM细胞
COLO 206F Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:PLA 802细胞、CCD 966 SK细胞、Hi-five细胞
MDAMB453 Cells;背景说明:该细胞系由CailleauR在1976年从一名48岁的患有转移性乳腺癌的白人女性的心包渗出液中分离建立的。该细胞表达FGF的受体。;传代方法:1:2-1:4传代;2-3天换液1次;生长特性:贴壁生长;形态特性:上皮样;多角形;相关产品有:MDA-MB-436细胞、H-1651细胞、SK-ML2细胞
894-mel Cells(提供STR鉴定图谱)
Abcam MCF-7 JAK1 KO Cells(提供STR鉴定图谱)
ATL-3I Cells(提供STR鉴定图谱)
BayGenomics ES cell line RRO124 Cells(提供STR鉴定图谱)
BayGenomics ES cell line YHB185 Cells(提供STR鉴定图谱)
CCLF-UPGI-0061-T Cells(提供STR鉴定图谱)
DA01075 Cells(提供STR鉴定图谱)
DA06190 Cells(提供STR鉴定图谱)
GM00726 Cells(提供STR鉴定图谱)
H-226 Cells;背景说明:1980年分离建立。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:RSC96细胞、CAL 62细胞、NCI-H28细胞
EB-3 Cells;背景说明:该细胞源自一名3岁患有Burkitt's淋巴瘤的黑人男孩的B淋巴细胞,EBNA阳性。;传代方法:1:2-1:4传代,每周2-3次。;生长特性:悬浮生长;形态特性:淋巴母细胞样;相关产品有:SW 1783细胞、SK-NM-C细胞、Y3-Ag 1.2.3细胞
H-596 Cells;背景说明:详见相关文献介绍;传代方法:1:4-1:8传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:H-661细胞、CAL62细胞、Tb1Lu细胞
PL-45 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:KPNRTBM1细胞、SAOS 2细胞、DHL-4细胞
BHK Cells;背景说明:详见相关文献介绍;传代方法:1:2传代,每周换液1-2次。;生长特性:贴壁生长;形态特性:成纤维细胞样;相关产品有:TEC细胞、I90细胞、H2085细胞
SK-LU-1 Cells;背景说明:该细胞系源于一位60岁的白人女性患者的肺腺癌组织。;传代方法:1:2传代;每周换液2次。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:OCI-Ly 3细胞、LN 382细胞、211H细胞
Hs 888Lu Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:Ramos 2G6 4C10细胞、KP2细胞、KYSE70细胞
NCI-SNU-1 Cells;背景说明:详见相关文献介绍;传代方法:2-3天换液1次。;生长特性:悬浮聚集;形态特性:上皮细胞;相关产品有:HCC-78细胞、MGSMC细胞、MH7A细胞
AGS人胃腺癌细胞全年复苏|已有STR图谱
EA hy 926 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:GM00637B细胞、SUDHL-6细胞、HS-68细胞
DHL-4 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:淋巴母细胞;相关产品有:NTHY-ORI3.1细胞、Panc-813细胞、H2110细胞
OVCAR8 Cells;背景说明:卵巢癌;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:RCC4细胞、SKRC-39细胞、Panc4.03细胞
Mc Ardle 7777 Cells;背景说明:肝癌;雌性;Buffalo;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:PLC-PRF-5细胞、MBMEC细胞、SUDHL-6细胞
Rat Chondrosarcoma Swarm Cells;背景说明:软骨肉瘤;SD;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HL1细胞、HEK-293A细胞、MES 23.5细胞
CEMC1 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:DK-MG细胞、H9c2 (2-1)细胞、MDCK.2细胞
32D.cl3 Cells;背景说明:骨髓淋巴瘤;C3H/HeJ;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:Mouse Podocyte Clone-5细胞、LS-411N细胞、QBC939细胞
GM21086 Cells(提供STR鉴定图谱)
HAP1 LITAF (-) 1 Cells(提供STR鉴定图谱)
KLN-205 Cells;背景说明:肺;鳞癌细胞;DBA;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:RCS细胞、H1437细胞、Centre Antoine Lacassagne-51细胞
SNU761 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:NCIH1694细胞、H1755细胞、Bac 1.2F5细胞
Huh-7.5 Cells;背景说明:肝癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HEK 293-H细胞、NCI-H510细胞、MA104细胞
HCC-202 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:RT4细胞、NB1-RGB细胞、ND7/23细胞
MG-63 Cells;背景说明:该细胞源自14岁患有骨肉瘤的白人男性;聚次黄嘌呤核苷-聚胞嘧啶核苷酸、和D可以诱导产生高水平的干扰素。该细胞表达TGF-β受体Ⅰ和Ⅱ。 ;传代方法:1:4-1:8传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:TEV-1细胞、NRK-52E细胞、FK81细胞
V-79 Cells;背景说明:肺;自发永生;雄性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:NCI-SNU-5细胞、H9细胞、SKM1细胞
CA922 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:MOLT4细胞、Mv.1.Lu细胞、SK-N-SH细胞
H-735 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:P30/Ohkubo细胞、LS 1034细胞、IPAM-WT细胞
HPSI0216i-heub_6 Cells(提供STR鉴定图谱)
K562 eGFP-NR2C2 Cells(提供STR鉴定图谱)
MEDEP-BRC4-2 Cells(提供STR鉴定图谱)
NH50167 Cells(提供STR鉴定图谱)
QGY-7701 Cells(提供STR鉴定图谱)
TOB0121 Cells(提供STR鉴定图谱)
UFL-AG-286 Cells(提供STR鉴定图谱)
HAP1 SUV39H1 (-) 2 Cells(提供STR鉴定图谱)
Capan1 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:SK-RC-20细胞、UWB1-289细胞、HRMC细胞
Baby Hamster Kidney-21 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代,每周换液1-2次。;生长特性:贴壁生长;形态特性:成纤维细胞样;相关产品有:UMC-11细胞、SW527细胞、HCC4006细胞
NCI-H2444 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:4传代;每周换液2次。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:MPC-5细胞、NCI-H2009细胞、KPL4细胞
TE-14 Cells;背景说明:详见相关文献介绍;传代方法:消化3-5分钟。1:2。3天内可长满。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:A-20细胞、C33A细胞、HEC1A细胞
PAa Cells;背景说明:肺腺癌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:ML2细胞、HCC2218细胞、C-8161细胞
MG-63 Cells;背景说明:该细胞源自14岁患有骨肉瘤的白人男性;聚次黄嘌呤核苷-聚胞嘧啶核苷酸、和D可以诱导产生高水平的干扰素。该细胞表达TGF-β受体Ⅰ和Ⅱ。 ;传代方法:1:4-1:8传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:TEV-1细胞、NRK-52E细胞、FK81细胞
HBVSMC Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:CAL-27细胞、Kelly细胞、OCI AML4细胞
BGC-823 Cells;背景说明:建自一位62岁的胃癌患者;传代方法:1:3传代,2-3天换液一次;生长特性:贴壁生长;形态特性:上皮样;相关产品有:Pa17C细胞、7404细胞、H-2106细胞
HCC-9724 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:LN299细胞、L-6 myoblast细胞、697细胞
Leghorn Male Hepatoma cell line Cells;背景说明:肝癌;雄性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:2V6.11细胞、P-19细胞、COR-L 105细胞
MGH-U3 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:RC-K8细胞、AR4-2J细胞、PANC1005细胞
MH7A Cells;背景说明:关节;成纤维细胞;SV40转化;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HOK细胞、BHP-10细胞、H1793细胞
HCC9724 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:BIU87细胞、MRAEC细胞、T-47D细胞
SUP-B15 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代。3天内可长满。;生长特性:悬浮生长;形态特性:淋巴母细胞;相关产品有:NK-92.05细胞、PC-3M 2B4细胞、Hs 742.T细胞
L-1210 Cells;背景说明:该细胞源于用0.2%甲基胆蒽(溶解)涂抹雌性小鼠的皮肤诱发的肿瘤,鼠痘病毒阴性。;传代方法:1:2传代;生长特性:悬浮生长;形态特性:淋巴母细胞样;相关产品有:Cattle chondrocytes细胞、3T3J2细胞、MJ细胞
Spli-B Cells(提供STR鉴定图谱)
AKR Cells;背景说明:食管癌;AKR;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:PA-TU S细胞、RS 4;11细胞、184A1细胞
MDCKII Cells;背景说明:详见相关文献介绍;传代方法:1:3传代,3-4天传1次;生长特性:贴壁生长;形态特性:上皮样;相关产品有:NCI-H774细胞、EoL-1-cell细胞、HCE细胞
AML193 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代。3天内可长满。;生长特性:悬浮生长;形态特性:淋巴母细胞;相关产品有:NCIH146细胞、MOLP2细胞、GM01232E细胞
Anip 973 Cells;背景说明:肺腺癌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:OE21细胞、CCD-966SK细胞、Co 115细胞
CNE2 Cells;背景说明:1983年由谷淑燕、孔繁裔等建系;源自人鼻咽低分化鳞癌组织;原代细胞胰蛋白酶消化,48小时开始生长,首次传代20天。裸鼠体内移植100%成瘤。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:WEHI 3细胞、HuPT3细胞、ECV细胞
Hca-F Cells;背景说明:肝癌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:ARO81细胞、RASMCs细胞、SK Mel 2细胞
MEL-526 Cells;背景说明:黑色素瘤;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:Tj-905细胞、HEK 293-H细胞、WILL2细胞
NCIH3255 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:EAhy 926细胞、A-375细胞、VK2 (E6/E7)细胞
AGS人胃腺癌细胞全年复苏|已有STR图谱
VP267 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:Adult Retinal Pigment Epithelial cell line-19细胞、COV-434细胞、H2029细胞
Murine Carcinoma-38 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:SNU-739细胞、NCIH345细胞、MALME 3M细胞
GMK,BSC-1 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:TE 85 ClF-5细胞、NB4细胞、COLO 205细胞
NCIH1975 Cells;背景说明:这株细胞于1988年七月建株。组织提供者是一位非吸烟人士。;传代方法:消化3-5分钟。1:2。3天内可长满。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:SW 480细胞、HUT-28细胞、EFM192B细胞
HCS2/8 Cells;背景说明:软骨肉瘤;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SNU-449细胞、SLMT1细胞、FHL 124细胞
KYSE510 Cells;背景说明:食管鳞癌;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:NCIH2342细胞、CORL23细胞、A375-S2细胞
BayGenomics ES cell line RRP208 Cells(提供STR鉴定图谱)
BayGenomics ES cell line YHC243 Cells(提供STR鉴定图谱)
Hepa-C12 Cells(提供STR鉴定图谱)
PCRP-DAXX-5G11 Cells(提供STR鉴定图谱)
C6 rho-0#14 Cells(提供STR鉴定图谱)
HPS0775 Cells(提供STR鉴定图谱)
" "PubMed=10402490; DOI=10.3892/ijmm.4.2.203
Rha S.Y., Noh S.H., Kim T.S., Yoo N.C., Roh J.K., Min J.S., Kim B.-S., Kim M.Y., Chung H.C.
Modulation of biological phenotypes for tumor growth and metastasis by target-specific biological inhibitors in gastric cancer.
Int. J. Mol. Med. 4:203-212(1999)
PubMed=15767549; DOI=10.1158/1535-7163.MCT-04-0234
Nakatsu N., Yoshida Y., Yamazaki K., Nakamura T., Dan S., Fukui Y., Yamori T.
Chemosensitivity profile of cancer cell lines and identification of genes determining chemosensitivity by an integrated bioinformatical approach using cDNA arrays.
Mol. Cancer Ther. 4:399-412(2005)
PubMed=17509637; DOI=10.1016/j.virol.2007.03.061
Young D.F., Carlos T.S., Hagmaier K., Fan L., Randall R.E.
AGS and other tissue culture cells can unknowingly be persistently infected with PIV5; a virus that blocks interferon signalling by degrading STAT1.
Virology 365:238-240(2007)
PubMed=18804159; DOI=10.1016/j.ygeno.2008.08.002
Jung J.-J., Jeung H.-C., Chung H.C., Lee J.O., Kim T.S., Kim Y.T., Noh S.H., Rha S.Y.
In vitro pharmacogenomic database and chemosensitivity predictive genes in gastric cancer.
Genomics 93:52-61(2009)
PubMed=20164919; DOI=10.1038/nature08768; PMCID=PMC3145113
Bignell G.R., Greenman C.D., Davies H.R., Butler A.P., Edkins S., Andrews J.M., Buck G., Chen L., Beare D., Latimer C., Widaa S., Hinton J., Fahey C., Fu B.-Y., Swamy S., Dalgliesh G.L., Teh B.T., Deloukas P., Yang F.-T., Campbell P.J., Futreal P.A., Stratton M.R.
Signatures of mutation and selection in the cancer genome.
Nature 463:893-898(2010)
PubMed=20215515; DOI=10.1158/0008-5472.CAN-09-3458; PMCID=PMC2881662
Rothenberg S.M., Mohapatra G., Rivera M.N., Winokur D., Greninger P., Nitta M., Sadow P.M., Sooriyakumar G., Brannigan B.W., Ulman M.J., Perera R.M., Wang R., Tam A., Ma X.-J., Erlander M., Sgroi D.C., Rocco J.W., Lingen M.W., Cohen E.E.W., Louis D.N., Settleman J., Haber D.A.
A genome-wide screen for microdeletions reveals disruption of polarity complex genes in diverse human cancers.
Cancer Res. 70:2158-2164(2010)
PubMed=22460905; DOI=10.1038/nature11003; PMCID=PMC3320027
Barretina J.G., Caponigro G., Stransky N., Venkatesan K., Margolin A.A., Kim S., Wilson C.J., Lehar J., Kryukov G.V., Sonkin D., Reddy A., Liu M., Murray L., Berger M.F., Monahan J.E., Morais P., Meltzer J., Korejwa A., Jane-Valbuena J., Mapa F.A., Thibault J., Bric-Furlong E., Raman P., Shipway A., Engels I.H., Cheng J., Yu G.-Y.K., Yu J.-J., Aspesi P. Jr., de Silva M., Jagtap K., Jones M.D., Wang L., Hatton C., Palescandolo E., Gupta S., Mahan S., Sougnez C., Onofrio R.C., Liefeld T., MacConaill L.E., Winckler W., Reich M., Li N.-X., Mesirov J.P., Gabriel S.B., Getz G., Ardlie K., Chan V., Myer V.E., Weber B.L., Porter J., Warmuth M., Finan P., Harris J.L., Meyerson M.L., Golub T.R., Morrissey M.P., Sellers W.R., Schlegel R., Garraway L.A.
The Cancer Cell Line Encyclopedia enables predictive modelling of anticancer drug sensitivity.
Nature 483:603-607(2012)
PubMed=24807215; DOI=10.1038/ncomms4830; PMCID=PMC4024760
Liu J.-F., McCleland M.L., Stawiski E.W., Gnad F., Mayba O., Haverty P.M., Durinck S., Chen Y.-J., Klijn C., Jhunjhunwala S., Lawrence M., Liu H.-B., Wan Y.-N., Chopra V.S., Yaylaoglu M.B., Yuan W.-L., Ha C., Gilbert H.N., Reeder J., Pau G., Stinson J., Stern H.M., Manning G., Wu T.D., Neve R.M., de Sauvage F.J., Modrusan Z., Seshagiri S., Firestein R., Zhang Z.-M.
Integrated exome and transcriptome sequencing reveals ZAK isoform usage in gastric cancer.
Nat. Commun. 5:3830.1-3830.8(2014)
PubMed=25960936; DOI=10.4161/21624011.2014.954893; PMCID=PMC4355981
Boegel S., Lower M., Bukur T., Sahin U., Castle J.C.
A catalog of HLA type, HLA expression, and neo-epitope candidates in human cancer cell lines.
OncoImmunology 3:e954893.1-e954893.12(2014)
PubMed=25984343; DOI=10.1038/sdata.2014.35; PMCID=PMC4432652
Cowley G.S., Weir B.A., Vazquez F., Tamayo P., Scott J.A., Rusin S., East-Seletsky A., Ali L.D., Gerath W.F.J., Pantel S.E., Lizotte P.H., Jiang G.-Z., Hsiao J., Tsherniak A., Dwinell E., Aoyama S., Okamoto M., Harrington W., Gelfand E.T., Green T.M., Tomko M.J., Gopal S., Wong T.C., Li H.-B., Howell S., Stransky N., Liefeld T., Jang D., Bistline J., Meyers B.H., Armstrong S.A., Anderson K.C., Stegmaier K., Reich M., Pellman D., Boehm J.S., Mesirov J.P., Golub T.R., Root D.E., Hahn W.C.
Parallel genome-scale loss of function screens in 216 cancer cell lines for the identification of context-specific genetic dependencies.
Sci. Data 1:140035-140035(2014)
PubMed=25485619; DOI=10.1038/nbt.3080
Klijn C., Durinck S., Stawiski E.W., Haverty P.M., Jiang Z.-S., Liu H.-B., Degenhardt J., Mayba O., Gnad F., Liu J.-F., Pau G., Reeder J., Cao Y., Mukhyala K., Selvaraj S.K., Yu M.-M., Zynda G.J., Brauer M.J., Wu T.D., Gentleman R.C., Manning G., Yauch R.L., Bourgon R., Stokoe D., Modrusan Z., Neve R.M., de Sauvage F.J., Settleman J., Seshagiri S., Zhang Z.-M.
A comprehensive transcriptional portrait of human cancer cell lines.
Nat. Biotechnol. 33:306-312(2015)
PubMed=26589293; DOI=10.1186/s13073-015-0240-5; PMCID=PMC4653878
Scholtalbers J., Boegel S., Bukur T., Byl M., Goerges S., Sorn P., Loewer M., Sahin U., Castle J.C.
TCLP: an online cancer cell line catalogue integrating HLA type, predicted neo-epitopes, virus and gene expression.
Genome Med. 7:118.1-118.7(2015)
PubMed=27397505; DOI=10.1016/j.cell.2016.06.017; PMCID=PMC4967469
Iorio F., Knijnenburg T.A., Vis D.J., Bignell G.R., Menden M.P., Schubert M., Aben N., Goncalves E., Barthorpe S., Lightfoot H., Cokelaer T., Greninger P., van Dyk E., Chang H., de Silva H., Heyn H., Deng X.-M., Egan R.K., Liu Q.-S., Miroo T., Mitropoulos X., Richardson L., Wang J.-H., Zhang T.-H., Moran S., Sayols S., Soleimani M., Tamborero D., Lopez-Bigas N., Ross-Macdonald P., Esteller M., Gray N.S., Haber D.A., Stratton M.R., Benes C.H., Wessels L.F.A., Saez-Rodriguez J., McDermott U., Garnett M.J.
A landscape of pharmacogenomic interactions in cancer.
Cell 166:740-754(2016)
PubMed=27445371; DOI=10.1128/genomeA.00653-16; PMCID=PMC4956444
Wignall-Fleming E.B., Young D.F., Goodbourn S., Davison A.J., Randall R.E.
Genome sequence of the parainfluenza virus 5 strain that persistently infects AGS cells.
Genome Announc. 4:e00653.16.1-e00653.16.2(2016)
PubMed=28196595; DOI=10.1016/j.ccell.2017.01.005; PMCID=PMC5501076
Li J., Zhao W., Akbani R., Liu W.-B., Ju Z.-L., Ling S.-Y., Vellano C.P., Roebuck P., Yu Q.-H., Eterovic A.K., Byers L.A., Davies M.A., Deng W.-L., Gopal Y.N.V., Chen G., von Euw E.M., Slamon D.J., Conklin D., Heymach J.V., Gazdar A.F., Minna J.D., Myers J.N., Lu Y.-L., Mills G.B., Liang H.
Characterization of human cancer cell lines by reverse-phase protein arrays.
Cancer Cell 31:225-239(2017)
PubMed=29435981; DOI=10.1002/ijc.31304
Kim H.J., Kang S.K., Kwon W.S., Kim T.S., Jeong I., Jeung H.-C., Kragh M., Horak I.D., Chung H.C., Rha S.Y.
Forty-nine gastric cancer cell lines with integrative genomic profiling for development of c-MET inhibitor.
Int. J. Cancer 143:151-159(2018)
PubMed=29717028; DOI=10.1042/BSR20180277; PMCID=PMC6050193
Zhang Y.-Q., Yu S.-T., Zhang Z.-Z., Zhao G., Xu J.
Long non-coding RNA AK096174 promotes cell proliferation and invasion in gastric cancer by regulating WDR66 expression.
Biosci. Rep. 38:BSR20180277.1-BSR20180277.12(2018)
PubMed=30894373; DOI=10.1158/0008-5472.CAN-18-2747; PMCID=PMC6445675
Dutil J., Chen Z.-H., Monteiro A.N.A., Teer J.K., Eschrich S.A.
An interactive resource to probe genetic diversity and estimated ancestry in cancer cell lines.
Cancer Res. 79:1263-1273(2019)
PubMed=30971826; DOI=10.1038/s41586-019-1103-9
Behan F.M., Iorio F., Picco G., Goncalves E., Beaver C.M., Migliardi G., Santos R., Rao Y., Sassi F., Pinnelli M., Ansari R., Harper S., Jackson D.A., McRae R., Pooley R., Wilkinson P., van der Meer D.J., Dow D., Buser-Doepner C.A., Bertotti A., Trusolino L., Stronach E.A., Saez-Rodriguez J., Yusa K., Garnett M.J.
Prioritization of cancer therapeutic targets using CRISPR-Cas9 screens.
Nature 568:511-516(2019)
PubMed=31068700; DOI=10.1038/s41586-019-1186-3; PMCID=PMC6697103
Ghandi M., Huang F.W., Jane-Valbuena J., Kryukov G.V., Lo C.C., McDonald E.R. 3rd, Barretina J.G., Gelfand E.T., Bielski C.M., Li H.-X., Hu K., Andreev-Drakhlin A.Y., Kim J., Hess J.M., Haas B.J., Aguet F., Weir B.A., Rothberg M.V., Paolella B.R., Lawrence M.S., Akbani R., Lu Y.-L., Tiv H.L., Gokhale P.C., de Weck A., Mansour A.A., Oh C., Shih J., Hadi K., Rosen Y., Bistline J., Venkatesan K., Reddy A., Sonkin D., Liu M., Lehar J., Korn J.M., Porter D.A., Jones M.D., Golji J., Caponigro G., Taylor J.E., Dunning C.M., Creech A.L., Warren A.C., McFarland J.M., Zamanighomi M., Kauffmann A., Stransky N., Imielinski M., Maruvka Y.E., Cherniack A.D., Tsherniak A., Vazquez F., Jaffe J.D., Lane A.A., Weinstock D.M., Johannessen C.M., Morrissey M.P., Stegmeier F., Schlegel R., Hahn W.C., Getz G., Mills G.B., Boehm J.S., Golub T.R., Garraway L.A., Sellers W.R.
Next-generation characterization of the Cancer Cell Line Encyclopedia.
Nature 569:503-508(2019)
PubMed=31978347; DOI=10.1016/j.cell.2019.12.023; PMCID=PMC7339254
Nusinow D.P., Szpyt J., Ghandi M., Rose C.M., McDonald E.R. 3rd, Kalocsay M., Jane-Valbuena J., Gelfand E.T., Schweppe D.K., Jedrychowski M.P., Golji J., Porter D.A., Rejtar T., Wang Y.K., Kryukov G.V., Stegmeier F., Erickson B.K., Garraway L.A., Sellers W.R., Gygi S.P.
Quantitative proteomics of the Cancer Cell Line Encyclopedia.
Cell 180:387-402.e16(2020)"