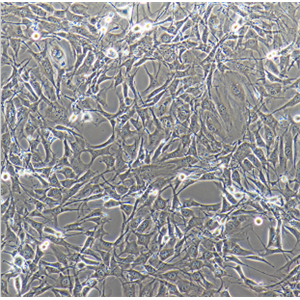
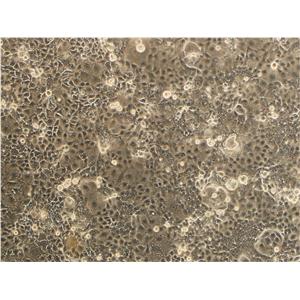
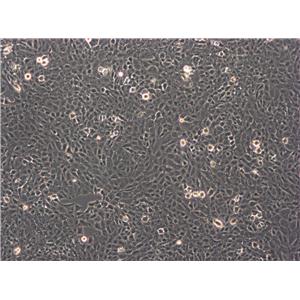
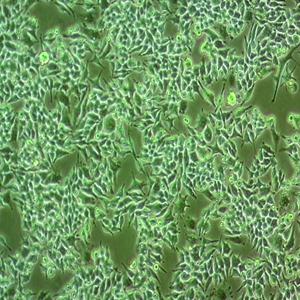
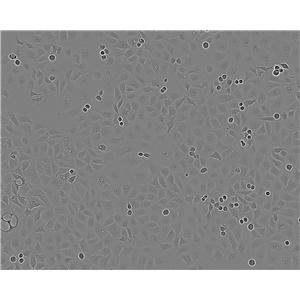
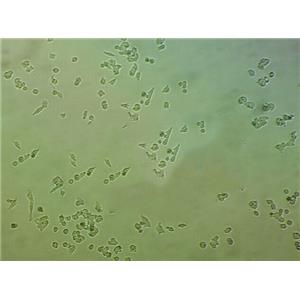
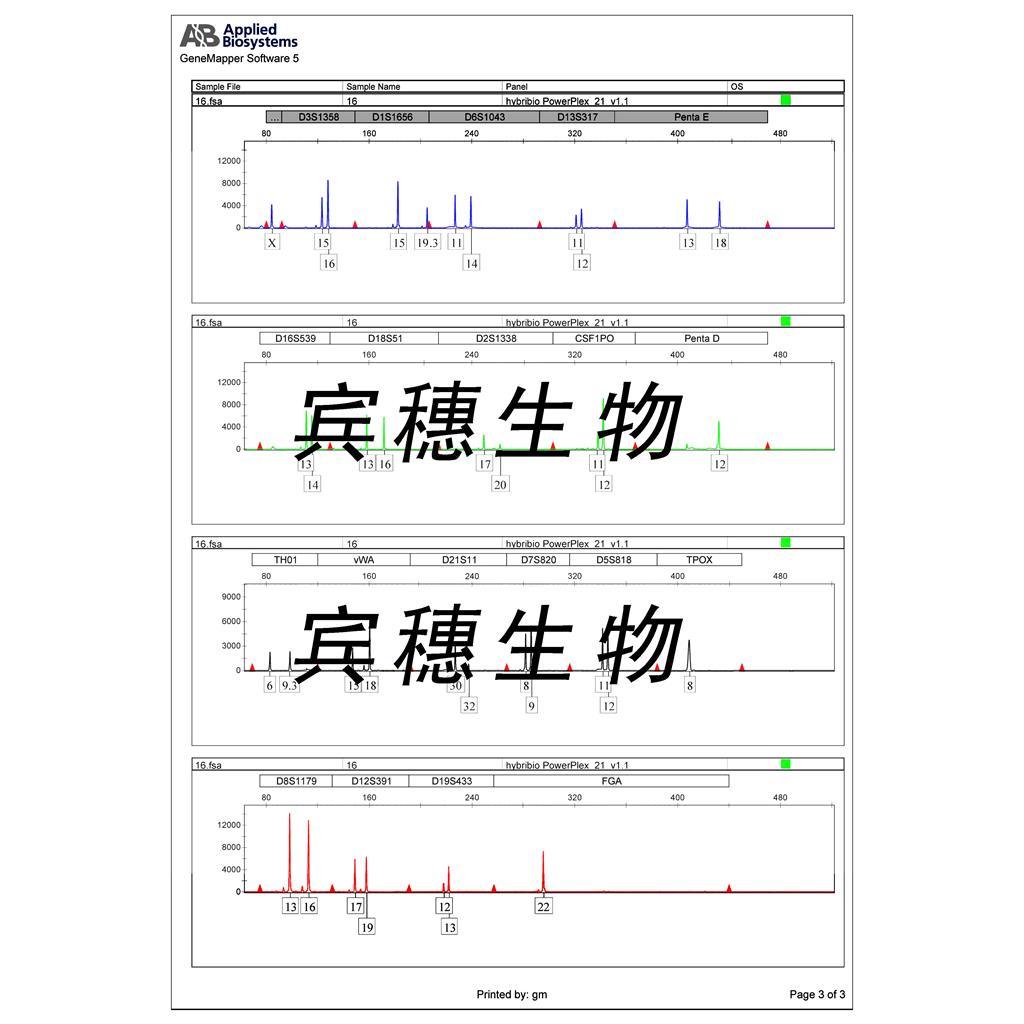
"NCI-H1395人肺腺癌细胞代次低|培养基|送STR图谱
传代比例:1:2-1:4(首次传代建议1:2)
生长特性:贴壁生长
细胞系培养所需基本设备:(1)细胞培养通风橱(即:层流通风橱或生物安全柜)(2)培养箱(推荐使用湿式二氧化碳培养箱)(3)水浴锅(4)离心机(5)冰箱和冰柜(-20℃)(6)细胞计数器(7)倒置显微镜(8)液氮罐或冻存容器(9)灭菌器(即:高压灭菌器);细胞系培养扩增所需设备:(1)抽吸泵(蠕动泵或真空泵)(2)pH计(3)共聚焦显微镜(4)流式细胞仪;细胞培养其他所需用品:(1)细胞培养容器(例如:培养瓶、培养皿、滚瓶、多孔板)(2)吸管和移液器(3)培养基、血清和试剂等。
换液周期:每周2-3次
Y1 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:CaSki细胞、28SC细胞、LS-123细胞
KM932 Cells;背景说明:B淋巴细胞;EBV转化;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:T-24细胞、Caco-2细胞、HRC-99细胞
NCI-H2171 Cells;背景说明:详见相关文献介绍;传代方法:3-4天换液1次。;生长特性:悬浮生长;形态特性:聚团悬浮;相关产品有:AN3细胞、Walker/LLC-WRC 256细胞、RCK8细胞
NCI-H1395人肺腺癌细胞代次低|培养基|送STR图谱
背景信息:详见相关文献介绍
┈订┈购(技术服务)┈热┈线:1┈3┈6┈4┈1┈9┈3┈0┈7┈9┈1【微信同号】┈Q┈Q:3┈1┈8┈0┈8┈0┈7┈3┈2┈4;
细胞根据其形态和功能可以分为多种类型,其中上皮细胞、成纤维细胞和淋巴母细胞是常见的三种类型。成纤维细胞,或称纤维母细胞,是一种存在于蜂窝组织或纤维结缔组织中的梭形细胞,能够分泌构成细胞外基质(ECM)的结构蛋白。这类细胞最初由德国病理学家鲁道夫·菲尔绍与法国解剖学家马蒂亚斯·杜瓦尔于19世纪中叶描述。成纤维细胞特异性标志物包括FAP(成纤维细胞激活蛋白)、α-SMA(α-平滑肌肌动蛋白)、骨膜蛋白、PDGFRα(血小板衍生生长因子受体α)、胶原蛋白、波形蛋白、纤连蛋白和胸腺细胞抗原1等。成纤维细胞在形态上是扁平的纺锤形细胞,缺乏基底膜,细胞核呈圆形拉长,被巨大的内质网包围。在培养中,它们表现出不同的形态学和生化特征,这取决于其起源位置、分化状态和培养条件。
产品包装:复苏发货:T25培养瓶(一瓶)或冻存发货:1ml冻存管(两支)
来源说明:细胞主要来源ATCC、ECACC、DSMZ、RIKEN等细胞库
NCI-H1395人肺腺癌细胞代次低|培养基|送STR图谱
物种来源:人源、鼠源等其它物种来源
HD-LM-2 Cells;背景说明:霍奇金淋巴瘤;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:EOC 20细胞、GM04679细胞、FU-MMT-1细胞
HCV 29 Cells;背景说明:膀胱;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:Ly19细胞、Ontario Cancer Institute-Acute Myeloid Leukemia-5细胞、OSRC2细胞
KMS26 Cells;背景说明:多发性骨髓瘤;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:Kuramochi细胞、NCI-441细胞、3T3 Swiss Albino细胞
EOMA Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:P3/NSI/1-AG4-1细胞、OB2细胞、H-548细胞
┈订┈购(技术服务)┈热┈线:1┈3┈6┈4┈1┈9┈3┈0┈7┈9┈1【微信同号】┈Q┈Q:3┈1┈8┈0┈8┈0┈7┈3┈2┈4;
形态特性:上皮细胞样
贴壁消化难题:1,先用PBS 把细胞洗两遍,使瓶内没有血清了,减少对胰酶的中和,然后用新配的0.25%的胰酶加入3ml左右,放在37度,然后可以在细胞有些消化下来时,拿着瓶口,运用手腕的力量轻轻震荡瓶内体,这样细胞很快就下来了,还不需要吹打,分散也均匀;2,成团、絮状:消化里加入eda可以减少细胞成团的现象,血清可以终止胰酶的作用,如果是进口血清的话也能终止eda的作用。用胰酶消化后胰酶可以倒掉,也可以不倒,直接加血清终止,如果消化中加入了eda的话,就要将消化倒干净,如果细胞贴壁要求不是很严格的话,一般不需要进行离心。鼻咽癌细胞的贴壁能力很强,用0.5%胰酶(含0.1%EDA)一般要消化12~15min。用PBS洗涤时要洗净残余的培养基,加入胰酶后在培养箱中消化(避免细胞室温下受损以及在此温度时胰酶活性Zui强)至细胞收缩变圆(可显微镜下观察)且有少许细胞脱落(有流下来的趋势),随后立即弃去胰酶(如果脱落的细胞很多且需要大量细胞实验,则不能弃去胰酶),加入培养基仔细吹打(不能用无血清培养基或者PBS替代,否则细胞聚集成团块或絮状)。一般我都离心一次弃去上清(去除残留的胰酶及漂浮的死细胞或细胞碎片);消化过度:马上用培养基中和,用吸管吹打细胞,收集全部的细胞到以无菌的离心管中800RPM 3分钟。弃上清,用全培重悬,换新的培养瓶继续培养,状态不HAO的细胞在培养的过程中会死亡脱落,在换的时候可以清除掉!
Michigan Cancer Foundation-10A Cells;背景说明:乳腺;上皮细胞;自发永生;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:ST486细胞、VP303细胞、3T3-J2细胞
H1975 Cells;背景说明:这株细胞于1988年七月建株。组织提供者是一位非吸烟人士。;传代方法:消化3-5分钟。1:2。3天内可长满。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:GM0637细胞、Spodoptera frugiperda clone 9细胞、Human Epidermoid carcinoma #2细胞
CNE-2 Cells;背景说明:1983年由谷淑燕、孔繁裔等建系;源自人鼻咽低分化鳞癌组织;原代细胞胰蛋白酶消化,48小时开始生长,首次传代20天。裸鼠体内移植100%成瘤。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:HCT15细胞、RMC-1细胞、MDA-330细胞
MAVER-1 Cells;背景说明:详见相关文献介绍;传代方法:1:3-1:5传代;2-3天换液1次。;生长特性:悬浮生长;形态特性:淋巴母细胞;相关产品有:AML-193细胞、NCI-H2170细胞、SNU-520细胞
NCI H157 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:Hs-606-T细胞、HPAF/CD18细胞、KGN细胞
OCI-AML-4 Cells;背景说明:急性髓系白血病;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:SK-N-DZ细胞、MC9细胞、SW 837细胞
OCI-Ly19 Cells;背景说明:弥漫大B淋巴瘤;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:T84细胞、K-1735细胞、TNC-1B12B4细胞
CHP 100 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:PANC3.27细胞、RWPE-1细胞、Hs-611-T细胞
TR-146 Cells;背景说明:食管鳞癌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:MDA-231细胞、University of Michigan-Urothelial Carcinoma-3细胞、CHO细胞
NCI H157 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:Hs-606-T细胞、HPAF/CD18细胞、KGN细胞
C3H/10T1/2 CL8 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:MT4细胞、NUGC3细胞、MCF.10A细胞
SNU387 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮样;相关产品有:3T3L1细胞、SNU739细胞、Human Intestinal Epithelial Cell-6细胞
MV-1-Lu Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:BIU-87/Adr细胞、NOZC-1细胞、T 98 G细胞
EC-GI Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:MV-3细胞、PK13细胞、293-GP细胞
NCIH2126 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代,每周2-3次。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:GM05862细胞、H1954细胞、HS-766T细胞
BJ [Human fibroblast] Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:成纤维细胞样;相关产品有:H-2591细胞、PGBE1细胞、JCA-1细胞
RERF-LCMS Cells;背景说明:详见相关文献介绍;传代方法:每周换液2次。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:NCI-H1882细胞、MAntle cell VERona-1细胞、BLO-11细胞
1A9PTX15 Cells(提供STR鉴定图谱)
Abcam HeLa MBD1 KO Cells(提供STR鉴定图谱)
AG24092 Cells(提供STR鉴定图谱)
BayGenomics ES cell line RRG134 Cells(提供STR鉴定图谱)
BayGenomics ES cell line XG862 Cells(提供STR鉴定图谱)
C0854 Cells(提供STR鉴定图谱)
CW60594 Cells(提供STR鉴定图谱)
FM3A Cells(提供STR鉴定图谱)
GM09487 Cells(提供STR鉴定图谱)
U138 Cells;背景说明:星形细胞瘤;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:EJ-1细胞、SW-1353细胞、EC-9706细胞
NCI-H1395人肺腺癌细胞代次低|培养基|送STR图谱
H-4-II-E Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:8505C细胞、SNUC2A细胞、U-373-MG细胞
SK-LU-1 Cells;背景说明:该细胞系源于一位60岁的白人女性患者的肺腺癌组织。;传代方法:1:2传代;每周换液2次。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:OCI-Ly 3细胞、LN 382细胞、211H细胞
RWPE2 Cells;背景说明:详见相关文献介绍;传代方法:1:3传代,2-3天传一代。;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:Stanford University-Diffuse Histiocytic Lymphoma-8细胞、DMS 153细胞、SCLC21H细胞
QGP-1 Cells;背景说明:胰腺癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:BALB 3T3 clone A31细胞、HSC-1细胞、JB6 Cl 30细胞
RCCJF Cells;背景说明:肾透明细胞癌;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:HSC-1细胞、UMUC1细胞、CLONE M3细胞
BayGenomics ES cell line CSA007 Cells(提供STR鉴定图谱)
H.Ep. No. 2 Cells;背景说明:最初认为这个细胞源自喉上皮癌,但随后通过同功酶分析、HeLa标记染色体和DNA指纹分析发现,起源细胞已被HeLa污染。 角蛋白免疫过氧化物酶染色阳性。;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:RBL 2H3细胞、Immortalized Human Hepatocytes细胞、OVCAR8/ADR细胞
686LN-M4e Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:HSC-2细胞、Dx5细胞、786-O RCC细胞
SF 126 Cells;背景说明:该细胞来源于星形胶质细胞瘤;胶质纤维酸性蛋白(GFAP)阴性;可以特异地结合β-内啡肽。;传代方法:1:3传代;3-4天1次。;生长特性:贴壁生长;形态特性:成纤维细胞;相关产品有:B16/BL6细胞、BSC-1细胞、SUM102细胞
CHL/IU Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:NCI-747细胞、DoTc2细胞、MOLP8细胞
RPTEC TERT1 Cells;背景说明:肾;近端小管上皮;HGNC-TERT转化;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:786O细胞、H2591细胞、CF PAC-1细胞
T-98 Cells;背景说明:胶质瘤;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SKml2细胞、MKN-28细胞、MDCK Type II细胞
CAKI 1 Cells;背景说明:该细胞超微结构中包含许多微绒毛、少许微丝、许多小线粒体、发达的高尔基休和内质网、许多脂滴和多层体、次级溶酶体,没有发现病毒颗粒。;传代方法:1:2-1:4传代;每周换液2-3次。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:OCI Ly10细胞、MILE SVEN1细胞、RC-4B/C细胞
LC2/Ad Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:RCM1细胞、McG-1细胞、Hep II细胞
GM10688 Cells(提供STR鉴定图谱)
HAP1 CDAN1 (-) Cells(提供STR鉴定图谱)
BV-173 Cells;背景说明:慢性粒细胞白血病;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:Hs 940.T细胞、Mv1.Lu细胞、H676细胞
C57/B6-L Cells;背景说明:肺;成纤维细胞;C57;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:Hs611T细胞、CCD-112CoN细胞、P3 88 D1细胞
CD18/HPAF Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:详见产品说明书;相关产品有:NB-9细胞、RL95-2细胞、Chinese Hamster Lung细胞
HuH 6 Cells;背景说明:肝癌。据说产球蛋白和甲胎蛋白。;传代方法:消化3-5分钟。1:2。6-7天长满。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:UACC812细胞、OE19细胞、NCI-SNU-601细胞
alpha-TC1-6 Cells;背景说明:胰岛素瘤;a细胞;C57BL/6xDBA/2;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:SW-527细胞、CTV-1细胞、SLK细胞
WRL-68 Cells;背景说明:胚胎;肝 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:LS411细胞、MeT-5A细胞、SUDHL-5细胞
SK LU 1 Cells;背景说明:该细胞系源于一位60岁的白人女性患者的肺腺癌组织。;传代方法:1:2传代;每周换液2次。;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:EMT6细胞、LA-N-6(OAN)细胞、NCIH1836细胞
NSC34 Cells;背景说明:神经元;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:NTera 2/cl.D1细胞、H.Ep. #2细胞、LC1-Sq细胞
HG03915 Cells(提供STR鉴定图谱)
IM-HBlSMC Cells(提供STR鉴定图谱)
Lu-134-B Cells(提供STR鉴定图谱)
ND01782 Cells(提供STR鉴定图谱)
PCG.G6 Cells(提供STR鉴定图谱)
Ubigene JIMT-1 LGALS3 KO Cells(提供STR鉴定图谱)
YAN3206 Cells(提供STR鉴定图谱)
HCT116-MFSD6-KO-c15 Cells(提供STR鉴定图谱)
KTC1 Cells;背景说明:甲状腺乳头状癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:VMM39细胞、3T3 Swiss Albino细胞、HCC-94细胞
Biologics Standards-Cercopithecus-1 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:H-810细胞、KAT-5细胞、MB39细胞
NS1 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:H-889细胞、OVCAR-5细胞、AN3细胞
Y1 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:CaSki细胞、28SC细胞、LS-123细胞
MC26 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:Hs-274-T细胞、TW 01细胞、HC-11细胞
MC26 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:Hs-274-T细胞、TW 01细胞、HC-11细胞
SW 626 Cells;背景说明:卵巢癌;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:LC-1/sq细胞、HK-2 [Human kidney]细胞、159 PT细胞
SW982 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:MD Anderson-Metastatic Breast-436细胞、HEI-193细胞、HS 1.Tes细胞
Huh 7.5 Cells;背景说明:肝癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:MiaPaCa2细胞、Lewis Lung Cancer细胞、SUM 190细胞
CHO/dhFr- Cells;背景说明:该细胞为二叶酸还原酶缺陷型;培养基中没有HT(次黄嘌呤-胸腺嘧啶)时,该细胞会死亡;培养基中加入甲喋呤可以防止对该药物具有低抵抗性的回变细胞的生长;可作转染宿主。;传代方法:消化3-5分钟。1:2。3天内可长满。;生长特性:贴壁生长;形态特性:上皮样;相关产品有:MDBK细胞、NOK细胞、HT 115细胞
MC-38 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长;形态特性:上皮细胞样;相关产品有:OE-21细胞、SUDHL8细胞、HeLa S3细胞
MBMEC Cells;背景说明:脑微血管;内皮 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:CNLMG-B5537SKIN细胞、alphaTC1 Clone 6细胞、UPCI:SCC90细胞
NS1-Ag4 Cells;背景说明:这是P3X63Ag8(ATCCTIB-9)的一个不分泌克隆。Kappa链合成了但不分泌。能抗0.1mM8-氮杂鸟嘌呤但不能在HAT培养基中生长。据报道它是由于缺失了3-酮类固醇还原酶活性的胆固醇营养缺陷型。检测表明肢骨发育畸形病毒(鼠痘)阴性。;传代方法:1:2传代,3天内可长满。;生长特性:悬浮生长;形态特性:淋巴母细胞;相关产品有:NCI-H2196细胞、OCI-Ly 3细胞、SW-626细胞
TB-1 Lu Cells;背景说明:肺;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:Jurkat细胞、b.End3细胞、D341MD细胞
U-266 Cells;背景说明:详见相关文献介绍;传代方法:1:3传代,2-3天传一代;生长特性:悬浮生长 ;形态特性:淋巴母细胞样;相关产品有:EA.hy 926细胞、NCI H508细胞、HCC-1500细胞
SCRP3601i Cells(提供STR鉴定图谱)
HSC1 Cells;背景说明:皮肤鳞癌;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:PC 61 5.3细胞、HLMVEC细胞、HT1376细胞
SU-DH-L5 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:PC 61细胞、RetroPack PT67细胞、EBTr细胞
ROS17/28 Cells;背景说明:骨肉瘤;ACI 9935;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:Immortalized Human Hepatocytes细胞、MC57G细胞、IGROV-1细胞
HuT-78 Cells;背景说明:皮肤;T淋巴瘤;男性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:悬浮;形态特性:详见产品说明书;相关产品有:LLC-PK1细胞、University of Arizona Cell Culture-812细胞、LS-513细胞
MSCs(mUCMSCs) Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:NCIH64细胞、NIH:OVCAR4细胞、MD Anderson-Metastatic Breast-231细胞
OVCA432 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:KU 19-19细胞、REC-1细胞、H-838细胞
NCI-H1395人肺腺癌细胞代次低|培养基|送STR图谱
HTori-3.1 Cells;背景说明:甲状腺;SV40转化;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:BEL-7405细胞、TEC细胞、P3HR-1细胞
NFHIOSE-29 Cells;背景说明:卵巢;上皮细胞;女性;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:NCM356细胞、NCI-H2029细胞、NCIH1341细胞
RPMC Cells;背景说明:腹膜间皮 Cells;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁;形态特性:详见产品说明书;相关产品有:RA-FLSs细胞、NeHepLxHT细胞、H2286细胞
BCP1 Cells;背景说明:详见相关文献介绍;传代方法:维持细胞浓度在2×105/ml-1×106/ml;根据细胞浓度每2-3天补液1次。;生长特性:悬浮生长 ;形态特性:淋巴母细胞样;相关产品有:M4e细胞、NU-GC-3细胞、SKNDZ细胞
SNU520 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:H2170细胞、RIN-m 14B细胞、H322T细胞
SNB19 Cells;背景说明:详见相关文献介绍;传代方法:1:2传代;生长特性:贴壁生长 ;形态特性:详见产品说明书;相关产品有:TOV21细胞、NRK细胞、HCC1143细胞
Centre Antoine Lacassagne-62 Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:3传代;每周换液2-3次。;生长特性:贴壁或悬浮,详见产品说明书部分;形态特性:详见产品说明书;相关产品有:ECC 10细胞、EC-9706细胞、LIM 1215细胞
MDA PCa 2b Cells;背景说明:详见相关文献介绍;传代方法:1:2-1:4传代,2-3天换液1次。;生长特性:贴壁生长;形态特性:上皮细胞;相关产品有:BEND细胞、Hs 822.T细胞、K422细胞
BayGenomics ES cell line RRR380 Cells(提供STR鉴定图谱)
BayGenomics ES cell line YHD375 Cells(提供STR鉴定图谱)
HVEM 18.10 Cells(提供STR鉴定图谱)
PCRP-IGF2BP1-2D4 Cells(提供STR鉴定图谱)
FIB21 Cells(提供STR鉴定图谱)
HPS3700 Cells(提供STR鉴定图谱)
" "PubMed=10987304
Girard L., Zochbauer-Muller S., Virmani A.K., Gazdar A.F., Minna J.D.
Genome-wide allelotyping of lung cancer identifies new regions of allelic loss, differences between small cell lung cancer and non-small cell lung cancer, and loci clustering.
Cancer Res. 60:4894-4906(2000)
PubMed=11030152; DOI=10.1038/sj.onc.1203815
Modi S., Kubo A., Oie H.K., Coxon A.B., Rehmatulla A., Kaye F.J.
Protein expression of the RB-related gene family and SV40 large T antigen in mesothelioma and lung cancer.
Oncogene 19:4632-4639(2000)
PubMed=11416159; DOI=10.1073/pnas.121616198; PMCID=PMC35459
Masters J.R.W., Thomson J.A., Daly-Burns B., Reid Y.A., Dirks W.G., Packer P., Toji L.H., Ohno T., Tanabe H., Arlett C.F., Kelland L.R., Harrison M., Virmani A.K., Ward T.H., Ayres K.L., Debenham P.G.
Short tandem repeat profiling provides an international reference standard for human cell lines.
Proc. Natl. Acad. Sci. U.S.A. 98:8012-8017(2001)
PubMed=12068308; DOI=10.1038/nature00766
Davies H.R., Bignell G.R., Cox C., Stephens P.J., Edkins S., Clegg S., Teague J.W., Woffendin H., Garnett M.J., Bottomley W., Davis N., Dicks E., Ewing R., Floyd Y., Gray K., Hall S., Hawes R., Hughes J., Kosmidou V., Menzies A., Mould C., Parker A., Stevens C., Watt S., Hooper S., Wilson R., Jayatilake H., Gusterson B.A., Cooper C.S., Shipley J.M., Hargrave D., Pritchard-Jones K., Maitland N.J., Chenevix-Trench G., Riggins G.J., Bigner D.D., Palmieri G., Cossu A., Flanagan A.M., Nicholson A., Ho J.W.C., Leung S.Y., Yuen S.T., Weber B.L., Seigler H.F., Darrow T.L., Paterson H.F., Marais R., Marshall C.J., Wooster R., Stratton M.R., Futreal P.A.
Mutations of the BRAF gene in human cancer.
Nature 417:949-954(2002)
PubMed=14762065; DOI=10.1101/gr.2012304; PMCID=PMC327104
Bignell G.R., Huang J., Greshock J., Watt S., Butler A.P., West S., Grigorova M., Jones K.W., Wei W., Stratton M.R., Futreal P.A., Weber B., Shapero M.H., Wooster R.
High-resolution analysis of DNA copy number using oligonucleotide microarrays.
Genome Res. 14:287-295(2004)
PubMed=16157194; DOI=10.1016/j.cancergencyto.2005.03.007
Grigorova M., Lyman R.C., Caldas C., Edwards P.A.W.
Chromosome abnormalities in 10 lung cancer cell lines of the NCI-H series analyzed with spectral karyotyping.
Cancer Genet. Cytogenet. 162:1-9(2005)
PubMed=16187286; DOI=10.1002/ijc.21491
Garnis C., Lockwood W.W., Vucic E., Ge Y., Girard L., Minna J.D., Gazdar A.F., Lam S., MacAulay C., Lam W.L.
High resolution analysis of non-small cell lung cancer cell lines by whole genome tiling path array CGH.
Int. J. Cancer 118:1556-1564(2006)
PubMed=19472407; DOI=10.1002/humu.21028; PMCID=PMC2900846
Blanco R., Iwakawa R., Tang M.-Y., Kohno T., Angulo B., Pio R., Montuenga L.M., Minna J.D., Yokota J., Sanchez-Cespedes M.
A gene-alteration profile of human lung cancer cell lines.
Hum. Mutat. 30:1199-1206(2009)
PubMed=20164919; DOI=10.1038/nature08768; PMCID=PMC3145113
Bignell G.R., Greenman C.D., Davies H.R., Butler A.P., Edkins S., Andrews J.M., Buck G., Chen L., Beare D., Latimer C., Widaa S., Hinton J., Fahey C., Fu B.-Y., Swamy S., Dalgliesh G.L., Teh B.T., Deloukas P., Yang F.-T., Campbell P.J., Futreal P.A., Stratton M.R.
Signatures of mutation and selection in the cancer genome.
Nature 463:893-898(2010)
PubMed=20215515; DOI=10.1158/0008-5472.CAN-09-3458; PMCID=PMC2881662
Rothenberg S.M., Mohapatra G., Rivera M.N., Winokur D., Greninger P., Nitta M., Sadow P.M., Sooriyakumar G., Brannigan B.W., Ulman M.J., Perera R.M., Wang R., Tam A., Ma X.-J., Erlander M., Sgroi D.C., Rocco J.W., Lingen M.W., Cohen E.E.W., Louis D.N., Settleman J., Haber D.A.
A genome-wide screen for microdeletions reveals disruption of polarity complex genes in diverse human cancers.
Cancer Res. 70:2158-2164(2010)
PubMed=20557307; DOI=10.1111/j.1349-7006.2010.01622.x; PMCID=PMC11158680
Iwakawa R., Kohno T., Enari M., Kiyono T., Yokota J.
Prevalence of human papillomavirus 16/18/33 infection and p53 mutation in lung adenocarcinoma.
Cancer Sci. 101:1891-1896(2010)
DOI=10.4172/2157-7145.S2-005
Fang R.-X., Shewale J.G., Nguyen V.T., Cardoso H., Swerdel M.R., Hart R.P., Furtado M.R.
STR profiling of human cell lines: challenges and possible solutions to the growing problem.
J. Forensic Res. 2 Suppl. 2:5-5(2011)
PubMed=22460905; DOI=10.1038/nature11003; PMCID=PMC3320027
Barretina J.G., Caponigro G., Stransky N., Venkatesan K., Margolin A.A., Kim S., Wilson C.J., Lehar J., Kryukov G.V., Sonkin D., Reddy A., Liu M., Murray L., Berger M.F., Monahan J.E., Morais P., Meltzer J., Korejwa A., Jane-Valbuena J., Mapa F.A., Thibault J., Bric-Furlong E., Raman P., Shipway A., Engels I.H., Cheng J., Yu G.-Y.K., Yu J.-J., Aspesi P. Jr., de Silva M., Jagtap K., Jones M.D., Wang L., Hatton C., Palescandolo E., Gupta S., Mahan S., Sougnez C., Onofrio R.C., Liefeld T., MacConaill L.E., Winckler W., Reich M., Li N.-X., Mesirov J.P., Gabriel S.B., Getz G., Ardlie K., Chan V., Myer V.E., Weber B.L., Porter J., Warmuth M., Finan P., Harris J.L., Meyerson M.L., Golub T.R., Morrissey M.P., Sellers W.R., Schlegel R., Garraway L.A.
The Cancer Cell Line Encyclopedia enables predictive modelling of anticancer drug sensitivity.
Nature 483:603-607(2012)
PubMed=25485619; DOI=10.1038/nbt.3080
Klijn C., Durinck S., Stawiski E.W., Haverty P.M., Jiang Z.-S., Liu H.-B., Degenhardt J., Mayba O., Gnad F., Liu J.-F., Pau G., Reeder J., Cao Y., Mukhyala K., Selvaraj S.K., Yu M.-M., Zynda G.J., Brauer M.J., Wu T.D., Gentleman R.C., Manning G., Yauch R.L., Bourgon R., Stokoe D., Modrusan Z., Neve R.M., de Sauvage F.J., Settleman J., Seshagiri S., Zhang Z.-M.
A comprehensive transcriptional portrait of human cancer cell lines.
Nat. Biotechnol. 33:306-312(2015)
PubMed=25877200; DOI=10.1038/nature14397
Yu M., Selvaraj S.K., Liang-Chu M.M.Y., Aghajani S., Busse M., Yuan J., Lee G., Peale F.V., Klijn C., Bourgon R., Kaminker J.S., Neve R.M.
A resource for cell line authentication, annotation and quality control.
Nature 520:307-311(2015)
PubMed=26589293; DOI=10.1186/s13073-015-0240-5; PMCID=PMC4653878
Scholtalbers J., Boegel S., Bukur T., Byl M., Goerges S., Sorn P., Loewer M., Sahin U., Castle J.C.
TCLP: an online cancer cell line catalogue integrating HLA type, predicted neo-epitopes, virus and gene expression.
Genome Med. 7:118.1-118.7(2015)
PubMed=27602502; DOI=10.18632/oncotarget.11845; PMCID=PMC5308618
Weber A.M., Drobnitzky N., Devery A.M., Bokobza S.M., Adams R.A., Maughan T.S., Ryan A.J.
Phenotypic consequences of somatic mutations in the ataxia-telangiectasia mutated gene in non-small cell lung cancer.
Oncotarget 7:60807-60822(2016)
PubMed=27397505; DOI=10.1016/j.cell.2016.06.017; PMCID=PMC4967469
Iorio F., Knijnenburg T.A., Vis D.J., Bignell G.R., Menden M.P., Schubert M., Aben N., Goncalves E., Barthorpe S., Lightfoot H., Cokelaer T., Greninger P., van Dyk E., Chang H., de Silva H., Heyn H., Deng X.-M., Egan R.K., Liu Q.-S., Miroo T., Mitropoulos X., Richardson L., Wang J.-H., Zhang T.-H., Moran S., Sayols S., Soleimani M., Tamborero D., Lopez-Bigas N., Ross-Macdonald P., Esteller M., Gray N.S., Haber D.A., Stratton M.R., Benes C.H., Wessels L.F.A., Saez-Rodriguez J., McDermott U., Garnett M.J.
A landscape of pharmacogenomic interactions in cancer.
Cell 166:740-754(2016)
PubMed=28196595; DOI=10.1016/j.ccell.2017.01.005; PMCID=PMC5501076
Li J., Zhao W., Akbani R., Liu W.-B., Ju Z.-L., Ling S.-Y., Vellano C.P., Roebuck P., Yu Q.-H., Eterovic A.K., Byers L.A., Davies M.A., Deng W.-L., Gopal Y.N.V., Chen G., von Euw E.M., Slamon D.J., Conklin D., Heymach J.V., Gazdar A.F., Minna J.D., Myers J.N., Lu Y.-L., Mills G.B., Liang H.
Characterization of human cancer cell lines by reverse-phase protein arrays.
Cancer Cell 31:225-239(2017)
PubMed=29681454; DOI=10.1016/j.cell.2018.03.028; PMCID=PMC5935540
McMillan E.A., Ryu M.-J., Diep C.H., Mendiratta S., Clemenceau J.R., Vaden R.M., Kim J.-H., Motoyaji T., Covington K.R., Peyton M., Huffman K., Wu X.-F., Girard L., Sung Y., Chen P.-H., Mallipeddi P.L., Lee J.Y., Hanson J., Voruganti S., Yu Y., Park S., Sudderth J., DeSevo C., Muzny D.M., Doddapaneni H., Gazdar A.F., Gibbs R.A., Hwang T.H., Heymach J.V., Wistuba I.I., Coombes K.R., Williams N.S., Wheeler D.A., MacMillan J.B., DeBerardinis R.J., Roth M.G., Posner B.A., Minna J.D., Kim H.S., White M.A.
Chemistry-first approach for nomination of personalized treatment in lung cancer.
Cell 173:864-878.e29(2018)
PubMed=30894373; DOI=10.1158/0008-5472.CAN-18-2747; PMCID=PMC6445675
Dutil J., Chen Z.-H., Monteiro A.N.A., Teer J.K., Eschrich S.A.
An interactive resource to probe genetic diversity and estimated ancestry in cancer cell lines.
Cancer Res. 79:1263-1273(2019)"